NGS-mRNA (referenčná)
Transkriptóm je spojenie medzi genómovou genetickou informáciou a proteómom biologickej funkcie.Regulácia na úrovni transkripcie je najdôležitejším a najviac študovaným spôsobom regulácie organizmov.Sekvenovanie transkriptómu môže sekvenovať transkriptóm v akomkoľvek bode v čase alebo za akýchkoľvek podmienok s rozlíšením presným na jeden nukleotid. Dokáže dynamicky odrážať úroveň transkripcie génu, súčasne identifikovať a kvantifikovať zriedkavé a normálne transkripty a poskytnúť štrukturálne informácie ukážte špecifické prepisy.
V súčasnosti je technológia transkriptómového sekvenovania široko používaná v agronómii, medicíne a iných oblastiach výskumu vrátane regulácie vývoja zvierat a rastlín, adaptácie prostredia, imunitnej interakcie, lokalizácie génov, genetickej evolúcie druhov a detekcie nádorov a genetických chorôb.
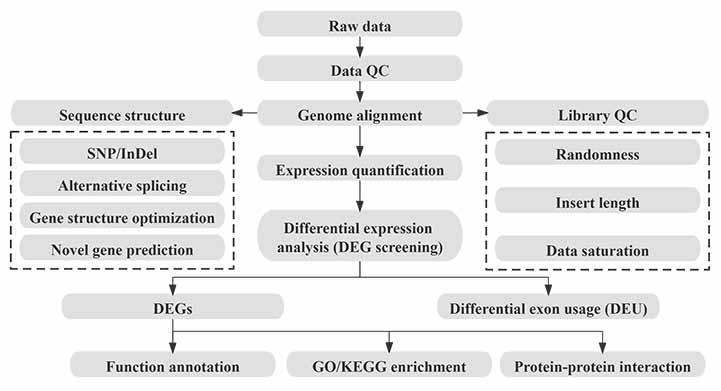
Bioinformatika
Pracovný tok bioinformatiky