NGS-mRNA (odniesienie)
Transkryptom jest łącznikiem między genomową informacją genetyczną a proteomem funkcji biologicznej.Regulacja poziomu transkrypcji jest najważniejszym i najszerzej badanym sposobem regulacji organizmów.Sekwencjonowanie transkryptomu umożliwia sekwencjonowanie transkryptomu w dowolnym momencie i w dowolnych warunkach, z rozdzielczością z dokładnością do pojedynczego nukleotydu. Może dynamicznie odzwierciedlać poziom transkrypcji genu, jednocześnie identyfikować i określać ilościowo rzadkie i normalne transkrypty oraz dostarczać informacji strukturalnych próbki konkretnych transkryptów.
Obecnie technologia sekwencjonowania transkryptomu jest szeroko stosowana w agronomii, medycynie i innych dziedzinach badań, w tym w regulacji rozwoju zwierząt i roślin, adaptacji środowiskowej, interakcjach immunologicznych, lokalizacji genów, ewolucji genetycznej gatunków oraz wykrywaniu nowotworów i chorób genetycznych.
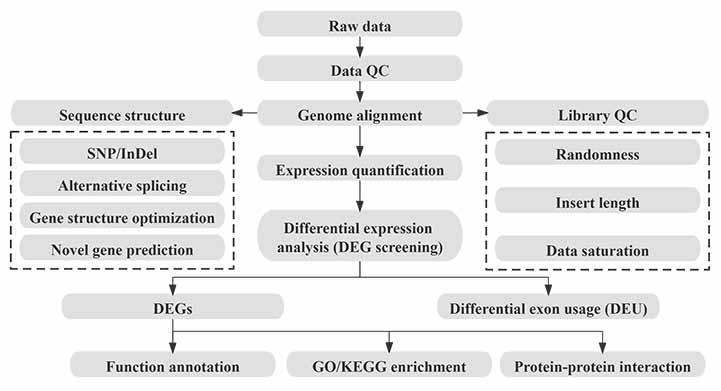
Bioinformatyka
Przepływ pracy w bioinformatyce