NGS-ARNm (referencia)
O transcriptoma é o vínculo entre a información xenética xenómica e o proteoma da función biolóxica.A regulación do nivel transcripcional é o modo de regulación dos organismos máis importante e máis estudado.A secuenciación do transcriptoma pode secuenciar o transcriptoma en calquera momento ou en calquera condición, cunha resolución precisa para un só nucleótido. Pode reflectir dinámicamente o nivel de transcrición xenética, identificar e cuantificar simultaneamente transcricións raras e normais e proporcionar a información estrutural de transcricións específicas de mostra.
Na actualidade, a tecnoloxía de secuenciación do transcriptoma utilizouse amplamente en agronomía, medicina e outros campos de investigación, incluíndo a regulación do desenvolvemento animal e vexetal, a adaptación ambiental, a interacción inmune, a localización de xenes, a evolución xenética de especies e a detección de enfermidades xenéticas e de tumores.
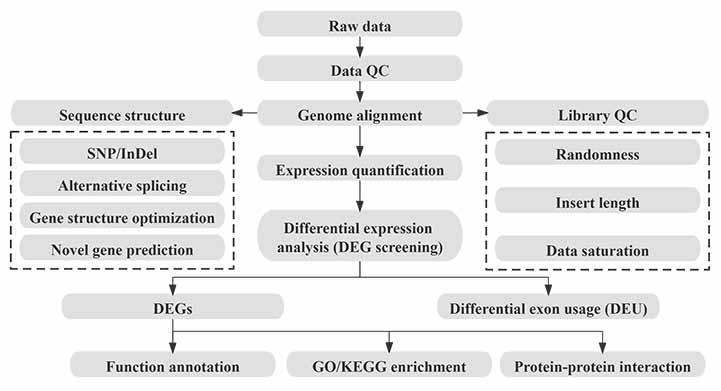
Bioinformática
Fluxo de traballo en bioinformática