NGS-mRNA (erreferentzia)
Transkriptoma informazio genomikoaren eta funtzio biologikoaren proteomaren arteko lotura da.Transkripzio-mailako erregulazioa organismoen erregulazio-modu garrantzitsuena eta aztertuena da.Transkriptomaren sekuentziazioak transkriptomia edozein momentutan edo edozein baldintzatan sekuentzia dezake, nukleotido bakarrerako bereizmen zehatzarekin. Geneen transkripzio maila dinamikoki islatu dezake, aldi berean transkripzio arraroak eta normalak identifikatu eta kuantifikatu eta egitura-informazioa eman dezake. transkripzio espezifikoak laginak.
Gaur egun, transkriptomaren sekuentziazio-teknologia oso erabilia izan da agronomian, medikuntzan eta beste ikerketa-eremu batzuetan, besteak beste, animalien eta landareen garapenaren erregulazioa, ingurumen-egokitzapena, interakzio immunologikoa, geneen lokalizazioa, espezieen bilakaera genetikoa eta tumoreak eta gaixotasun genetikoak detektatzeko.
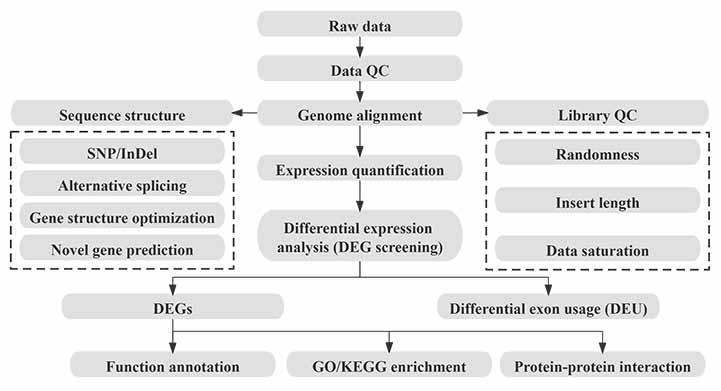
Bioinformatika
Bioinformatika Lan Fluxua