NGS-mRNA (მინიშნება)
ტრანსკრიპტომი არის კავშირი გენომიურ გენეტიკურ ინფორმაციასა და ბიოლოგიური ფუნქციის პროტეომს შორის.ტრანსკრიპციული დონის რეგულირება არის ორგანიზმების ყველაზე მნიშვნელოვანი და ყველაზე ფართოდ შესწავლილი რეგულირების რეჟიმი.ტრანსკრიპტომის თანმიმდევრობას შეუძლია ტრანსკრიპტომის თანმიმდევრობა დროის ნებისმიერ მომენტში ან ნებისმიერ პირობებში, რეზოლუციით ზუსტი ერთი ნუკლეოტიდის მიმართ. მას შეუძლია დინამიურად ასახოს გენის ტრანსკრიპციის დონე, ერთდროულად გამოავლინოს და რაოდენობრივად განსაზღვროს იშვიათი და ნორმალური ტრანსკრიპტები და მიაწოდოს სტრუქტურული ინფორმაცია. კონკრეტული ტრანსკრიპტების ნიმუში.
ამჟამად, ტრანსკრიპტომის თანმიმდევრობის ტექნოლოგია ფართოდ გამოიყენება აგრონომიაში, მედიცინაში და სხვა კვლევით სფეროებში, მათ შორის ცხოველებისა და მცენარეების განვითარების რეგულირებაში, გარემოსდაცვითი ადაპტაციის, იმუნური ურთიერთქმედების, გენების ლოკალიზაციის, სახეობების გენეტიკური ევოლუციისა და სიმსივნისა და გენეტიკური დაავადებების გამოვლენაში.
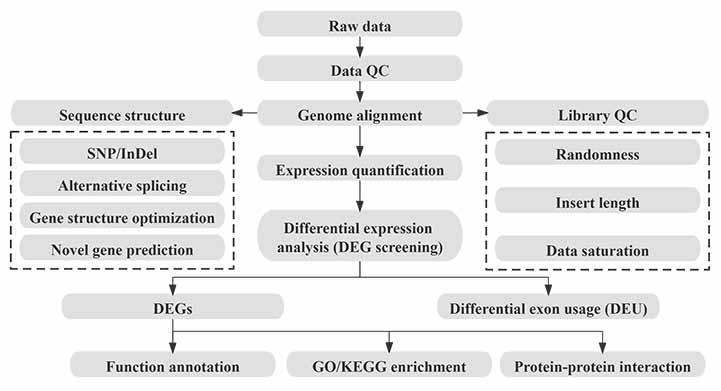
ბიოინფორმატიკა
ბიოინფორმატიკის სამუშაო ნაკადი