NGS-мРНК (спасылка)
Транскрыптом - гэта сувязь паміж геномнай генетычнай інфармацыяй і пратэомам біялагічнай функцыі.Рэгуляцыя ўзроўню транскрыпцыі - найбольш важны і найбольш шырока вывучаны спосаб рэгуляцыі арганізмаў.Секвеніраванне транскрыптому можа секвенаваць транскрыптом у любы момант часу і пры любых умовах з дакладнасцю да аднаго нуклеатыду. Ён можа дынамічна адлюстроўваць узровень транскрыпцыі гена, адначасова ідэнтыфікаваць і колькасна ацэньваць рэдкія і нармальныя транскрыпты і прадастаўляць структурную інфармацыю ўзоры канкрэтных стэнаграм.
У цяперашні час тэхналогія секвеніравання транскрыптомаў шырока выкарыстоўваецца ў аграноміі, медыцыне і іншых галінах даследаванняў, уключаючы рэгуляванне развіцця жывёл і раслін, адаптацыю да навакольнага асяроддзя, імуннае ўзаемадзеянне, лакалізацыю генаў, генетычную эвалюцыю відаў і выяўленне пухлін і генетычных захворванняў.
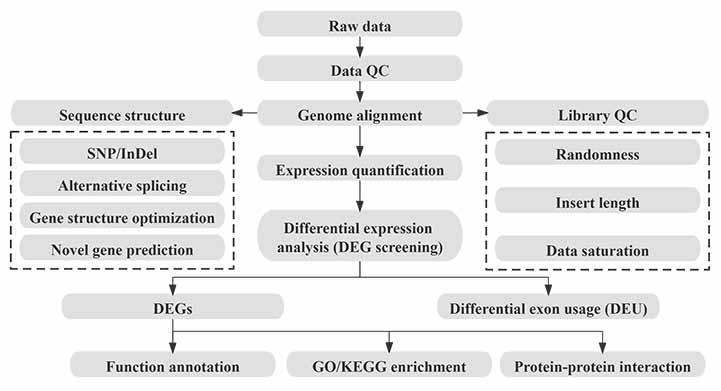
Біяінфарматыка
Праца па біяінфарматыцы