NGS-mRNR (nuoroda)
Transkriptas yra ryšys tarp genominės genetinės informacijos ir biologinės funkcijos proteomos.Transkripcijos lygio reguliavimas yra svarbiausias ir plačiausiai ištirtas organizmų reguliavimo būdas.Transkripto sekos nustatymas gali nustatyti transkripto seką bet kuriuo momentu arba bet kokiomis sąlygomis su vieno nukleotido skiriamąja geba. Jis gali dinamiškai atspindėti genų transkripcijos lygį, tuo pačiu metu nustatyti ir kiekybiškai įvertinti retus ir normalius nuorašus bei pateikti struktūrinę informaciją apie transkriptą. konkrečių nuorašų pavyzdžiai.
Šiuo metu transkripto sekos nustatymo technologija plačiai naudojama agronomijoje, medicinoje ir kitose tyrimų srityse, įskaitant gyvūnų ir augalų vystymosi reguliavimą, prisitaikymą prie aplinkos, imuninę sąveiką, genų lokalizaciją, rūšių genetinę evoliuciją ir navikų bei genetinių ligų aptikimą.
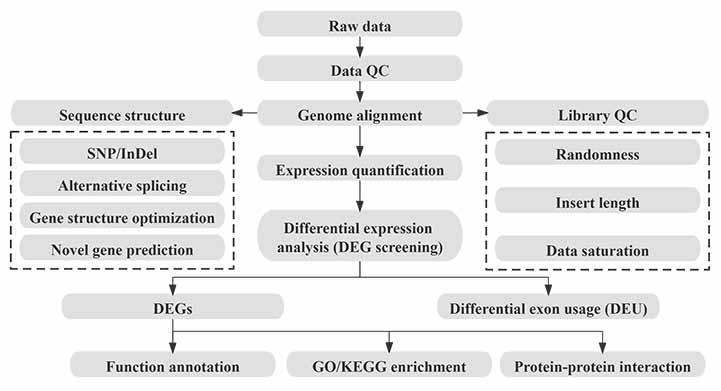
Bioinformatika
Bioinformatikos darbo eiga