NGS-mRNA (Referenz)
Das Transkriptom ist die Verbindung zwischen genomischer genetischer Information und dem Proteom der biologischen Funktion.Die Regulation auf Transkriptionsebene ist die wichtigste und am besten untersuchte Regulationsart von Organismen.Die Transkriptomsequenzierung kann das Transkriptom zu jedem Zeitpunkt und unter jeder Bedingung mit einer auf ein einzelnes Nukleotid genauen Auflösung sequenzieren. Sie kann den Grad der Gentranskription dynamisch widerspiegeln, gleichzeitig seltene und normale Transkripte identifizieren und quantifizieren und die Strukturinformationen davon bereitstellen Beispielspezifische Transkripte.
Gegenwärtig wird die Transkriptom-Sequenzierungstechnologie in großem Umfang in der Agronomie, der Medizin und anderen Forschungsbereichen eingesetzt, einschließlich der Regulierung der Tier- und Pflanzenentwicklung, der Anpassung an die Umwelt, der Immuninteraktion, der Genlokalisierung, der genetischen Evolution von Arten sowie der Erkennung von Tumoren und genetischen Krankheiten.
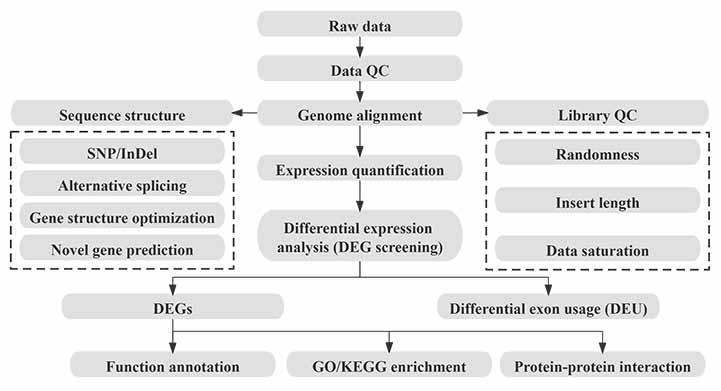
Bioinformatik
Arbeitsablauf in der Bioinformatik