NGS-мРНК (ссылка)
Транскриптом — это связь между геномной генетической информацией и протеомом биологической функции.Регуляция уровня транскрипции является наиболее важным и наиболее широко изученным способом регуляции организмов.Секвенирование транскриптома позволяет секвенировать транскриптом в любой момент времени и при любых условиях с точностью до одного нуклеотида. Оно может динамически отражать уровень транскрипции генов, одновременно идентифицировать и количественно определять редкие и нормальные транскрипты, а также предоставлять структурную информацию о образцы конкретных транскриптов.
В настоящее время технология секвенирования транскриптома широко используется в агрономии, медицине и других областях исследований, включая регулирование развития животных и растений, адаптацию к окружающей среде, иммунное взаимодействие, локализацию генов, генетическую эволюцию видов, а также обнаружение опухолей и генетических заболеваний.
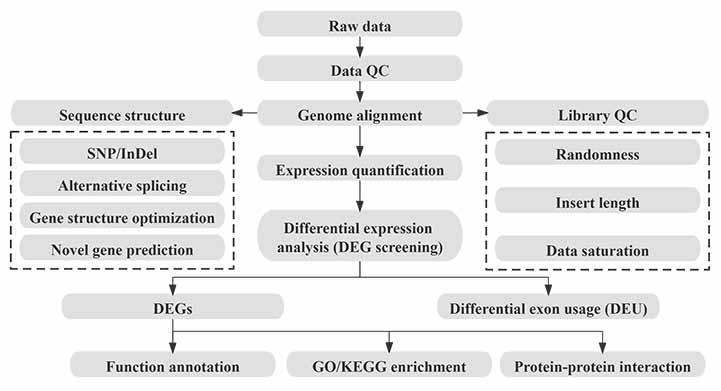
Биоинформатика
Рабочий процесс биоинформатики