NGS-mRNA (verwysing)
Transkriptoom is die skakel tussen genomiese genetiese inligting en die proteoom van biologiese funksie.Transkripsievlakregulering is die belangrikste en die mees bestudeerde reguleringsmodus van organismes.Transkripsievolgordebepaling kan die transkripsie op enige tydstip of onder enige toestand volgorde, met 'n resolusie akkuraat tot 'n enkele nukleotied. Dit kan die vlak van geentranskripsie dinamies weerspieël, seldsame en normale transkripsies gelyktydig identifiseer en kwantifiseer, en die strukturele inligting van monster spesifieke transkripsies.
Tans word transkripsievolgordebepalingstegnologie wyd gebruik in agronomie, medisyne en ander navorsingsvelde, insluitend diere- en plantontwikkelingsregulering, omgewingsaanpassing, immuuninteraksie, geenlokalisering, spesie-genetiese evolusie en opsporing van tumor- en genetiese siektes.
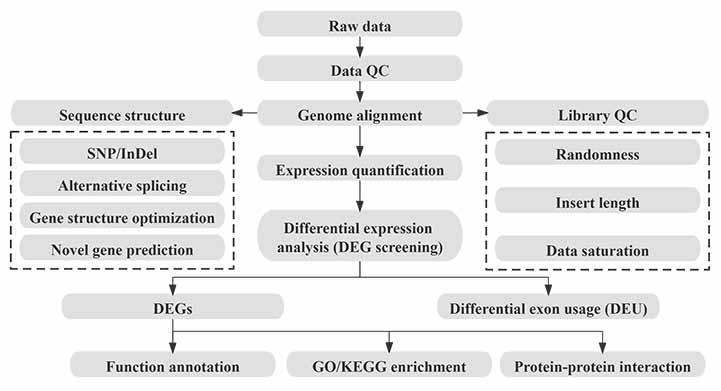
Bioinformatika
Bioinformatika-werkvloei