NGS-mRNA (مرجع)
ترانسکریپتوم ارتباط بین اطلاعات ژنتیکی ژنومی و پروتئوم عملکرد بیولوژیکی است.تنظیم سطح رونویسی مهمترین و گسترده ترین روش تنظیم موجودات است.توالی یابی ترانسکریپتوم می تواند رونوشت را در هر نقطه از زمان یا تحت هر شرایطی با وضوح دقیق به یک نوکلئوتید توالی یابی کند. می تواند به صورت پویا سطح رونویسی ژن را منعکس کند، همزمان رونوشت های نادر و عادی را شناسایی و کمیت کند و اطلاعات ساختاری را ارائه دهد. نمونه رونوشت های خاص
در حال حاضر، فناوری توالی یابی رونوشت به طور گسترده ای در زراعت، پزشکی و سایر زمینه های تحقیقاتی، از جمله تنظیم توسعه حیوانات و گیاهان، سازگاری با محیط، تعامل ایمنی، محلی سازی ژن، تکامل ژنتیکی گونه ها و تشخیص بیماری های تومور و ژنتیکی استفاده شده است.
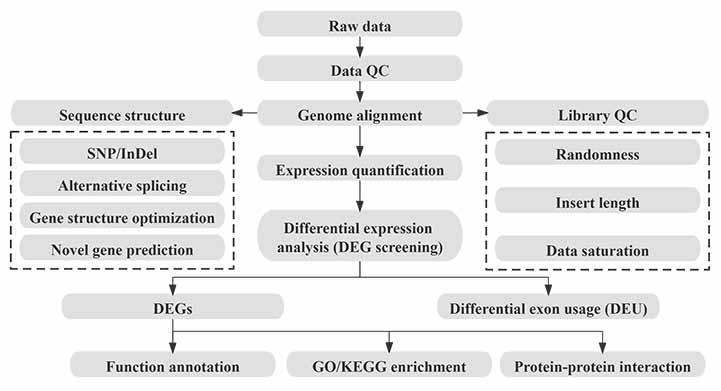
بیوانفورماتیک
جریان کار بیوانفورماتیک