NGS-mRNA (referentie)
Transcriptoom is de link tussen genomische genetische informatie en het proteoom van de biologische functie.Regulatie op transcriptieniveau is de belangrijkste en meest bestudeerde regulatiemodus van organismen.Transcriptoomsequencing kan het transcriptoom op elk moment en onder elke omstandigheid sequencen, met een resolutie die nauwkeurig is tot op een enkel nucleotide. Het kan op dynamische wijze het niveau van gentranscriptie weerspiegelen, tegelijkertijd zeldzame en normale transcripten identificeren en kwantificeren, en de structurele informatie verschaffen van voorbeeld van specifieke transcripties.
Momenteel wordt transcriptoomsequencingtechnologie op grote schaal gebruikt in de agronomie, de geneeskunde en andere onderzoeksgebieden, waaronder de regulering van de ontwikkeling van dieren en planten, aanpassing aan het milieu, immuuninteractie, genlokalisatie, genetische evolutie van soorten en detectie van tumoren en genetische ziekten.
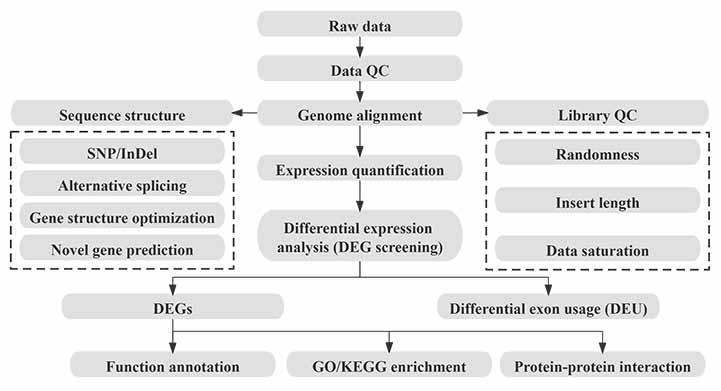
Bio-informatica
Bio-informatica werkstroom