NGS-mRNA (Referinsje)
Transkriptoom is de ferbining tusken genomyske genetyske ynformaasje en it proteoom fan biologyske funksje.Regulearring fan transkripsjenivo is de wichtichste en de meast studearre regeljouwingsmodus fan organismen.Transkriptoom-sekwinsje kin it transkriptoom op elk punt yn 'e tiid of ûnder elke betingst folje, mei in resolúsje krekt foar ien nukleotide. sample spesifike transkripsjes.
Op it stuit is technology foar transkriptoomsekwinsjes in protte brûkt yn agronomy, medisinen en oare ûndersyksfjilden, ynklusyf regeljouwing foar dier- en plantûntwikkeling, miljeu-oanpassing, ymmuninteraksje, genlokalisaasje, genetyske evolúsje fan soarten en deteksje fan tumors en genetyske sykten.
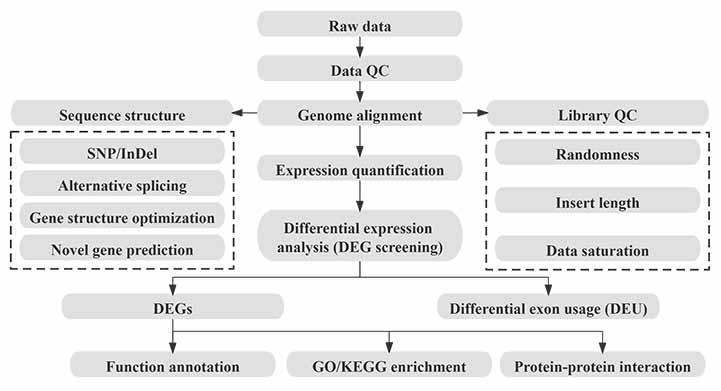
Bioinformatika
Bioinformatics Work Flow