10x Genomics Visium Spatial Transcriptome
Egenskaper
● Oppløsning: 100 µM
● Spotdiameter: 55 µM
● Antall plasser: 4992
● Fangstområde: 6,5 x 6,5 mm
● Hver strekkodede spot er lastet med primere som består av 4 seksjoner:
- poly(dT)-hale for mRNA-priming og cDNA-syntese
- Unik Molecular Identifier (UMI) for å korrigere amplifikasjonsskjevhet
- Romlig strekkode
- Bindingssekvens av delvis lest 1 sekvenseringsprimer
● H&E-farging av seksjoner
Fordeler
●One-stop service: integrerer alle erfarings- og ferdighetsbaserte trinn, inkludert kryo-seksjonering, farging, vevsoptimalisering, romlig strekkoding, bibliotekforberedelse, sekvensering og bioinformatikk.
● Høyt dyktig teknisk team: med erfaring i over 250 vevstyper og 100+ arter inkludert mennesker, mus, pattedyr, fisk og planter.
●Sanntidsoppdatering på hele prosjektet: med full kontroll over eksperimentell fremgang.
●Omfattende standard bioinformatikk:Pakken inkluderer 29 analyser og 100+ høykvalitetsfigurer.
●Tilpasset dataanalyse og visualisering: tilgjengelig for ulike forskningsforespørsler.
●Valgfri fellesanalyse med enkeltcellet mRNA-sekvensering
Spesifikasjoner
| Eksempelkrav | Bibliotek | Sekvenseringsstrategi | Data anbefales | Kvalitetskontroll |
| OCT-innebygde kryoprøver, FFPE-prøver (Optimal diameter: ca. 6x6x6 mm3) 3 blokker per prøve | 10X Visium cDNA-bibliotek | Illumina PE150 | 50K PE-avlesninger per spot (60 Gb) | RIN>7 |
For mer informasjon om veiledning for prøveforberedelse og servicearbeidsflyt, kan du gjerne snakke med aBMKGENE-ekspert
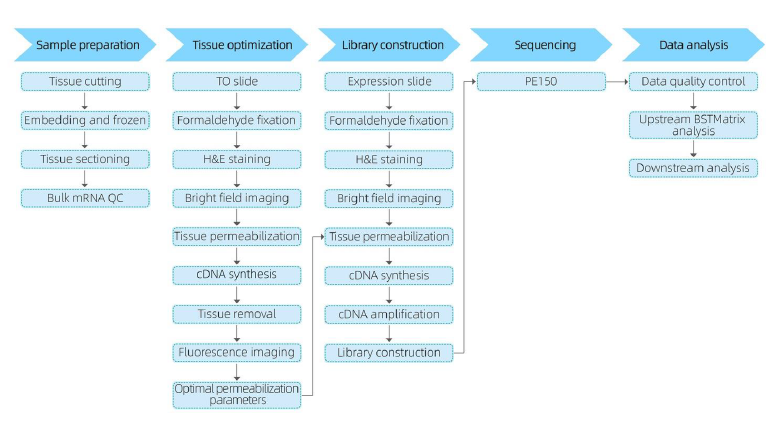
Tjenestearbeidsflyt
I prøveforberedelsesfasen utføres en innledende bulk-RNA-ekstraksjonsforsøk for å sikre at et RNA av høy kvalitet kan oppnås.I vevsoptimaliseringsstadiet farges og visualiseres seksjonene, og permeabiliseringsbetingelsene for mRNA-frigjøring fra vev er optimalisert.Den optimaliserte protokollen brukes deretter under bibliotekkonstruksjon, etterfulgt av sekvensering og dataanalyse.
Den komplette tjenestearbeidsflyten involverer sanntidsoppdateringer og klientbekreftelser for å opprettholde en responsiv tilbakemeldingssløyfe, som sikrer jevn prosjektgjennomføring.
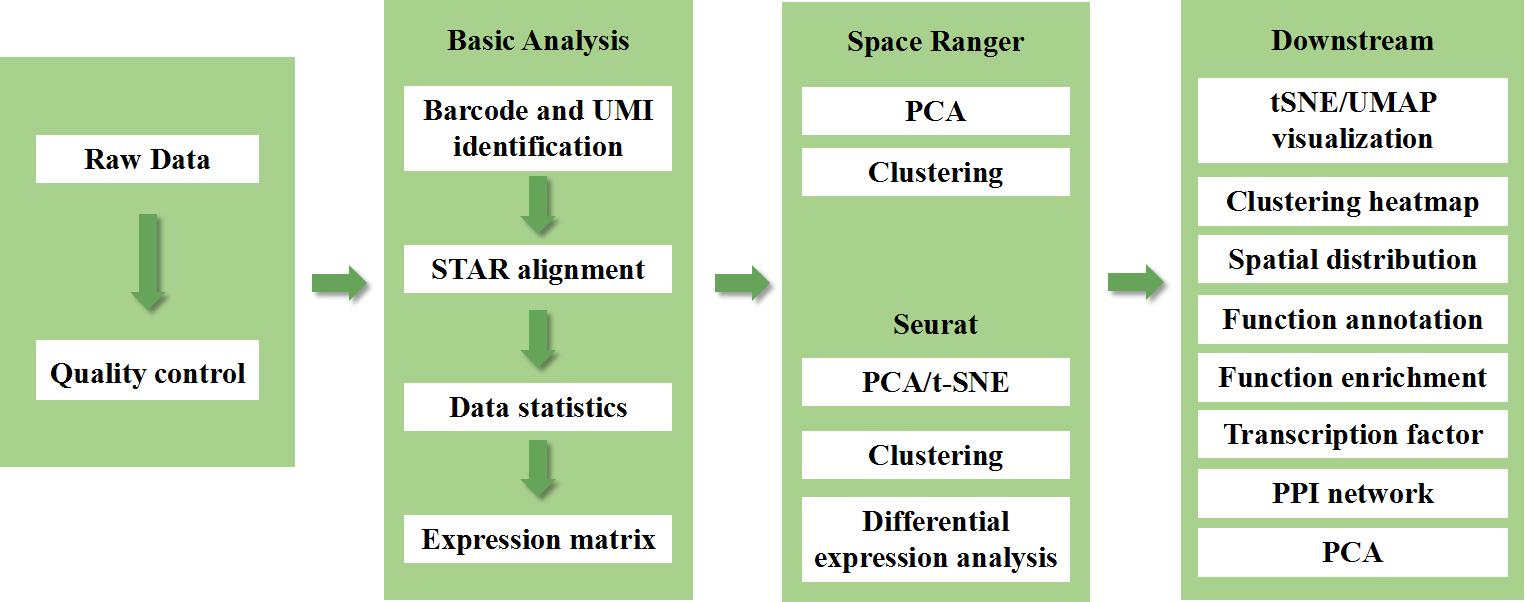
Inkluderer følgende analyse:
Datakvalitetskontroll:
o Datautgang og distribusjon av kvalitetspoeng
o Gendeteksjon per punkt
o Vevsdekning
Analyse av indre prøve:
o Genrikdom
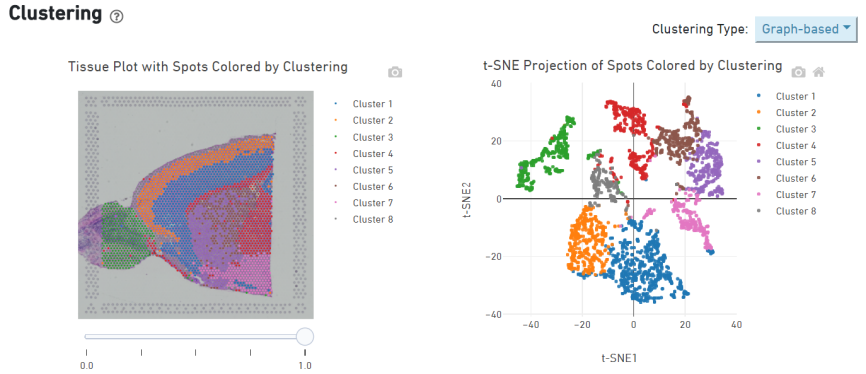
o Spot clustering, inkludert redusert dimensjonsanalyse
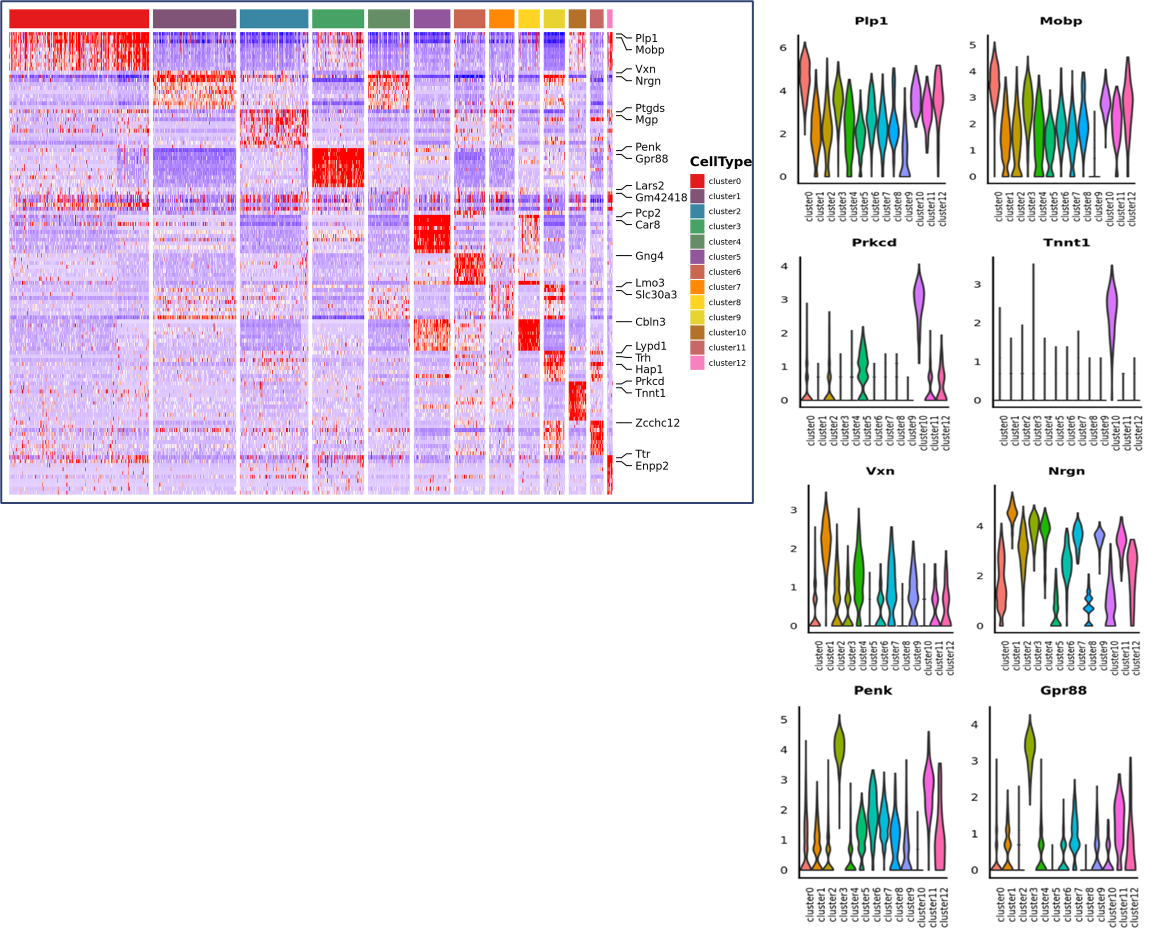
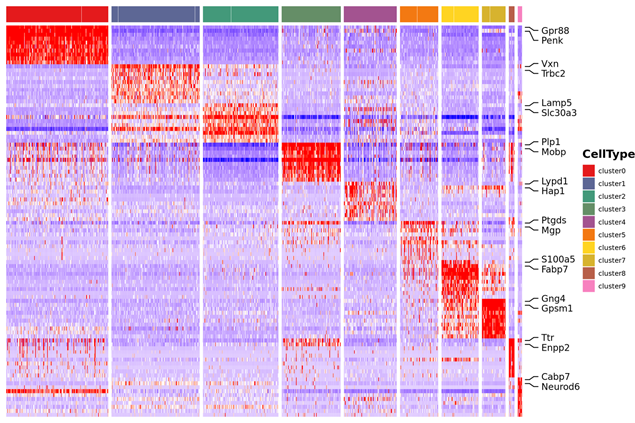
o Differensiell ekspresjonsanalyse mellom klynger: identifikasjon av markørgener
o Funksjonell annotering og berikelse av markørgener
Intergruppeanalyse
o Re-kombinasjon av flekker fra både prøver (f.eks. syk og kontroll) og re-cluster
o Identifikasjon av markørgener for hver klynge
o Funksjonell annotering og berikelse av markørgener
o Differensielt uttrykk for samme klynge mellom grupper
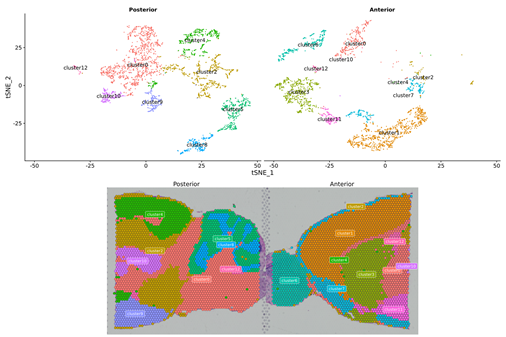
Analyse av indre prøve
Flekkgruppering
Markørgener identifisering og romlig distribusjon
Intergruppeanalyse
Datakombinasjon fra begge grupper og re-cluster
Markørgener for nye klynger
Utforsk fremskritt tilrettelagt av BMKGenes romlige transkripsjonstjeneste av 10X Visium I disse omtalte publikasjonene:
Chen, D. et al.(2023) 'mthl1, en potensiell Drosophila-homolog av pattedyradhesjons-GPCR-er, er involvert i antitumorreaksjoner på injiserte onkogene celler i fluer', Proceedings of the National Academy of Sciences of the United States of America, 120(30), s.e2303462120.doi: /10.1073/pnas.2303462120
Chen, Y. et al.(2023) 'STEEL muliggjør høyoppløselig avgrensning av spatiotemporale transkriptomiske data', Briefings in Bioinformatics, 24(2), s. 1–10.doi: 10.1093/BIB/BBAD068.
Liu, C. et al.(2022) 'A spatiotemporal atlas of organogenesis in the development of orchid flowers', Nucleic Acids Research, 50(17), s. 9724–9737.doi: 10.1093/NAR/GKAC773.
Wang, J. et al.(2023) "Integrating Spatial Transcriptomics and Single-nucleus RNA Sequencing Reveals the Potential Therapeutic Strategies for Uterine Leiomyoma", International Journal of Biological Sciences, 19(8), s. 2515–2530.doi: 10.7150/IJBS.83510.