
पूर्ण-लम्बाइ mRNA अनुक्रमण - PacBio
सेवा लाभहरू
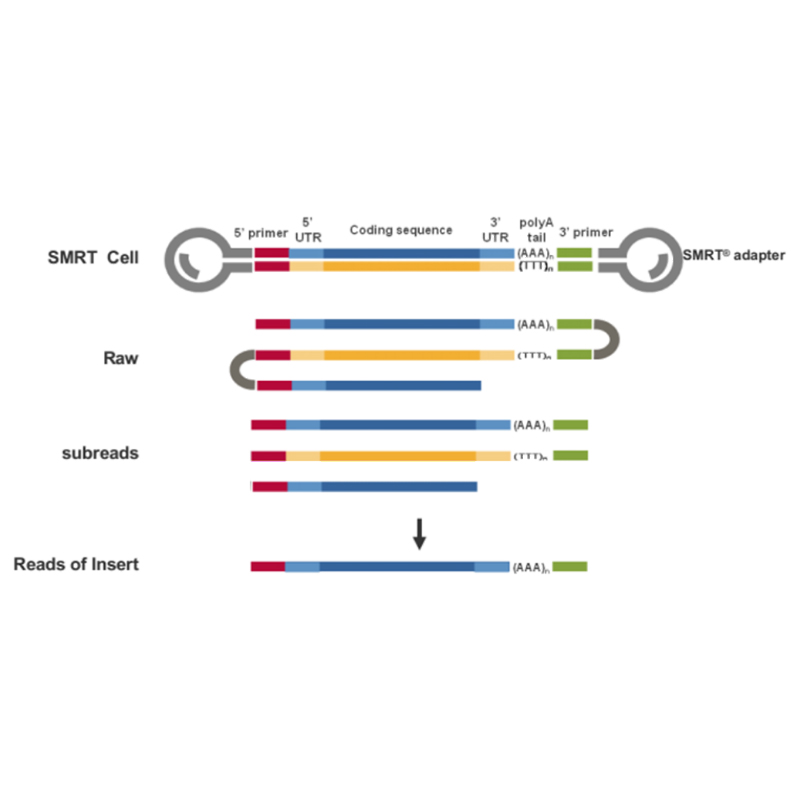
● 3'- अन्त्यदेखि 5'- अन्त्यसम्म पूर्ण-लम्बाइको cDNA अणुको प्रत्यक्ष पढाइ
● अनुक्रम संरचनामा आईएसओ-फार्म स्तर रिजोल्युसन
● उच्च शुद्धता र अखण्डताका साथ ट्रान्सक्रिप्टहरू
● vaours प्रजातिहरूको लागि उच्च मिल्दो
● 4 PacBio सिक्वेल II अनुक्रमणिका प्लेटफर्महरू सुसज्जित भएको ठूलो अनुक्रमण क्षमता
● 700 भन्दा बढी Pacbio-आधारित RNA अनुक्रमण परियोजनाहरूसँग अत्यधिक अनुभवी
● BMKCloud-आधारित परिणाम वितरण: प्लेटफर्ममा अनुकूलित डाटा-खनन उपलब्ध छ।
● परियोजना पूरा भएपछि 3 महिनाको लागि मान्य बिक्री पछि सेवाहरू
सेवा विशिष्टताहरू
प्लेटफर्म: PacBio सिक्वेल II
अनुक्रम पुस्तकालय: Poly A- समृद्ध mRNA पुस्तकालय
सिफारिस गरिएको डाटा उपज: 20 Gb/नमूना (प्रजातिहरूमा निर्भर गर्दै)
FLNC(%): ≥75%
*FLNC: पूर्ण-लम्बाइ गैर-काइमेरिक ट्रान्सिप्टहरू
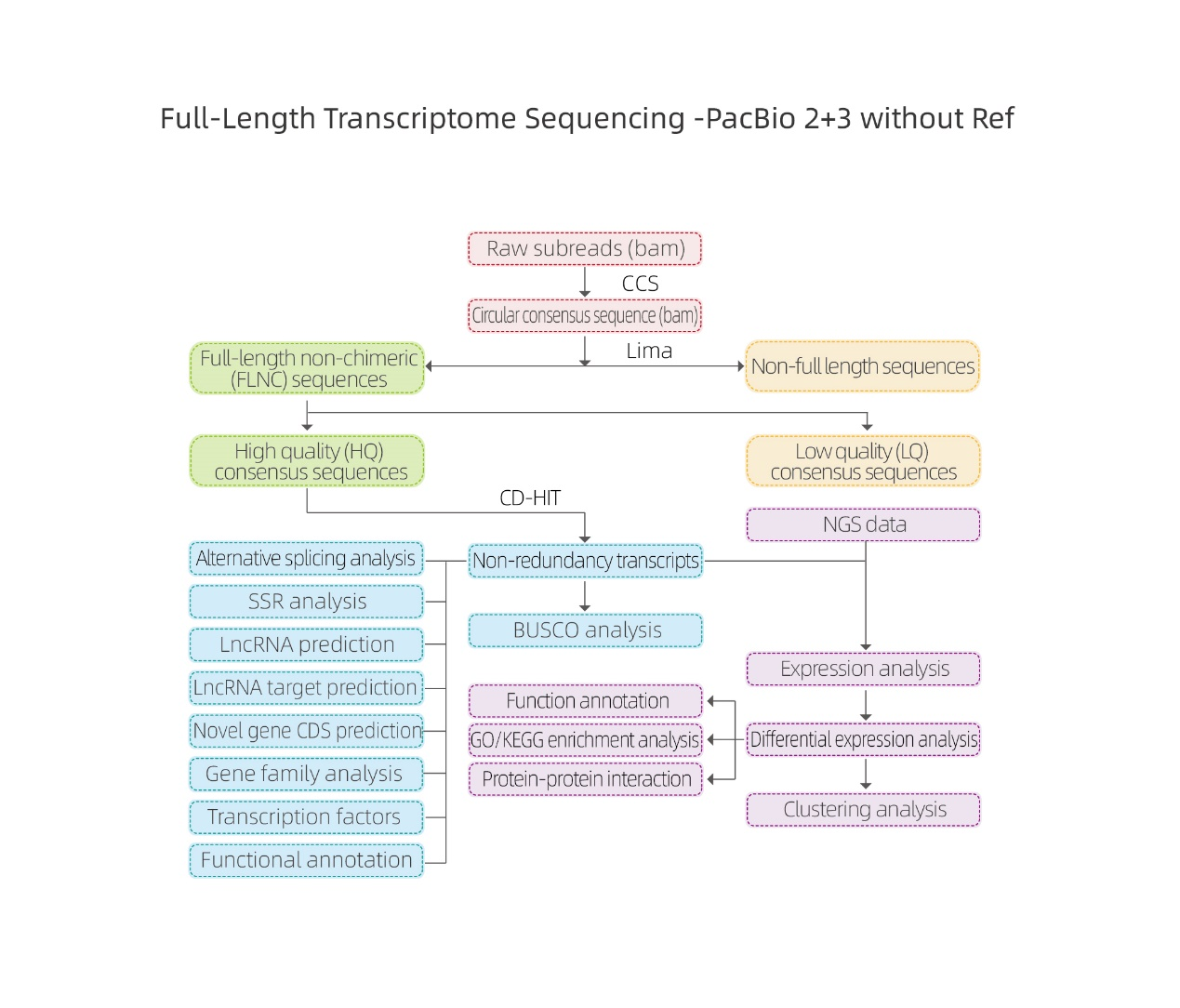
बायोइन्फर्मेटिक्स विश्लेषण
● कच्चा डाटा प्रशोधन
● ट्रान्सक्रिप्ट पहिचान
● अनुक्रम संरचना
● अभिव्यक्ति परिमाणीकरण
● प्रकार्य एनोटेसन
नमूना आवश्यकताहरू र डेलिभरी
नमूना आवश्यकताहरू:
न्यूक्लियोटाइड्स:
| Conc.(ng/μl) | रकम (μg) | शुद्धता | निष्ठा |
| ≥ १२० | ≥ ०.६ | OD260/280=1.7-2.5 OD260/230=0.5-2.5 जेलमा देखाइएको सीमित वा कुनै प्रोटीन वा डीएनए प्रदूषण। | बिरुवाहरूको लागि: RIN≥7.5; जनावरहरूको लागि: RIN≥8.0; 5.0≥ 28S/18S≥1.0; सीमित वा कुनै आधार रेखा उचाइ |
तन्तु: वजन (सुखा):≥1 ग्राम
*५ मिलीग्राम भन्दा सानो टिस्युको लागि, हामी फ्ल्याश फ्रोजन (तरल नाइट्रोजनमा) टिस्यु नमूना पठाउन सिफारिस गर्छौं।
सेल निलम्बन:सेल गणना = 3 × 106- 1×107
*हामी फ्रोजन सेल लाइसेट पठाउन सिफारिस गर्छौं।यदि त्यो कक्ष 5×10 भन्दा सानो गणना हुन्छ5, तरल नाइट्रोजनमा जमेको फ्ल्याश सिफारिस गरिएको छ, जुन सूक्ष्म निकासीको लागि उपयुक्त छ।
रगत नमूना:भोल्युम≥1 एमएल
सूक्ष्मजीव:मास ≥ 1 ग्राम
सिफारिस गरिएको नमूना वितरण
कन्टेनर:
2 एमएल सेन्ट्रीफ्यूज ट्यूब (टिन पन्नी सिफारिस गरिएको छैन)
नमूना लेबलिंग: समूह + प्रतिकृति जस्तै A1, A2, A3;B1, B2, B3...
ढुवानी:
1. ड्राई-बरफ: नमूनाहरू झोलाहरूमा प्याक गरी ड्राई-बरफमा गाडिनु पर्छ।
2. RNAstable ट्यूबहरू: RNA नमूनाहरू RNA स्थिरीकरण ट्यूब (जस्तै RNAstable®) मा सुकाउन सकिन्छ र कोठाको तापक्रममा पठाउन सकिन्छ।
सेवा कार्य प्रवाह

प्रयोग डिजाइन

नमूना वितरण

आरएनए निकासी

पुस्तकालय निर्माण

अनुक्रम

डाटा विश्लेषण

बिक्री पछि सेवाहरू
1.FLNC लम्बाइ वितरण
पूर्ण-लम्बाइ गैर-काइमेरिक रिड (FLNC) को लम्बाइले पुस्तकालय निर्माणमा cDNA को लम्बाइलाई सङ्केत गर्छ।FLNC लम्बाइ वितरण पुस्तकालय निर्माण को गुणस्तर मूल्याङ्कन मा एक महत्वपूर्ण सूचक हो।
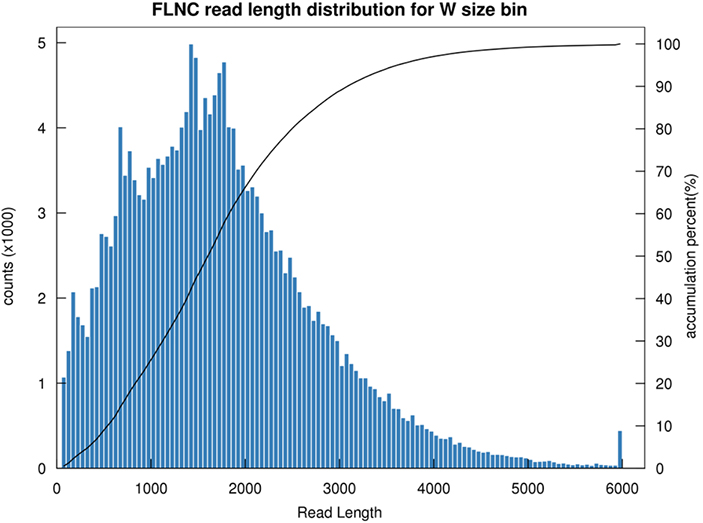
FLNC पढ्ने लम्बाइ वितरण
2. पूरा ORF क्षेत्र लम्बाइ वितरण
हामी प्रोटिन कोडिङ क्षेत्रहरू र सम्बन्धित एमिनो एसिड अनुक्रमहरू यूनिजीन सेटहरू उत्पन्न गर्नको लागि भविष्यवाणी गर्न ट्रान्सडेकोडर प्रयोग गर्छौं, जसमा सबै नमूनाहरूमा पूर्ण गैर-रिडन्डन्ट ट्रान्सक्रिप्ट जानकारी समावेश हुन्छ।
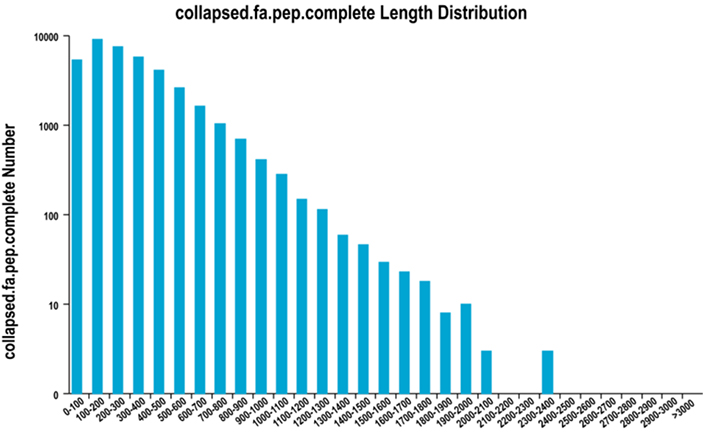
ORF क्षेत्र लम्बाइ वितरण पूरा गर्नुहोस्
3.KEGG मार्ग संवर्धन विश्लेषण
PacBio अनुक्रमण डेटा द्वारा उत्पन्न पूर्ण-लम्बाइ ट्रान्सक्रिप्ट सेटहरूमा NGS-आधारित RNA अनुक्रमण डेटा पङ्क्तिबद्ध गरेर भिन्न रूपमा व्यक्त ट्रान्सक्रिप्टहरू (DETs) पहिचान गर्न सकिन्छ।यी DET हरू विभिन्न कार्यात्मक विश्लेषणको लागि थप प्रशोधन गर्न सकिन्छ, जस्तै KEGG मार्ग संवर्धन विश्लेषण।
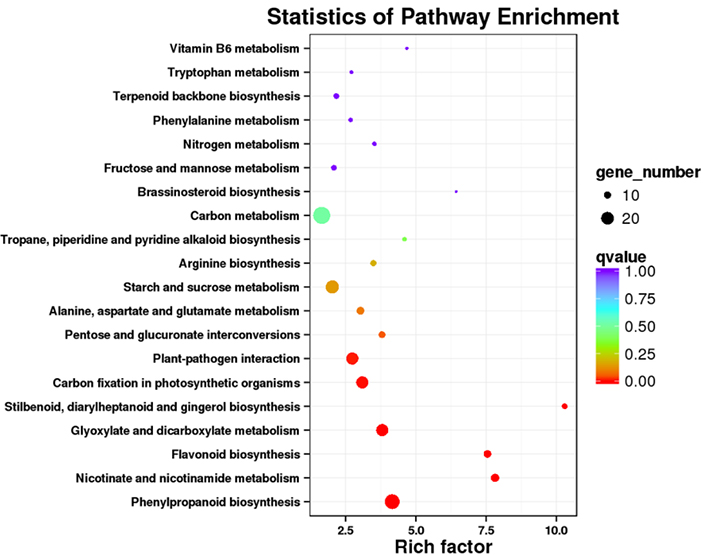
DET KEGG मार्ग संवर्धन - डट प्लट
BMK केस
Populus स्टेम ट्रान्सक्रिप्टोम को विकास गतिशीलता
प्रकाशित: प्लान्ट बायोटेक्नोलोजी जर्नल, २०१९
अनुक्रम रणनीति:
नमूना संग्रह:स्टेम क्षेत्रहरू: शीर्ष, पहिलो इन्टरनोड (IN1), दोस्रो इन्टरनोड (IN2), तेस्रो इन्टरनोड (IN3), इन्टरनोड (IN4) र Nanlin895 बाट इन्टरनोड (IN5)
NGS-अनुक्रम:15 व्यक्तिहरूको आरएनए एक जैविक नमूनाको रूपमा जम्मा गरिएको थियो।प्रत्येक बिन्दुको तीन जैविक प्रतिकृतिहरू NGS अनुक्रमको लागि प्रशोधन गरिएको थियो
TGS-अनुक्रम:स्टेम क्षेत्रहरूलाई तीन क्षेत्रहरूमा विभाजन गरिएको थियो, अर्थात् शीर्ष, IN1-IN3 र IN4-IN5।प्रत्येक क्षेत्रलाई चार प्रकारका पुस्तकालयहरू सहित PacBio अनुक्रमणिका लागि प्रशोधन गरिएको थियो: 0-1 kb, 1-2 kb, 2-3 kb र 3-10 kb।
प्रमुख परिणामहरू
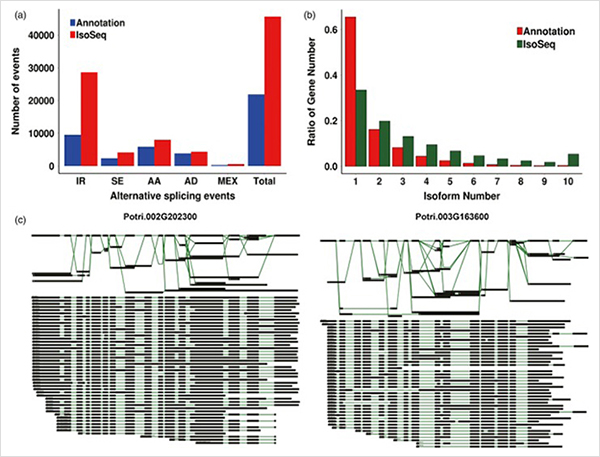
1. कुल 87150 पूर्ण-लम्बाइ ट्रान्सक्रिप्टहरू पहिचान गरिएको थियो, जसमा, 2081 उपन्यास आइसोफर्महरू र 62058 उपन्यास वैकल्पिक विभाजित आइसोफर्महरू पहिचान गरियो।
2.1187 lncRNA र 356 फ्युजन जीनहरू पहिचान गरियो।
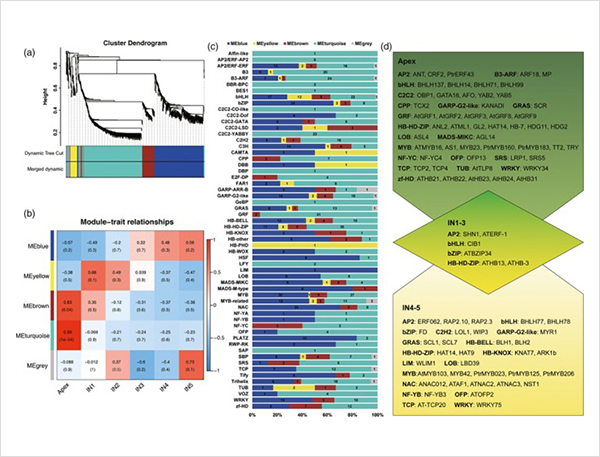
3.प्राथमिक वृद्धि देखि माध्यमिक वृद्धि सम्म, 15838 भिन्न रूप देखि व्यक्त 995 भिन्न जीनहरु लाई पहिचान गरियो।सबै DEGs मा, 1216 ट्रान्सक्रिप्शन कारकहरू थिए, जसमध्ये धेरै जसो अझै रिपोर्ट गरिएको छैन।
4.GO संवर्धन विश्लेषणले प्राथमिक र माध्यमिक वृद्धिमा कोशिका विभाजन र अक्सिडेशन-घटाउने प्रक्रियाको महत्त्व प्रकट गर्यो।
वैकल्पिक विभाजन घटनाहरू र विभिन्न isoforms
ट्रान्सक्रिप्शन कारकहरूमा WGCNA विश्लेषण
सन्दर्भ
चाओ Q, Gao ZF, Zhang D, et al।Populus स्टेम ट्रान्सक्रिप्टोम को विकास गतिशीलता।प्लान्ट बायोटेक्नोल जे. 2019;17(1):206-219।doi:10.1111/pbi.12958











