
Urutan mRNA berdurasi penuh -PacBio
Keunggulan Layanan
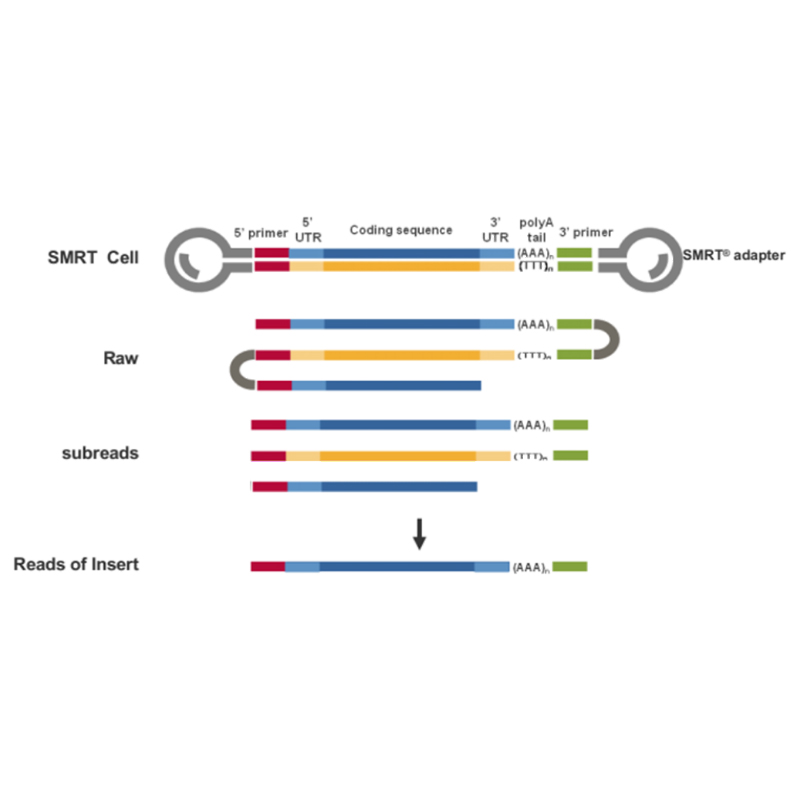
● Pembacaan langsung molekul cDNA panjang penuh dari ujung 3'- hingga ujung 5'-
● Resolusi tingkat bentuk iso dalam struktur urutan
● Transkrip dengan akurasi dan integritas tinggi
● Sangat kompatibel dengan spesies apa pun
● Kapasitas pengurutan yang besar dengan dilengkapi 4 platform pengurutan PacBio Sekuel II
● Sangat berpengalaman dengan lebih dari 700 proyek pengurutan RNA berbasis Pacbio
● Pengiriman hasil berbasis BMKCloud: Penambangan data yang disesuaikan tersedia di platform.
● Layanan purna jual berlaku selama 3 bulan setelah proyek selesai
Spesifikasi Layanan
Platform: Sekuel PacBio II
Perpustakaan sekuensing: Perpustakaan mRNA yang diperkaya Poli A
Hasil data yang disarankan: 20 Gb/sampel (Tergantung spesies)
FLNC(%): ≥75%
*FLNC: Transkrip non-chimeric berdurasi penuh
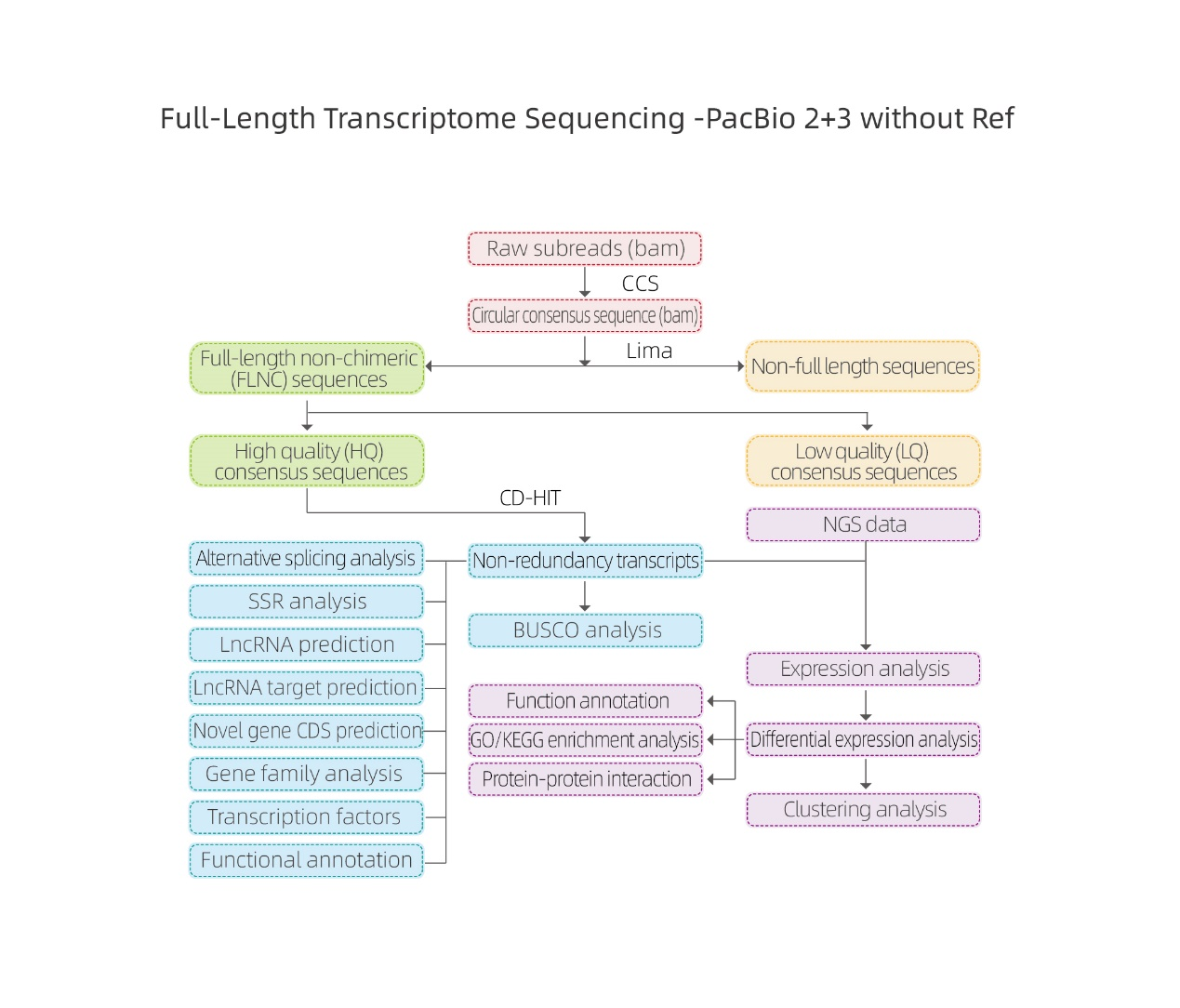
Analisis bioinformatika
● Pemrosesan data mentah
● Identifikasi transkrip
● Struktur urutan
● Kuantifikasi Ekspresi
● Anotasi Fungsi
Persyaratan Sampel dan Pengiriman
Persyaratan Sampel:
Nukleotida:
| Konsentrasi (ng/μl) | Jumlah (μg) | Kemurnian | Integritas |
| ≥ 120 | ≥ 0,6 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Kontaminasi protein atau DNA terbatas atau tidak ada pada gel. | Untuk tanaman: RIN≥7.5; Untuk hewan: RIN≥8.0; 5,0≥ 28S/18S≥1,0; elevasi dasar yang terbatas atau tidak ada sama sekali |
Jaringan: Berat (kering):≥1 gram
*Untuk jaringan yang lebih kecil dari 5 mg, kami menyarankan untuk mengirimkan sampel jaringan beku (dalam nitrogen cair).
Suspensi sel:Jumlah sel = 3×106- 1×107
*Kami menyarankan untuk mengirimkan lisat sel beku.Jika jumlah sel tersebut lebih kecil dari 5×105, direkomendasikan untuk dibekukan dalam nitrogen cair, yang lebih disukai untuk ekstraksi mikro.
Sampel darah:Volume≥1 mL
Mikroorganisme:Massa ≥ 1 gram
Pengiriman Sampel yang Direkomendasikan
Wadah:
Tabung centrifuge 2 ml (kertas timah tidak disarankan)
Contoh pelabelan: Grup+replikasi misalnya A1, A2, A3;B1, B2, B3... ...
Pengiriman:
1. Es kering: Sampel harus dikemas dalam kantong dan dikubur dalam es kering.
2. Tabung RNAstabil: Sampel RNA dapat dikeringkan dalam tabung stabilisasi RNA (misalnya RNAstable®) dan dikirim dalam suhu kamar.
Alur Kerja Layanan

Desain percobaan

Pengiriman sampel

Ekstraksi RNA

Pembangunan perpustakaan

Pengurutan

Analisis data

Layanan purna jual
1. Distribusi panjang FLNC
Panjang pembacaan non-chimeric penuh (FLNC) menunjukkan panjang cDNA dalam konstruksi perpustakaan.Distribusi panjang FLNC merupakan indikator penting dalam mengevaluasi kualitas konstruksi perpustakaan.
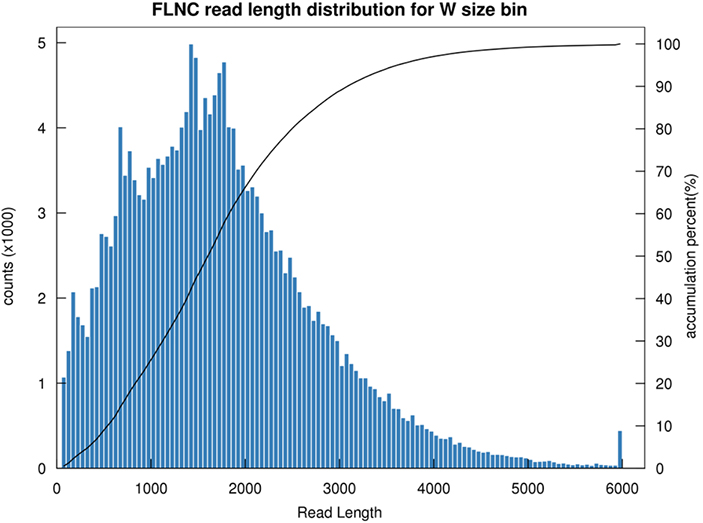
Distribusi panjang baca FLNC
2. Distribusi panjang wilayah ORF yang lengkap
Kami menggunakan TransDecoder untuk memprediksi daerah pengkode protein dan urutan asam amino yang sesuai untuk menghasilkan set unigene, yang berisi informasi transkrip lengkap yang tidak berlebihan di semua sampel.
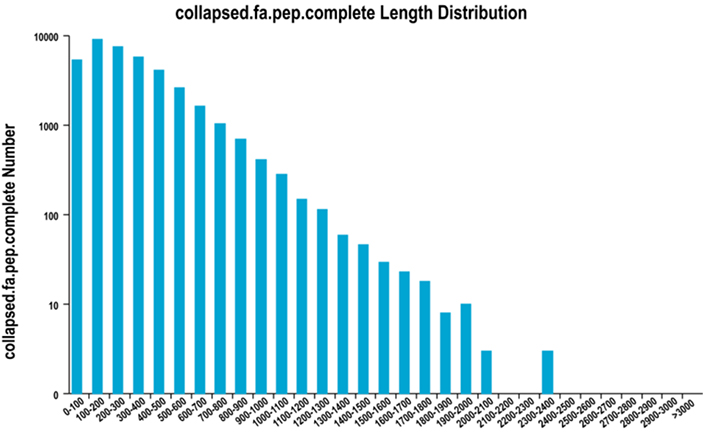
Menyelesaikan distribusi panjang wilayah ORF
3. Analisis pengayaan jalur KEGG
Transkrip yang diekspresikan secara berbeda (DET) dapat diidentifikasi dengan menyelaraskan data pengurutan RNA berbasis NGS pada set transkrip panjang penuh yang dihasilkan oleh data pengurutan PacBio.DET ini selanjutnya dapat diproses untuk berbagai analisis fungsional, misalnya analisis pengayaan jalur KEGG.
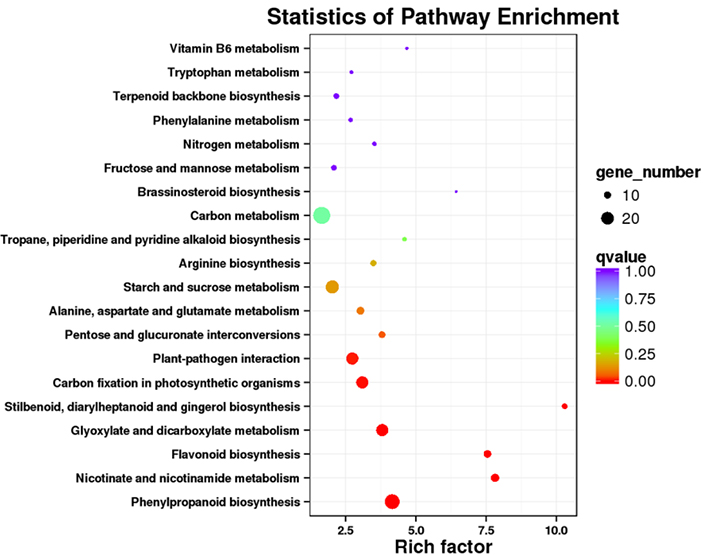
Pengayaan jalur DET KEGG -Dot plot
Kasus BMK
Dinamika perkembangan transkriptom batang Populus
Diterbitkan: Jurnal Bioteknologi Tanaman, 2019
Strategi pengurutan:
Koleksi sampel:daerah batang: puncak, ruas pertama (IN1), ruas kedua (IN2), ruas ketiga (IN3), ruas (IN4) dan ruas (IN5) dari Nanlin895
Urutan NGS:RNA dari 15 individu dikumpulkan sebagai satu sampel biologis.Tiga ulangan biologis dari setiap titik diproses untuk urutan NGS
Urutan TGS:Daerah batang dibagi menjadi tiga daerah yaitu apex, IN1-IN3 dan IN4-IN5.Setiap wilayah diproses untuk pengurutan PacBio dengan empat jenis perpustakaan: 0-1 kb, 1-2 kb, 2-3 kb, dan 3-10 kb.
Hasil utama
1. Sebanyak 87150 transkrip lengkap diidentifikasi, di mana, 2081 isoform baru dan 62058 isoform sambungan alternatif baru diidentifikasi.
2.1187 lncRNA dan 356 gen fusi diidentifikasi.
3.Dari pertumbuhan primer ke pertumbuhan sekunder, 15838 transkrip yang diekspresikan secara berbeda dari 995 gen yang diekspresikan secara berbeda telah diidentifikasi.Di semua DEG, 1.216 merupakan faktor transkripsi, yang sebagian besar belum dilaporkan.
4. Analisis pengayaan GO mengungkapkan pentingnya pembelahan sel dan proses reduksi oksidasi dalam pertumbuhan primer dan sekunder.
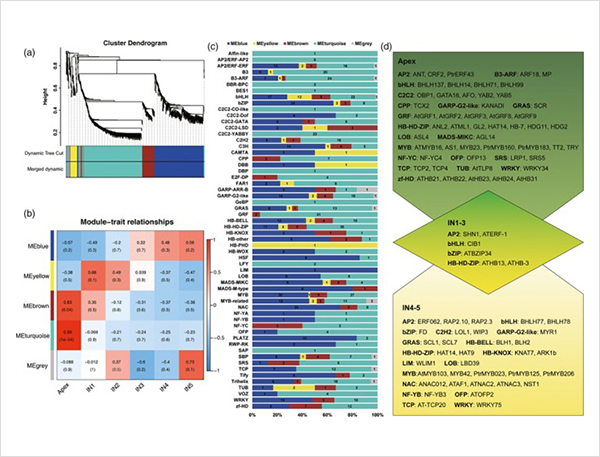
Peristiwa penyambungan alternatif dan isoform berbeda
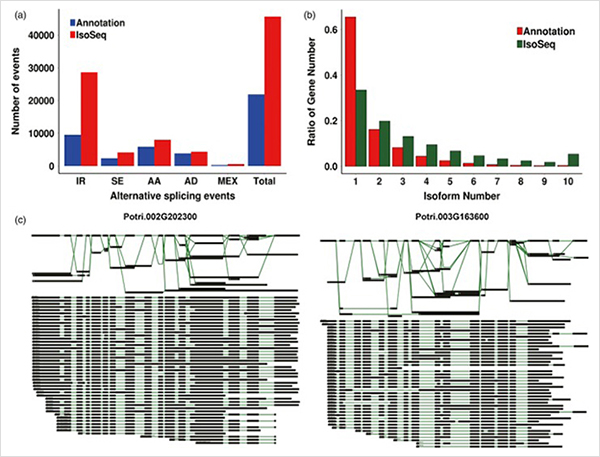
Analisis WGCNA pada faktor transkripsi
Referensi
Chao Q, Gao ZF, Zhang D, dkk.Dinamika perkembangan transkriptom batang Populus.Bioteknologi Tanaman J. 2019;17(1):206-219.doi:10.1111/pbi.12958











