Lange niet-coderende sequencing-Illumina
Servicevoordelen
● Servicevoordelen
● Cellulair en weefselspecifiek
● Specifieke fase drukt en presenteert dynamische expressieverandering
● Nauwkeurige patronen van tijd- en ruimte-expressie
● Gezamenlijke analyse met mRNA-gegevens.
● Op BMKCloud gebaseerde resultaatlevering: op maat gemaakte datamining beschikbaar op het platform.
● After-sales services geldig gedurende 3 maanden na voltooiing van het project
Monstervereisten en levering
| Bibliotheek | Platform | Aanbevolen gegevens | Gegevens kwaliteitscontrole |
| rRNA-uitputting | Illumina PE150 | 10 GB | Q30≥85% |
| Conc. (ng/μl) | Hoeveelheid (μg) | Puurheid | Integriteit |
| ≥ 100 | ≥ 0,5 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Beperkte of geen eiwit- of DNA-verontreiniging weergegeven op de gel. | Voor planten: RIN≥6,5; Voor dieren: RIN≥7,0; 5,0≥28S/18S≥1,0; beperkte of geen basislijnhoogte |
Nucleotiden:
Weefsel: Gewicht (droog): ≥1 g
*Voor weefsel kleiner dan 5 mg raden wij aan om snel ingevroren (in vloeibare stikstof) weefselmonsters op te sturen.
Celsuspensie: celgetal = 3×107
*Wij raden aan om bevroren cellysaat te verzenden.In het geval dat het aantal cellen kleiner is dan 5×105wordt snel ingevroren in vloeibare stikstof aanbevolen.
Bloedstalen:
PA×genBloodRNATube;
6 mlLTRIzol en 2 ml bloed (TRIzol:Bloed=3:1)
Aanbevolen monsterlevering
Verpakking: centrifugebuisje van 2 ml (aluminiumfolie wordt niet aanbevolen)
Monsterlabeling: groeperen+repliceren, bijvoorbeeld A1, A2, A3;B1, B2, B3... ...
Verzending:
1. Droogijs: monsters moeten in zakken worden verpakt en in droogijs worden begraven.
2.RNAstable buizen: RNA-monsters kunnen worden gedroogd in een RNA-stabilisatiebuis (bijv. RNAstable®) en bij kamertemperatuur worden verzonden.
Servicewerkstroom

Experimentontwerp

Levering van monsters

RNA-extractie

Bouw van bibliotheek

Volgorde aanbrengen in

Gegevensanalyse

After-sales diensten
Bio-informatica
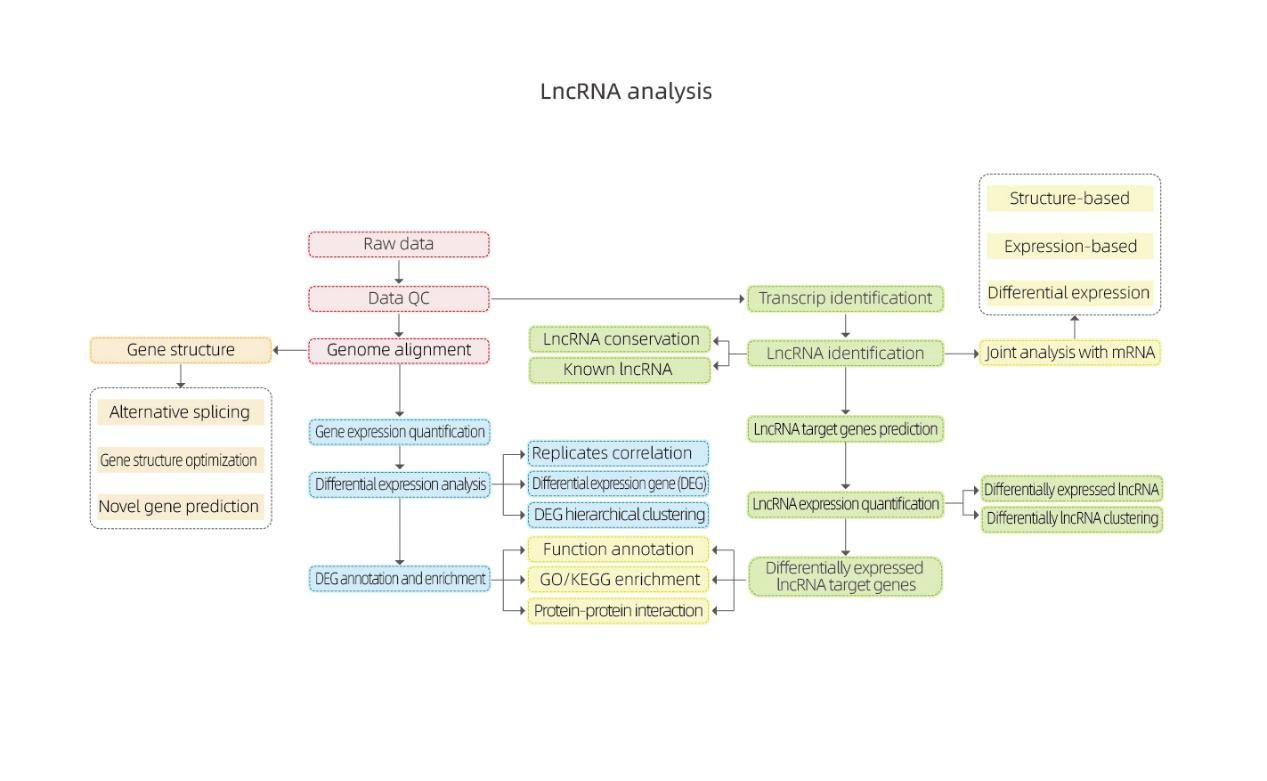
1.LncRNA-classificatie
LncRNA voorspeld door de vier bovenstaande software werd geclassificeerd in 4 categorieën: lincRNA, anti-sense-LncRNA, intronic-LncRNA;sense-LncRNA.De LncRNA-classificatie werd weergegeven in het onderstaande histogram.
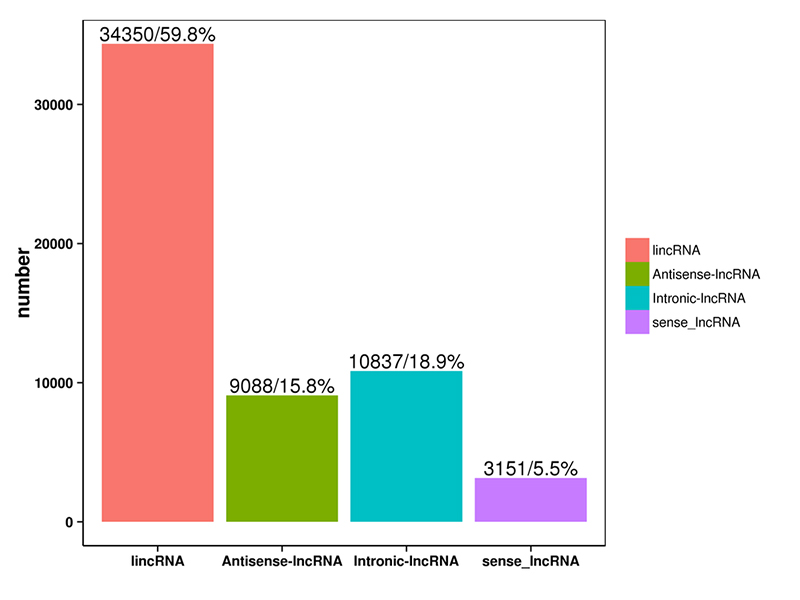
LncRNA-classificatie
2.Cis-gerichte genen van DE-lncRNA-verrijkingsanalyse
ClusterProfiler werd gebruikt bij GO-verrijkingsanalyse op cis-gerichte genen van differentieel tot expressie gebracht lncRNA (DE-lncRNA), in termen van biologische processen, moleculaire functies en cellulaire componenten.GO-verrijkingsanalyse is een proces om DEG-gerichte, aanzienlijk verrijkte GO-termen te identificeren in vergelijking met het hele genoom.De verrijkte termen werden gepresenteerd in histogram, bellendiagram, enz., zoals hieronder weergegeven.
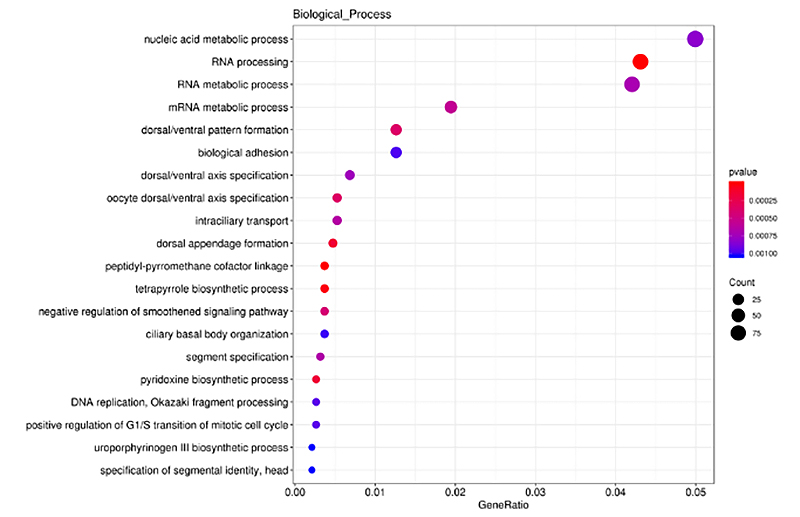 Cis-gerichte genen van DE-lncRNA-verrijkingsanalyse - Bellendiagram
Cis-gerichte genen van DE-lncRNA-verrijkingsanalyse - Bellendiagram
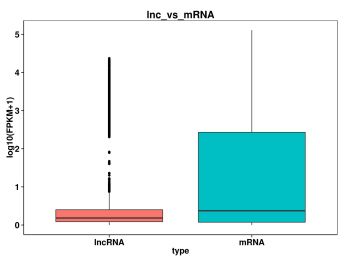
3. Door de lengte, het exon-nummer, het ORF en de expressiehoeveelheid van mRNA en lncRNA te vergelijken, kunnen we de verschillen in structuur, sequentie enzovoort daartussen begrijpen, en ook verifiëren of het door ons voorspelde nieuwe lncRNA voldoet aan de algemene kenmerken.
BMK-zaak
Gedereguleerd lncRNA-expressieprofiel in longadenocarcinomen van muizen met KRAS-G12D-mutatie en P53-knock-out
Gepubliceerd:Tijdschrift voor cellulaire en moleculaire geneeskunde,2019
Sequentiestrategie
Illumina
Monsterverzameling
De NONMMUT015812-knockdown KP (shRNA-2) cellen en negatieve controle (sh-Scr) cellen werden verkregen op dag 6 van een specifieke virale infectie.
Belangrijkste resultaten
Deze studie onderzoekt de afwijkend tot expressie gebrachte lncRNA's in het longadenocarcinoom van muizen met P53 knock-out en de KrasG12D-mutatie.
1,6424 lncRNA's werden differentieel tot expressie gebracht (≥ 2-voudige verandering, P <0,05).
2. Van alle 210 lncRNA's (FC≥8) werd de expressie van 11 lncRNA's gereguleerd door respectievelijk P53, 33 lncRNA's door KRAS en 13 lncRNA's door hypoxie in de primaire KP-cellen.
3.NONMMUT015812, dat opmerkelijk opwaarts werd gereguleerd in het longadenocarcinoom van muizen en negatief werd gereguleerd door de re-expressie van P53, werd gedetecteerd om de cellulaire functie ervan te analyseren.
4. Neerhalen van NONMMUT015812 door shRNA's verminderde de proliferatie en migratiecapaciteiten van KP-cellen.NONMMUT015812 was een potentieel oncogen.
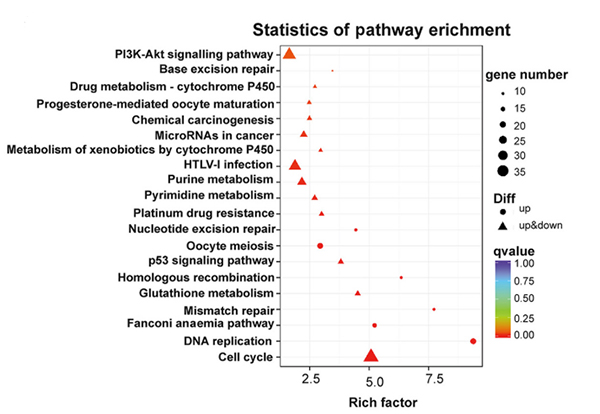 KEGG-pathwayanalyse van de differentieel tot expressie gebrachte genen in de NONMMUT015812-knockdown KP-cellen | 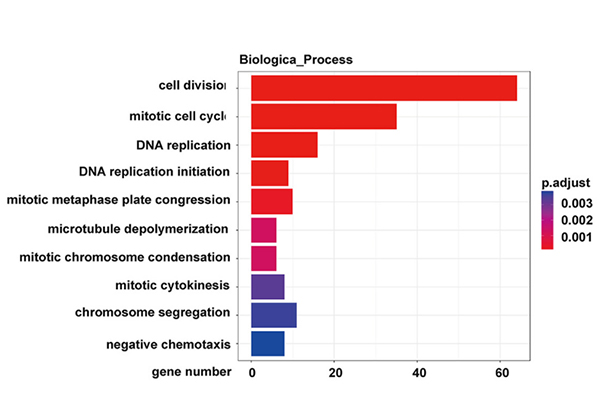 Gene Ontology-analyse van de differentieel tot expressie gebrachte genen in de NONMMUT015812-knockdown KP-cellen |
Referentie
Gedereguleerd lncRNA-expressieprofiel in de longadenocarcinomen van muizen met KRAS-G12D-mutatie en P53-knock-out [J].Journal of Cellular and Molecular Medicine, 2019, 23(10).DOI: 10.1111/jcmm.14584