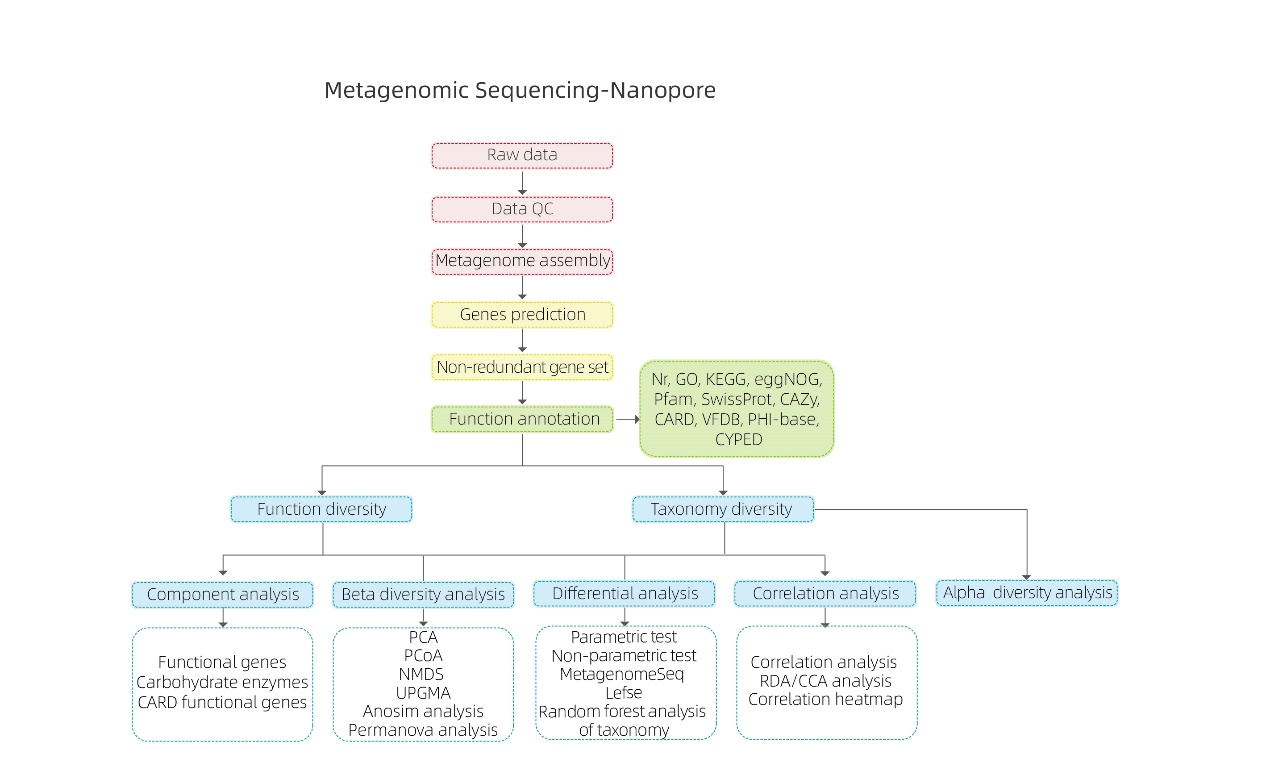
Metagenomisk sekvensering-Nanopore
Tjenestefordeler
● Høykvalitets montering – Forbedrer nøyaktigheten av artsidentifikasjon og funksjonell genprediksjon
● Lukket bakteriell genomisolering
● Kraftigere og mer pålitelig applikasjon i forskjellige områder, f.eks. påvisning av patogene mikroorganismer eller antibiotikaresistensrelaterte gener
● Komparativ metagenomanalyse
Tjenestespesifikasjoner
| Plattform | Sekvensering | Anbefalte data | Omløpstid |
| Nanopore | PÅ T | 6 G/10 G | 65 virkedager |
Bioinformatikkanalyser
● Kvalitetskontroll av rådata
● Metagenommontering
● Ikke-redundant gensett og merknad
● Artsmangfoldsanalyse
● Genetisk funksjonsmangfoldsanalyse
● Intergruppeanalyse
● Assosiasjonsanalyse mot eksperimentelle faktorer
Prøvekrav og levering
Prøvekrav og levering
Eksempelkrav:
TilDNA-ekstrakter:
| Eksempeltype | Beløp | Konsentrasjon | Renhet |
| DNA-ekstrakter | 1-1,5 μg | > 20 ng/μl | OD260/280= 1,6-2,5 |
For miljøprøver:
| Prøvetype | Anbefalt prøvetakingsprosedyre |
| Jord | Prøvemengde: ca.5 g;Gjenværende visnet substans må fjernes fra overflaten;Mal store stykker og passer gjennom 2 mm filter;Aliquot prøver i sterilt EP-rør eller cyrotube for reservasjon. |
| Avføring | Prøvemengde: ca.5 g;Samle og alikvoter prøver i sterilt EP-rør eller kryotube for reservasjon. |
| Tarminnhold | Prøver må behandles under aseptisk tilstand.Vask oppsamlet vev med PBS;Sentrifuger PBS og samle utfellingsmidlet i EP-rør. |
| Slam | Prøvemengde: ca.5 g;Samle og alikvoter slamprøve i sterilt EP-rør eller kryotube for reservasjon |
| Vann kropp | For prøver med begrenset mengde mikrobielle, for eksempel vann fra springen, brønnvann, etc., Saml minst 1 L vann og passer gjennom 0,22 μm filter for å berike mikrobielle på membranen.Oppbevar membranen i sterilt rør. |
| Hud | Skrap hudoverflaten forsiktig med en steril bomullspinne eller kirurgisk blad og plasser den i et sterilt rør. |
Anbefalt prøvelevering
Frys prøvene i flytende nitrogen i 3-4 timer og oppbevar i flytende nitrogen eller -80 grader til langtidsreservasjon.Prøvefrakt med tørris er nødvendig.
Servicearbeidsflyt

Prøvelevering

Bygging av bibliotek

Sekvensering

Dataanalyse

Ettersalgstjenester
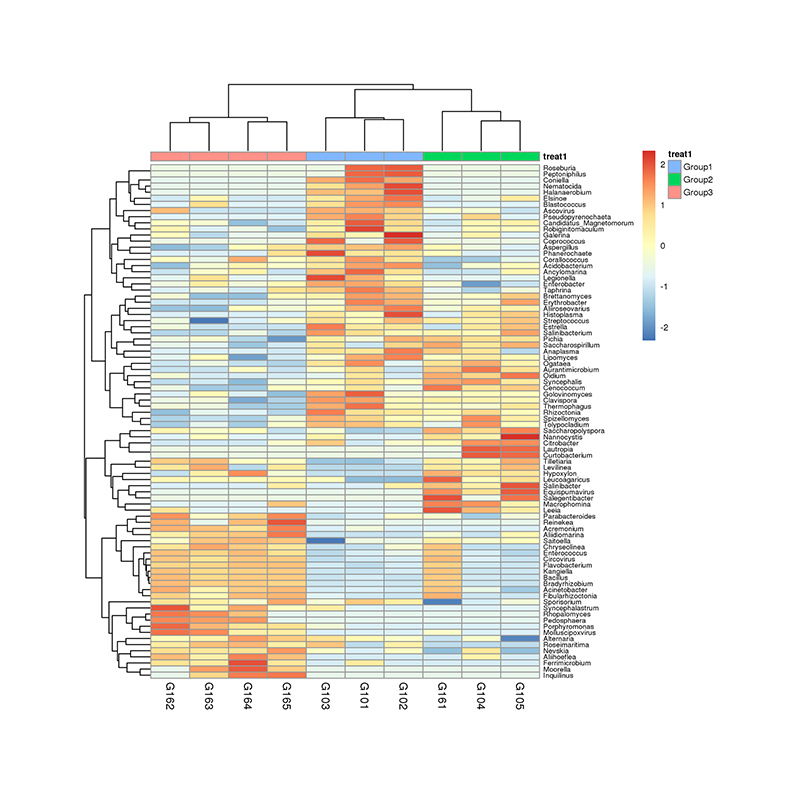
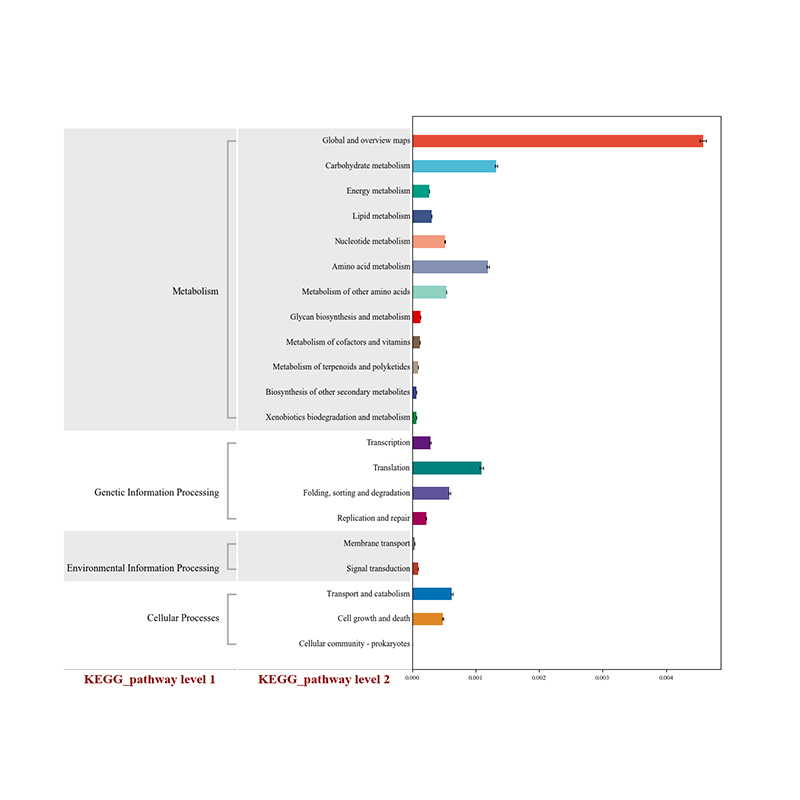
1. Varmekart: Artsrikdomsgruppering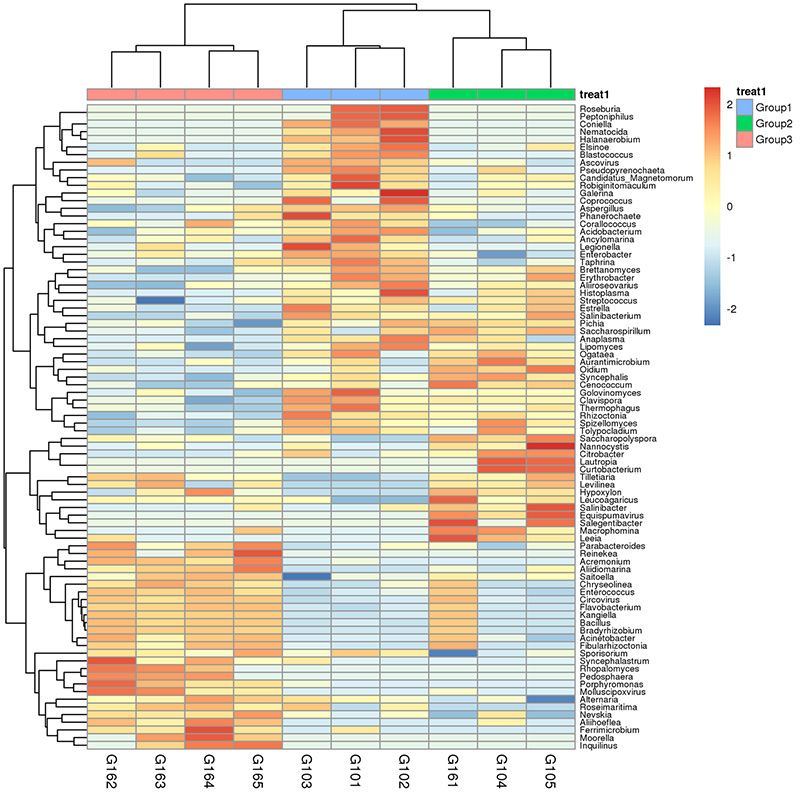 2. Funksjonelle gener annotert til KEGG metabolske veier
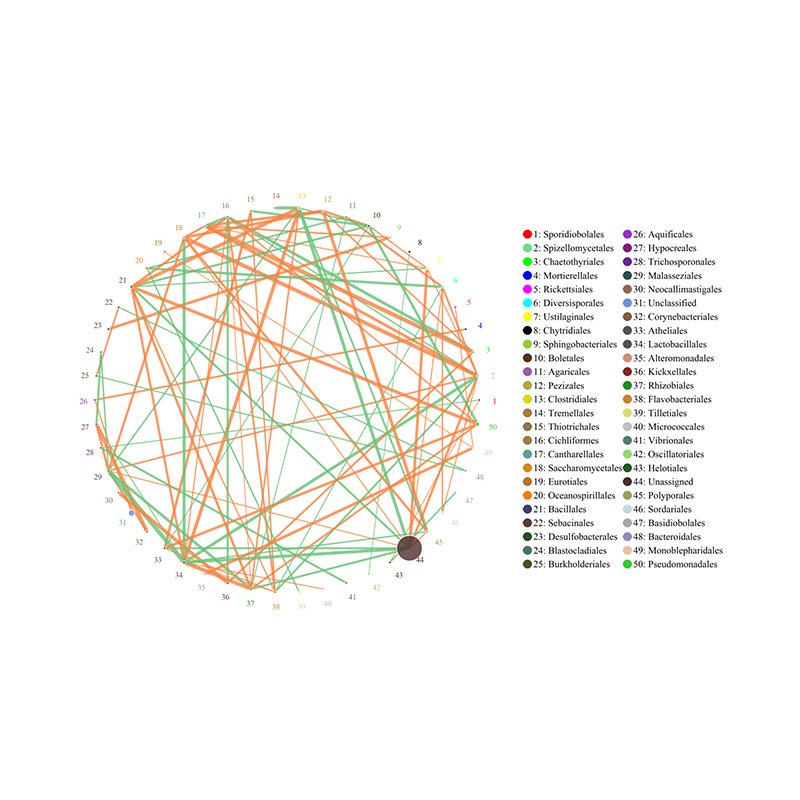
2. Funksjonelle gener annotert til KEGG metabolske veier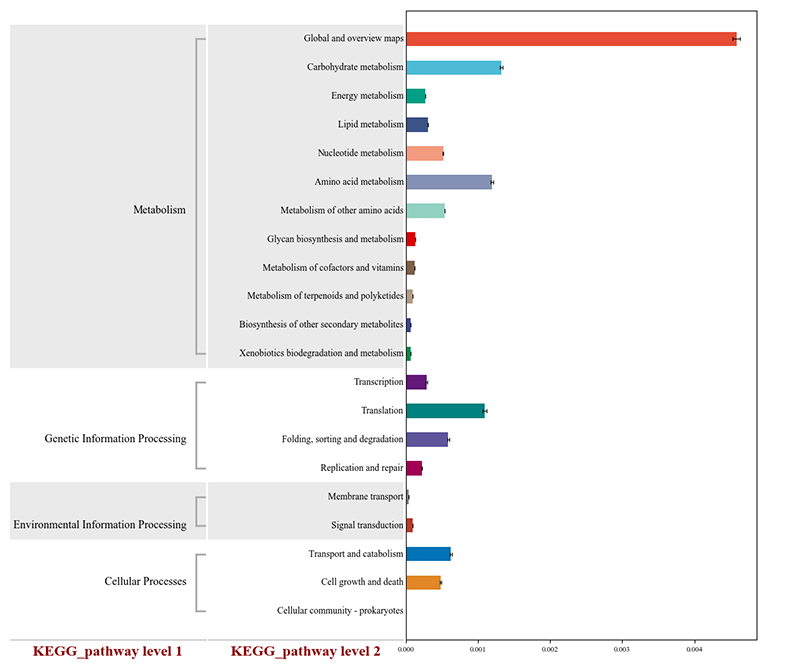 3. Artskorrelasjonsnettverk
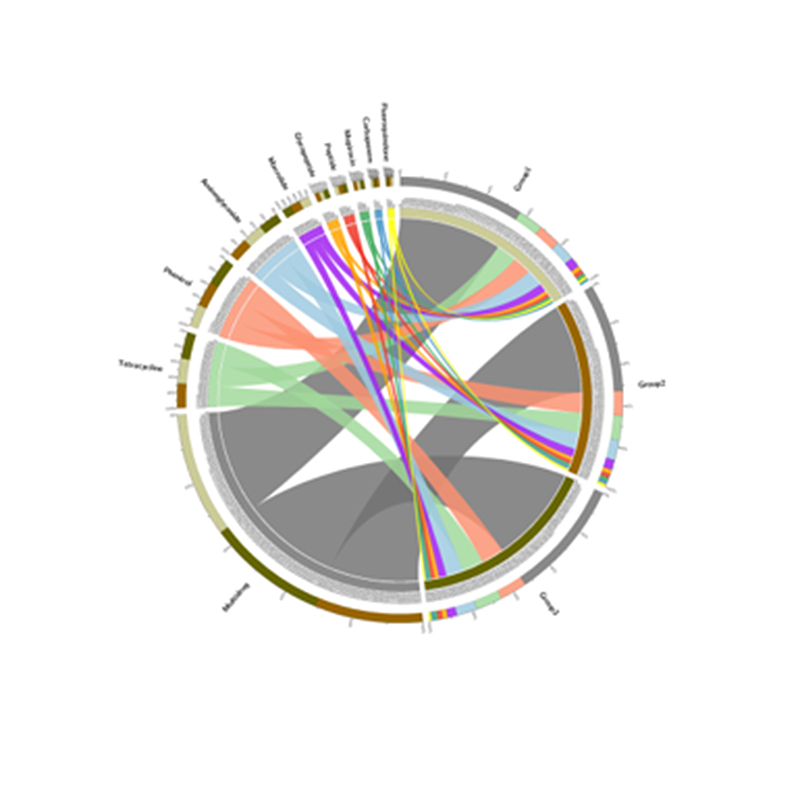
3. Artskorrelasjonsnettverk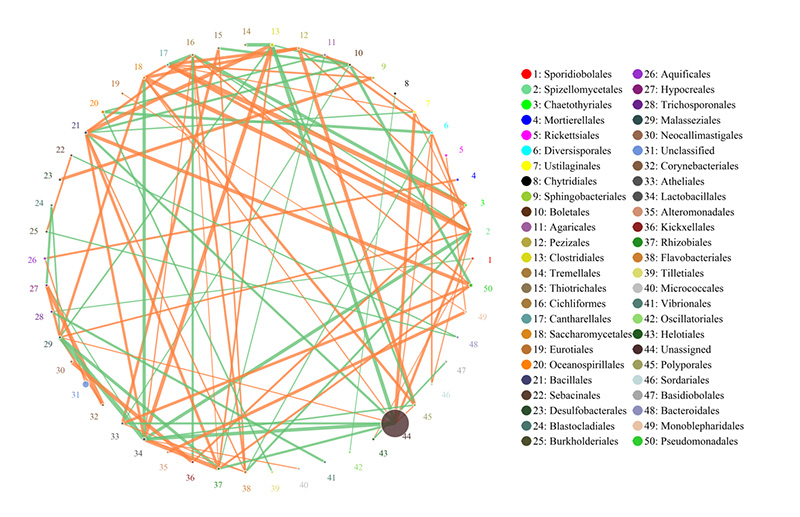 4. Circos of CARD antibiotikaresistensgener
4. Circos of CARD antibiotikaresistensgener
BMK sak
Nanopore metagenomics muliggjør rask klinisk diagnose av bakteriell nedre luftveisinfeksjon
Publisert:Naturbioteknologi, 2019
Tekniske høydepunkter
Sekvensering: Nanopore MinION
Klinisk metagenomikk bioinformatikk: verts-DNA-utarming, WIMP og ARMA-analyse
Rask deteksjon: 6 timer
Høy følsomhet: 96,6 %
Nøkkelresultater
I 2006 forårsaket nedre luftveisinfeksjon (LR) 3 millioner menneskers død globalt.Den typiske metoden for LR1-patogendeteksjon er dyrking, som har dårlig følsomhet, lang omløpstid og er mangel på veiledning i tidlig antibiotikabehandling.En rask og nøyaktig mikrobiell diagnose har lenge vært et presserende behov.Dr. Justin fra University of East Anglia og hans partnere har utviklet en Nanopore-basert metagenomisk metode for patogendeteksjon.I henhold til deres arbeidsflyt kan 99,99 % av verts-DNA bli utarmet.Påvisning i patogener og antibiotikaresistente gener kan være ferdig på 6 timer.
Henvisning
Charalampous, T., Kay, GL, Richardson, H., Aydin, A., & O'Grady, J..(2019).Nanopore metagenomics muliggjør rask klinisk diagnose av bakteriell nedre luftveisinfeksjon.Nature Biotechnology, 37(7), 1.