
Genetica Evolutiva
Vantaghji di serviziu
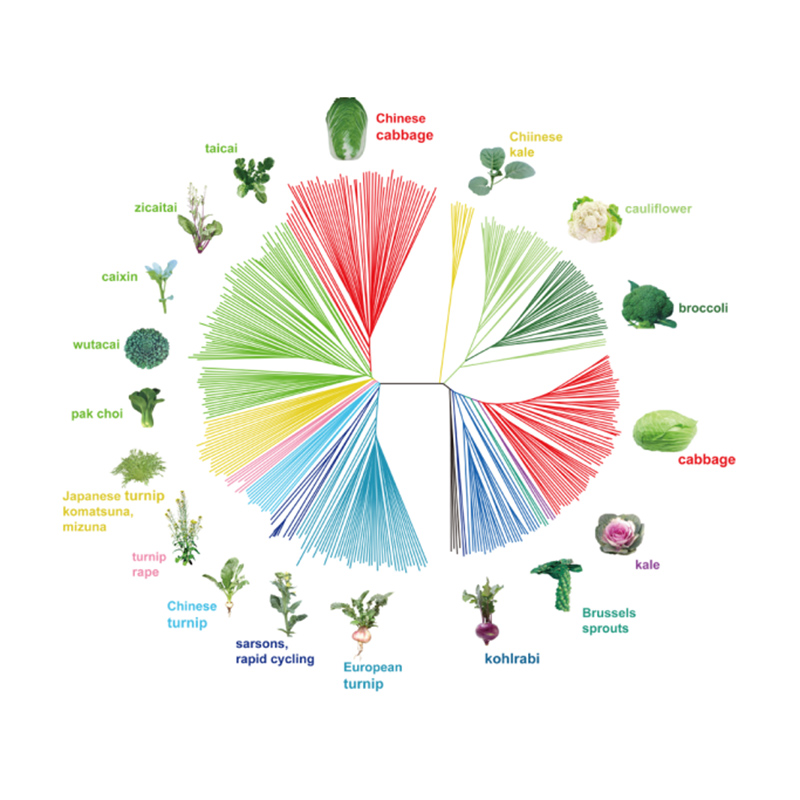
Takagi et al.,U ghjurnale di a pianta, 2013
● Stima di u tempu è a velocità di divergenza di spezie basatu annantu à variazioni à u nivellu di nucleotidi è aminoacidi
● Revelazione di una relazione filogenetica più affidabile trà spezie cù influenza minimizzata di l'evoluzione convergente è l'evoluzione parallela
● Custruì ligami trà i cambiamenti genetichi è i fenotipi per scopre i genesi di tratti
● Stima di a diversità genetica, chì riflette u putenziale evolutivu di e spezie
● Faster Turnaround time
● Esperienza estensiva: BMK hà accumulatu una sperienza massiccia in prughjetti di pupulazione è evoluzione per più di 12 anni, chì copre centinaie di spezie, etc., è hà cuntribuitu in più di 80 prughjetti d'altu livellu publicati in Nature Communications, Molecular Plants, Plant Biotechnology Journal, etc.
Specificazioni di serviziu
Materiali:
Normalmente, almenu trè sub-populazioni (per esempiu sottospecie o ceppi) hè cunsigliatu.Ogni sub-populazione ùn deve cuntene micca menu di 10 individui (Plants > 15, pò esse ridutta per spezie rari).
Strategia di sequenza:
* WGS pò esse impiegatu per spezie cù genoma di riferimentu di alta qualità, mentri SLAF-Seq hè applicabile à spezie cù o senza genoma di riferimentu, o genoma di riferimentu di qualità povera.
| Applicabile à a dimensione di u genoma | WGS | SLAF-Tags (×10.000) |
| ≤ 500 Mb | 10×/individuu | WGS hè più cunsigliatu |
| 500 Mb - 1 Gb | 10 | |
| 1 Gb - 2 Gb | 20 | |
| ≥2 Gb | 30 |
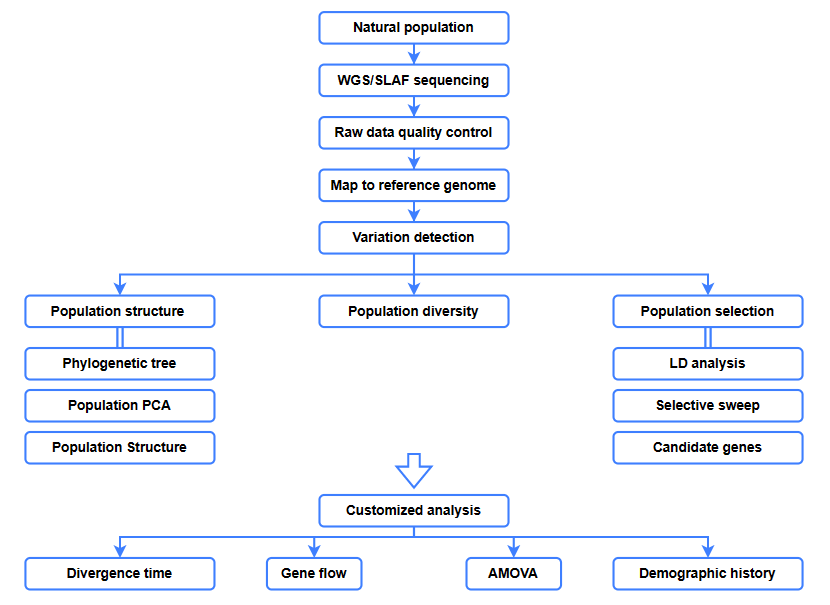
Analisi bioinformatica
● Analisi evolutivu
● Spazzatura selettiva
● Flussu di geni
● Storia demugrafica
● Tempu di divergenza
Requisiti di mostra è consegna
Requisiti di mostra:
| Spezie | Tissu | WGS-NGS | SLAF |
| Animal
| Tissu viscerale |
0,5 ~ 1 g
|
0,5 g
|
| Tissu musculu | |||
| Sangue di mammiferi | 1,5 ml
| 1,5 ml
| |
| Sangue di pollame/pesce | |||
| Pianta
| Foglia fresca | 1 ~ 2 g | 0,5 ~ 1 g |
| Petale/Stem | |||
| Radici / Semente | |||
| Cellule | Cellula cultivata |
| gDNA | Cuncentrazione | A quantità (ug) | OD260/OD280 |
| SLAF | ≥35 | ≥1,6 | 1,6-2,5 |
| WGS-NGS | ≥1 | ≥ 0,1 | - |
Flussu di travagliu di serviziu

Prughjettu di cuncepimentu

Consegna di mostra

Custruzzione di biblioteca

Sequencing

Analisi di dati

Servizi post-vendita
*I risultati demo mostrati quì sò tutti da genomi publicati cù BMKGENE
1.L'analisi di l'evoluzione cuntene a custruzzione di l'arbulu filogeneticu, a struttura di a pupulazione è a PCA basatu nantu à variazioni genetiche.
L'arburu filogeneticu rapprisenta relazioni tassonomiche è evolutive trà e spezie cù antenati cumuni.
A PCA hà u scopu di visualizà a vicinanza trà e subpopulazioni.
A struttura di a pupulazione mostra a presenza di sub-populazione geneticamente distinta in termini di frequenze alleliche.
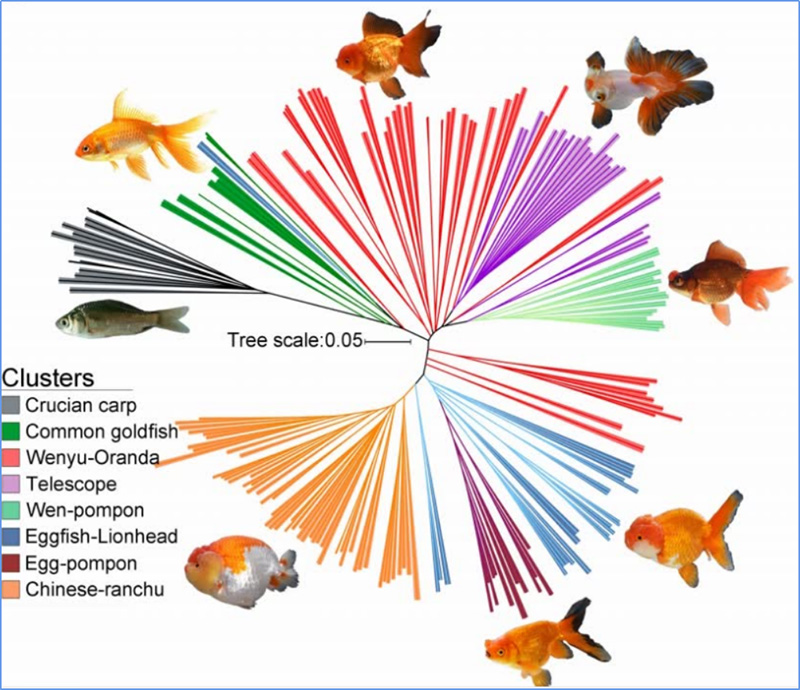
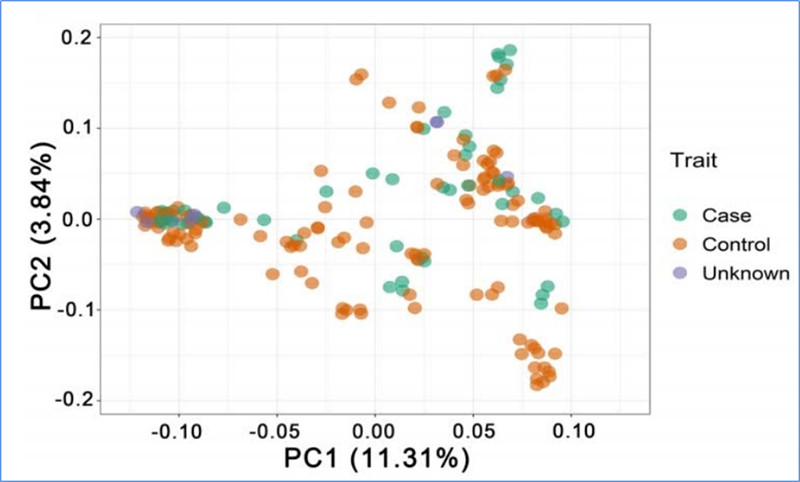
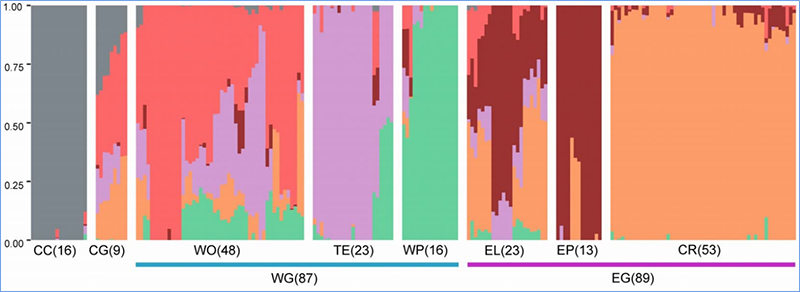
Chen, et.al.,PNAS, 2020
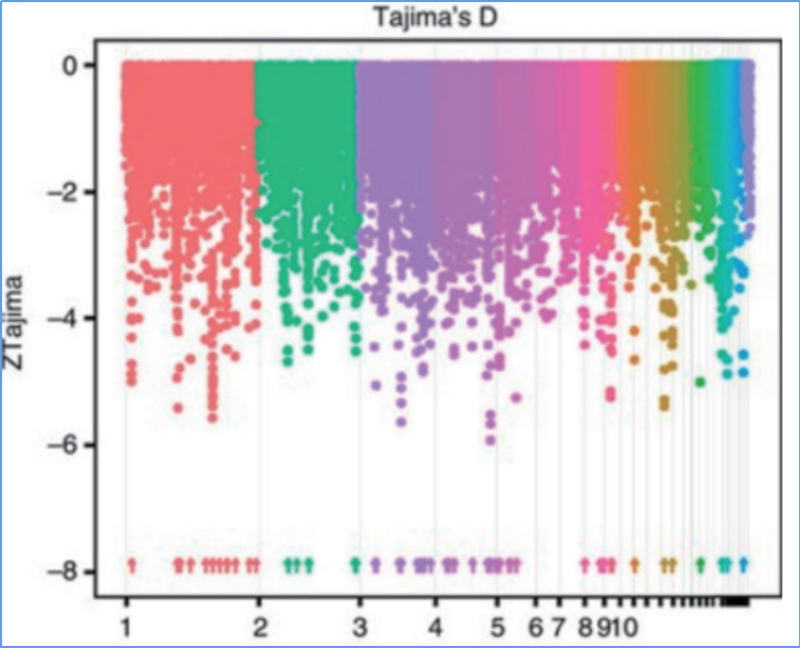
2.Spazza selettiva
Sweep selettivu si riferisce à un prucessu per quale un situ vantaghju hè sceltu è frequenze di siti neutrali ligati sò aumentati è quelli di siti unlinked sò diminuite, risultatu in a riduzzione di righjunali.
La détection à l'échelle du génome sur les régions de balayage sélectif est traitée en calculant l'indice génétique de population (π,Fst, D de Tajima) de tous les SNP dans une fenêtre glissante (100 Kb) à un certain pas (10 Kb).
Diversità di nucleotidi (π)
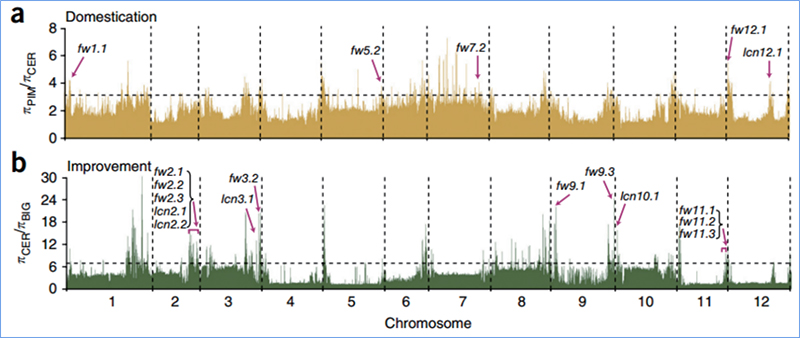
Tajima's D
Indice di fissazione (Fst)
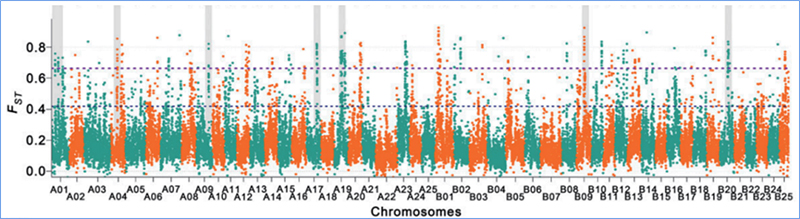
Wu, et.al.,Pianta Molecular, 2018
3.Gene Flow
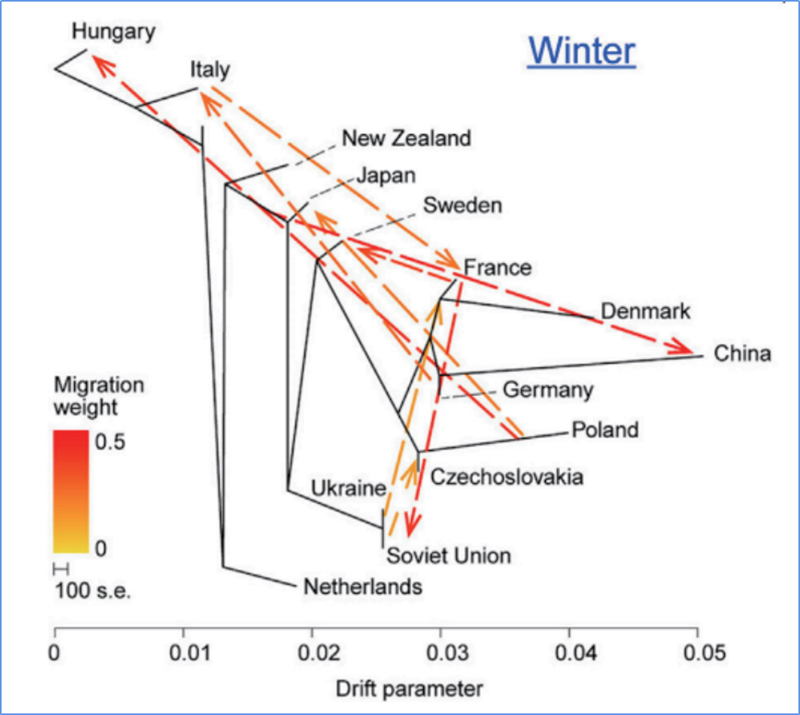
Wu, et.al.,Pianta Molecular, 2018
4.Storia demugrafica
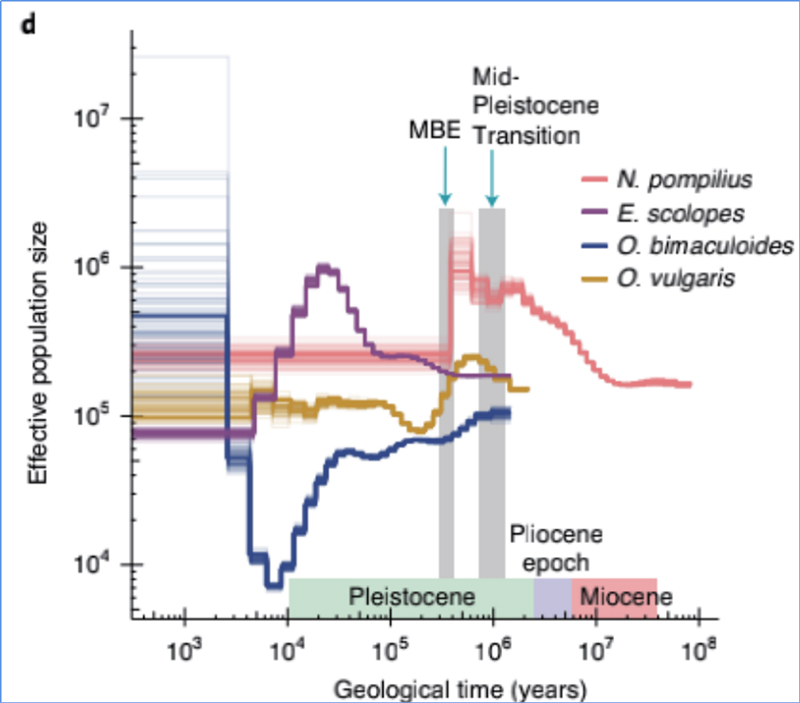
Zhang, et.al.,Ecologia di a natura è Evoluzione, 2021
5.Divergenza tempu
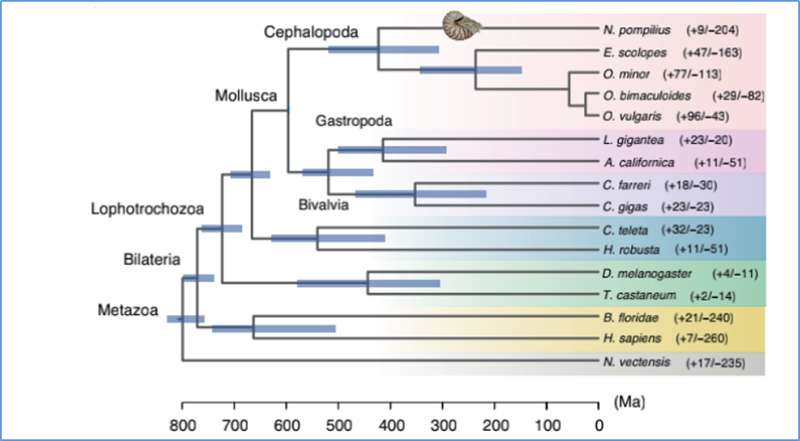
Zhang, et.al.,Ecologia di a natura è Evoluzione, 2021
Casu BMK
Una mappa di variazione genomica furnisce insights in a basa genetica di a selezzione di Spring Chinese Cabbage (Brassica rapa ssp. Pekinensis)
Publicatu: Pianta Molecular, 2018
Strategia di sequenza:
Resequencing: prufundità di sequenza: 10×
I risultati chjave
In questu studiu, 194 cabbages chinesi sò stati processati per re-sequencing cù una prufundità media di 10 ×, chì hà datu 1,208,499 SNP è 416,070 InDels.L'analisi filogenetiche nantu à sti 194 linii dimustranu chì sti linii ponu esse divisi in trè ecotipi, primavera, veranu è vaghjimu.Inoltre, a struttura di a pupulazione è l'analisi PCA indicanu chì a col chinesa di primavera hè stata urigginata da una col di vaghjimu in Shandong, Cina.Quessi sò stati successivamente intrudutti in Corea è u Giappone, cruciati cù e linee lucali è alcune varietà di bolting tardu di elli sò stati introdotti in Cina è infine sò diventati a col di primavera cinese.
U scanning genome-wide nantu à i colti cinesi di primavera è i colti di vaghjime nantu à a selezzione hà revelatu 23 lochi genomici chì anu passatu per una selezzione forte, dui di i quali sò stati sovrapposti cù a regione di cuntrollu di u tempu di bolting basatu in QTL-mapping.Sti dui rigioni sò stati truvati per cuntene geni chjave chì regulanu a fioritura, BrVIN3.1 è BrFLC1.Questi dui geni sò stati ancu cunfirmati per esse implicati in u tempu di bolting da u studiu di transcriptome è esperimenti transgenici.
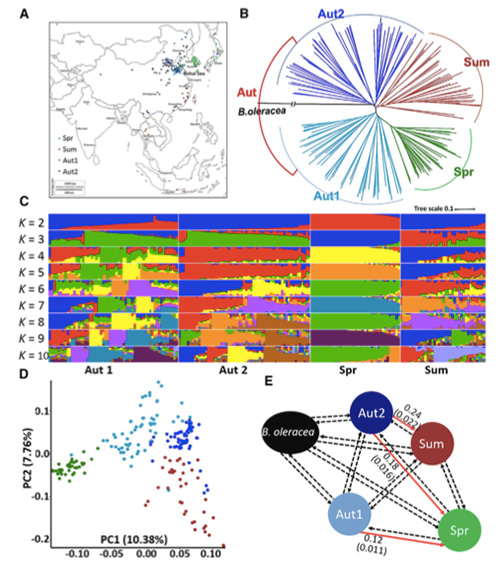 Analisi di a struttura di a pupulazione nantu à i colti chinesi | 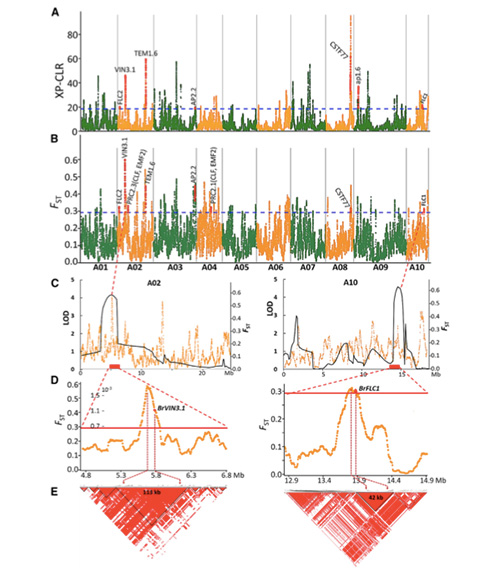 L'infurmazione genetica nantu à a selezzione di col cinese |
Tongbing, et al."Una mappa di variazione genomica furnisce insights nantu à a basa genetica di a selezzione di col cinese di primavera (Brassica rapa ssp.pekinensis)".Piante moleculari,11 (2018): 1360-1376.















