
Sequencing Genome De Novo Plant/Animal
Vantaghji di serviziu
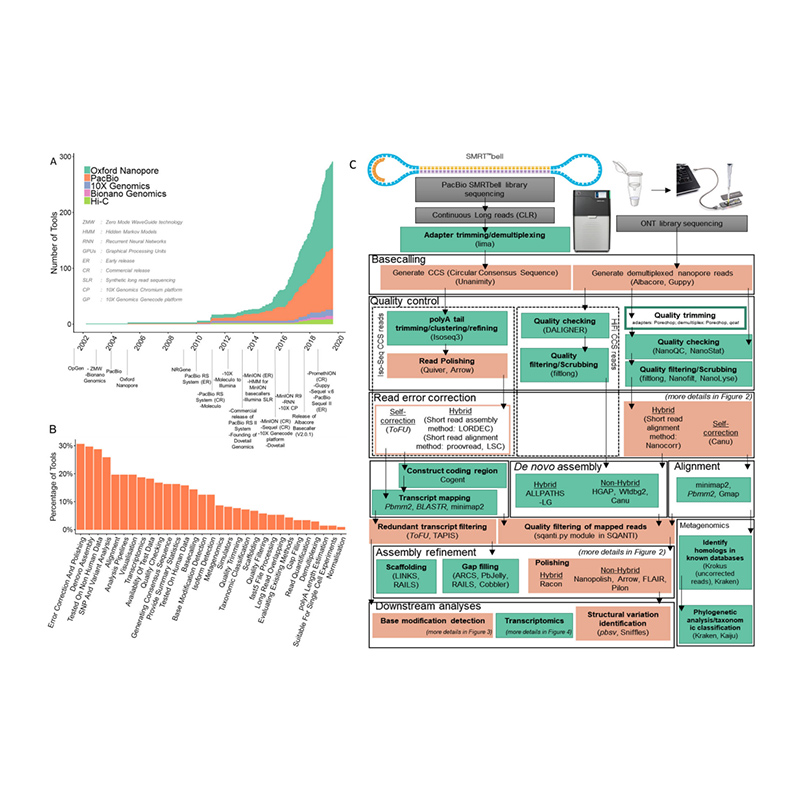
Sviluppu di piattaforme di sequenza è bioinformatica inde novoassemblea di genoma
(Amarasinghe SL et al.,Biologia di u genoma, 2020)
● Custruì genomi novi è migliurà i genomi di riferimentu esistenti per spezie d'interessu.
● A più alta precisione, continuità è cumpleta in l'assemblea
● Custruzzione di risorsa fundamentale per a ricerca in polimorfismu di sequenza, QTLs, edizione di geni, ripruduzzione, etc.
● Fornitu cù una gamma completa di piattaforme di sequenza di terza generazione: una soluzione di assemblea di genoma unicu.
● Strategie di sequenza è assemblea flessibili chì cumpienu diversi genomi cù caratteristiche diverse
● Squadra di bioinformatica altamente qualificata cù una grande sperienza in assemblee di genoma cumplessu, cumprese poliploidi, genomi giganti, etc.
● Più di 100 casi di successu cù un fattore d'impattu cumulativu publicatu di più di 900
● Turn-around-time cum'è 3 mesi per l'assemblea di genomu à livellu di cromusomu.
● Supportu tecnicu solidu cù una seria di brevetti è copyright di software in u latu sperimentale è bioinformatica.
Specificazioni di serviziu
|
Cuntinutu
|
Piattaforma
|
Lunghezza di lettura
|
Copertura
|
| Indagine di Genoma
| Illumina NovaSeq
| PE150
| ≥ 50X
|
| Sequencing Genome
| PacBio Revio
| 15 kb di lettura HiFi
| ≥ 30X
|
| Ciao-C
| Illumina NovaSeq
| PE150
| ≥100X
|
Flussu di travagliu

Requisiti di mostra è consegna
Requisiti di mostra:
| Spezie | Tissu | Per PacBio | Per Nanopore |
| Animali | Organi viscerali (fegato, spleen, etc.) | ≥ 1,0 g | ≥ 3,5 g |
| Musculu | ≥ 1,5 g | ≥ 5,0 g | |
| Sangue di mammiferi | ≥ 1,5 mL | ≥ 5,0 mL | |
| Sangue di pisci o d'acelli | ≥ 0,2 mL | ≥ 0,5 mL | |
| Piante | Foglie fresche | ≥ 1,5 g | ≥ 5,0 g |
| Petali o steli | ≥ 3,5 g | ≥ 10,0 g | |
| Radici o sementi | ≥ 7,0 g | ≥ 20,0 g | |
| Cellule | Culture cellulaire | ≥ 3×107 | ≥ 1×108 |
Cunsigliu Cunsigliu di Campione
Contenitore: Tubu da centrifuga da 2 ml (Un fogliu di stagno ùn hè micca cunsigliatu)
Per a maiò parte di i campioni, ricumandemu micca di priservà in etanolu.
Etichettatura di campioni: I campioni anu da esse chjaramente etichettati è identici à a forma d'infurmazione di mostra presentata.
Spedizione: Ghiaccio secco: I campioni anu da esse imballati in sacchetti prima è intarrati in ghiaccio seccu.
Flussu di travagliu di serviziu

Prughjettu di cuncepimentu

Consegna di mostra

estrazione di DNA

Custruzzione di biblioteca

Sequencing

Analisi di dati

Servizi post-vendita
* I risultati demo mostrati quì sò tutti da genomi publicati cù Biomarker Technologies
1.Circos nantu à assemblea di genomu cromusomu-livellu diG. rotundifoliumda a piattaforma di sequenza Nanopore
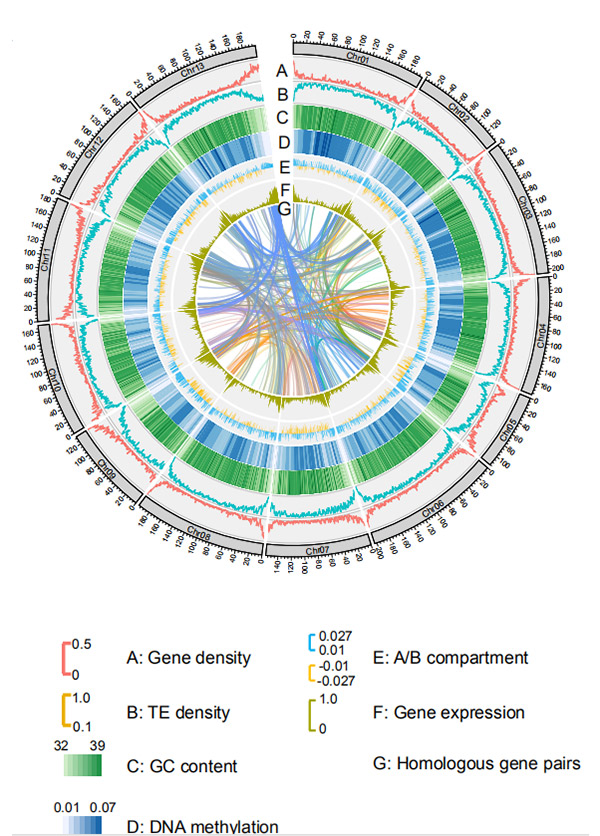
Wang M et al.,Biologia Molecular è Evoluzione, 2021
2.Statistiche di l'assemblea di u genoma di u segale di Weining è l'annotazione
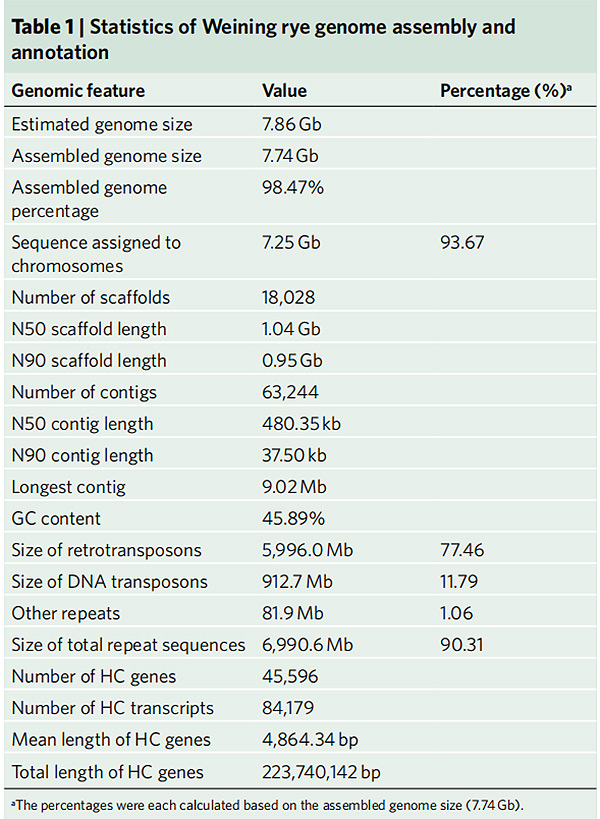
Li G et al.,Genetica di a natura, 2021
3.Gene prediction diSechium edulegenoma, derivata da trè metudi di predizione:De novopredizione, prediczione basata in omologia è predizione basata in dati RNA-Seq
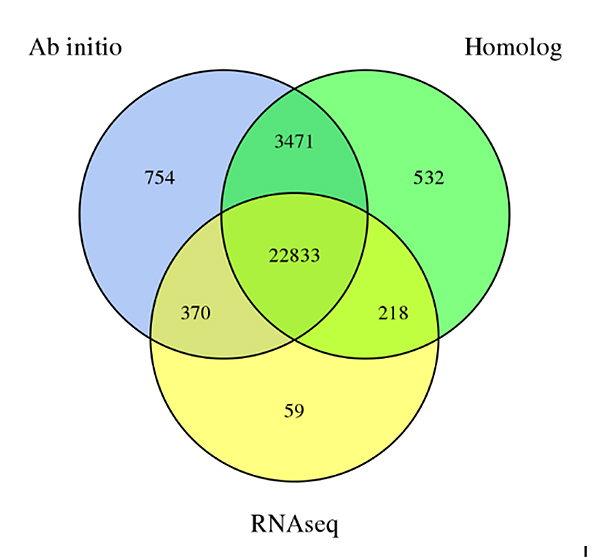
Fu A et al.,Ricerca Orticultura, 2021
4.Identificazione di ripetizioni terminali longu intactu in trè genomi di cuttuni
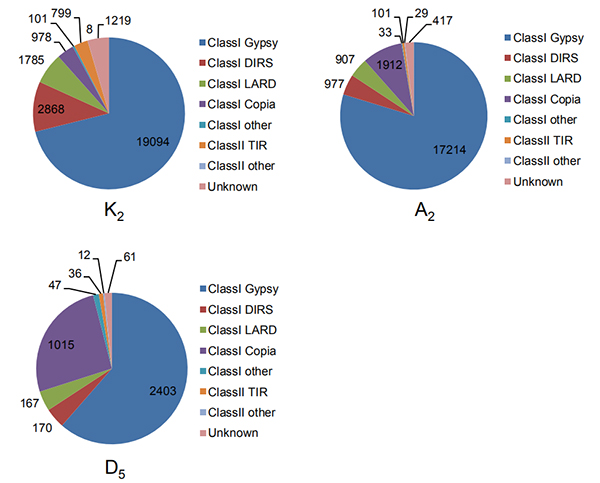
Wang M et al.,Biologia Molecular è Evoluzione, 2021
5.Hi-C heat map of theC. acuminatagenoma chì mostra interazzioni in tuttu u genoma.L'intensità di l'interazzione Hi-C hè proporzionale à a distanza lineare trà i contigs.Una linea dritta pulita nantu à sta mappa di calore indica un ancoramentu assai precisu di cuntighi nantu à i cromusomi.(Ratio di ancoraggio contig: 96,03%)
kang M et al.,cumunicazioni naturali,2021
Casu BMK
Un assemblea di genoma di alta qualità mette in risaltu e caratteristiche genomiche di segale è geni agronomichi impurtanti
Publicatu: Genetica di a natura, 2021
Strategia di sequenza:
Assemblea Genome: Modu PacBio CLR cù biblioteca di 20 kb (497 Gb, circa 63×)
Correzione di sequenza: NGS cù libreria di DNA di 270 bp (430 Gb, circa 54×) nantu à a piattaforma Illumina
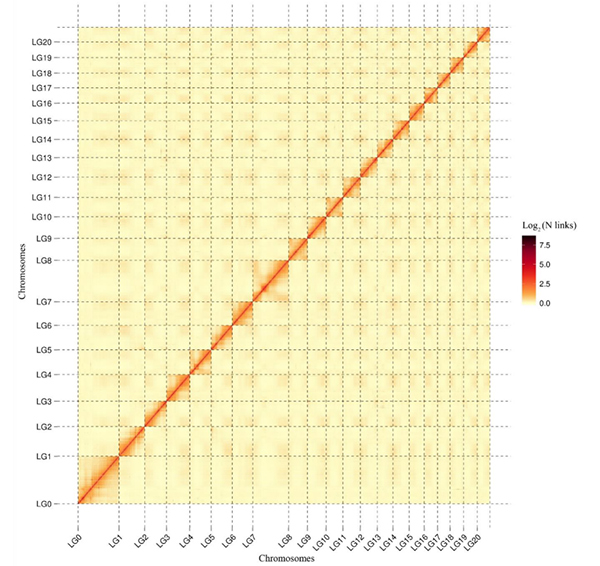
Ancoraggio di Contigs: libreria Hi-C (560 Gb, circa 71×) su piattaforma Illumina
Mappa ottica: (779,55 Gb, circa 99×) su Bionano Irys
I risultati chjave
1.Una assemblea di u genoma di u segale di Weining hè stata publicata cù a dimensione di u genoma tutale di 7,74 Gb (98,74% di a dimensione di u genoma stimatu per citometria di flussu).Scaffold N50 di questa assemblea hà righjuntu 1.04 Gb.U 93,67% di i contigs sò stati ancorati bè in 7 pseudo-cromusomi.Questa assemblea hè stata evaluata da a mappa di ligame, LAI è BUSCO, chì hà risultatu in puntuazioni elevate in tutte e valutazioni.
Studi 2.Further nantu à a genomica comparativa, a mappa di ligame geneticu, i studii di transcriptomica sò stati realizati nantu à a basa di stu genoma.Una seria di caratteristiche genomiche sò state revelate, cumprese duplicazioni di geni in tuttu u genoma è u so impattu nantu à i geni di biosintesi di amido;l'urganizazione fisica di i lochi di prolamin cumplessi, e caratteristiche di l'espressione genica sottumessi à u trattu di l'intestazione iniziale è e regioni cromosomiali è i loci assuciati à a domesticazione putativa in a segale.
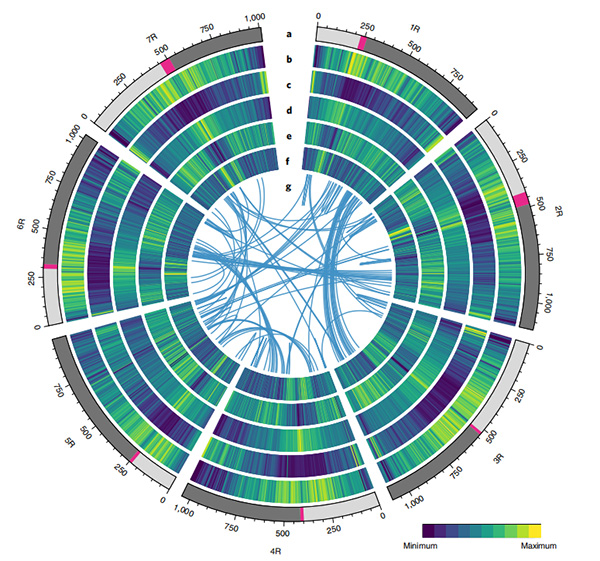 Diagramma di Circos nantu à e caratteristiche genomiche di u genoma di u segale di Weining | 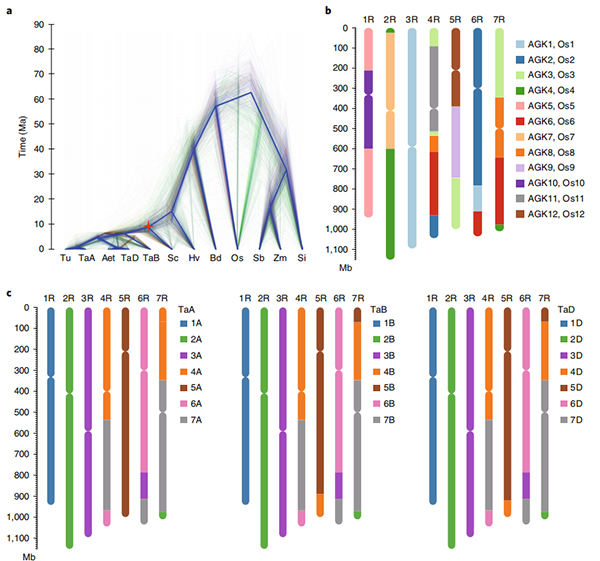 Analisi di sintesi evolutiva è cromusomica di u genoma di segale |
Li, G., Wang, L., Yang, J.et al.Un assemblea di genomu di alta qualità mette in risaltu e caratteristiche genomiche di segale è i geni agronomichi impurtanti.Nat Genet 53,574–584 (2021).
https://doi.org/10.1038/s41588-021-00808-z










