Sequenza di mRNA-Illumina basata senza riferimentu
Features
● Indipendente da ogni genoma di riferimentu,
● I dati puderanu esse utilizati per analizà a struttura è l'espressione di e trascrizioni
● Identificà siti di clipping variàbbili
Vantaghji di serviziu
● Consegna di risultati basati in BMKCloud: I risultati sò furniti cum'è un schedariu di dati è un rapportu interattivu via a piattaforma BMKCloud, chì permette una lettura amichevule di l'output di l'analisi cumplessu è l'estrazione di dati persunalizata nantu à a basa di l'analisi bioinformatica standard.
● Servizii dopu à a vendita: i servizii dopu à a vendita sò validi per 3 mesi dopu à a fine di u prughjettu, cumpresi u seguitu di i prughjetti, a risoluzione di i prublemi, i risultati Q&A, etc.
Requisiti di mostra è consegna
Requisiti di mostra:
Nucleotidi:
| Conc. (ng/μl) | Quantità (μg) | Purità | Integrità |
| ≥ 20 | ≥ 0,5 | OD260/280 = 1,7-2,5 OD260/230 = 0,5-2,5 Cuntaminazione limitata o micca di proteine o DNA mostrata nantu à u gel. | Per i pianti: RIN≥6.5; Per l'animali: RIN≥7.0; 5.0≥28S/18S≥1.0; limitazione o senza elevazione di basa |
Tissu: Pesu (secu): ≥1 g
* Per i tissuti più chjuchi di 5 mg, ricumandemu di mandà un campione di tissutu congelatu (in nitrogenu liquidu).
Suspension cellula: Conte di cellula = 3 × 107
* Hè cunsigliatu di spedite lisatu di cellule congelate.In casu chì a cellula conta più chjuca di 5 × 105, Flash congelatu in nitrogenu liquidu hè cunsigliatu.
Campioni di sangue:
PA×geneBloodRNATube;
6 mLTRIzol è 2 mL di sangue (TRIzol: Sangue = 3:1)
Cunsigliu Cunsigliu di Campione
Container:
Tubu da centrifuga da 2 ml (sconsigliatu u fogliu di stagno)
Esempiu di etichettatura: Gruppu + replicate per esempiu A1, A2, A3;B1, B2, B3....
spedizione:
1.Dry-ice: Samples deve esse imballatu in sacchetti è intarratu in seccu-ghiacciu.
2. Tubi RNAstable: i campioni di RNA ponu esse secchi in un tubu di stabilizazione di RNA (per esempiu RNAstable®) è spediti in a temperatura di l'ambienti.
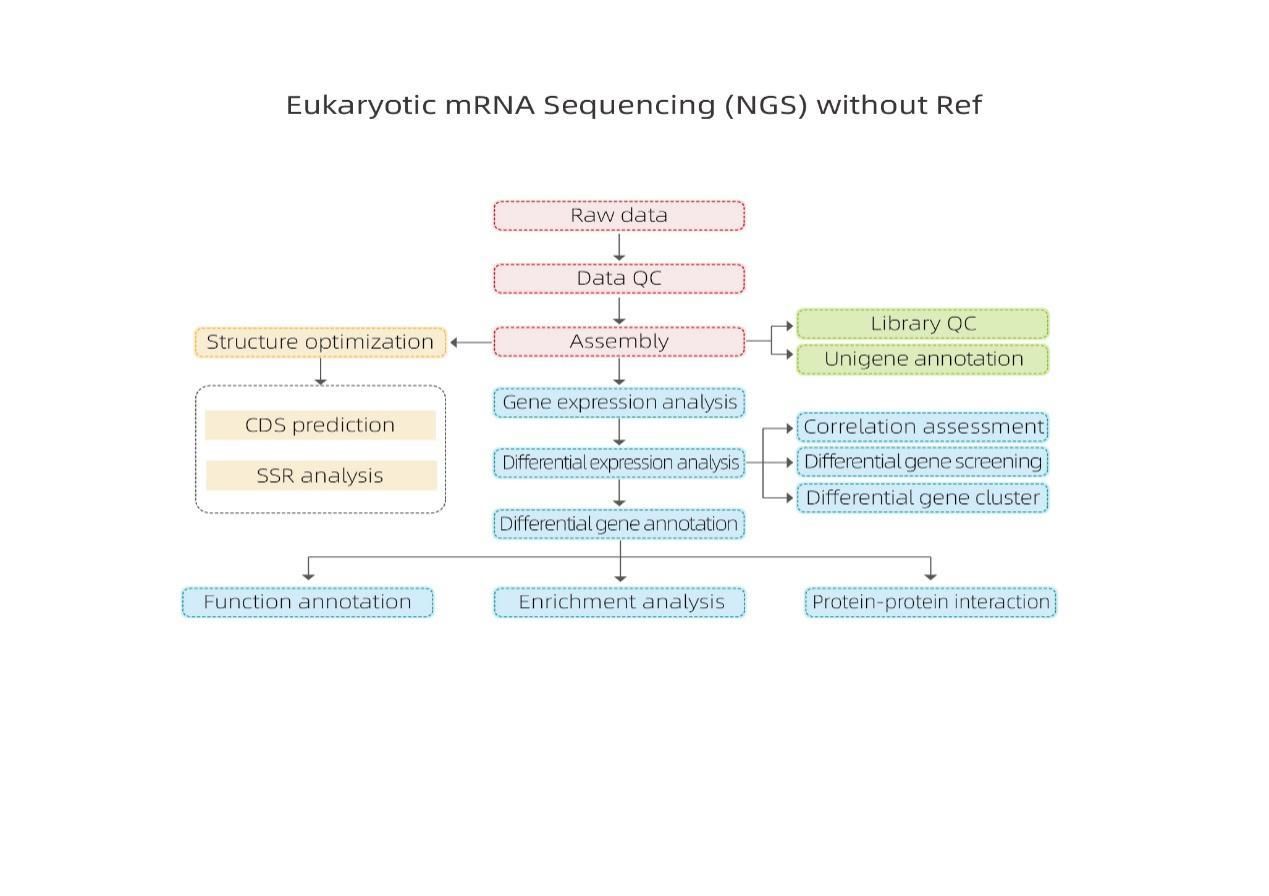
Flussu di travagliu di serviziu

Prughjettu di cuncepimentu

Consegna di mostra

estrazione di RNA

Custruzzione di biblioteca

Sequencing

Analisi di dati

Servizi post-vendita
Bioinformatica
1.mRNA (denovo) Principiu di Assemblea
Per Trinity, i leghje sò frammentati in pezzi più chjuchi, cunnisciuti cum'è K-mer.Questi K-mers sò allora usati cum'è sementi per esse allargati in contigs è dopu cumpunenti basati nantu à sovrapposizioni contig.Infine, De Bruijn hè stata applicata quì per ricunnosce e trascrizioni in i cumpunenti.
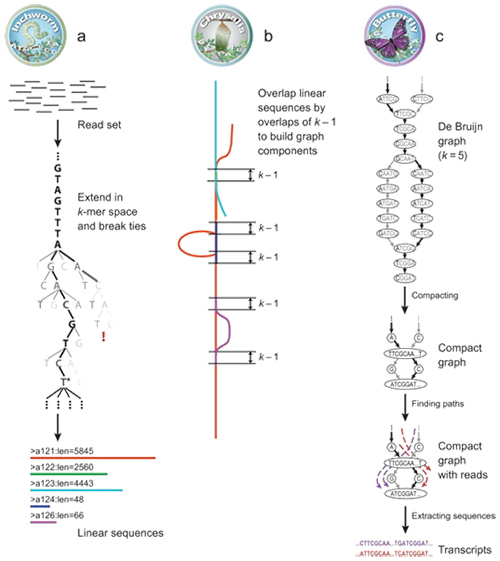
mRNA (De novo) Panoramica di Trinità
2.mRNA (De novo) Distribution of Gene Expression Level
RNA-Seq hè capaci di ottene una stima altamente sensitiva di l'espressione genica.Normalmente, a gamma detectable di l'espressione di trascrizioni FPKM varia da 10^-2 à 10^6
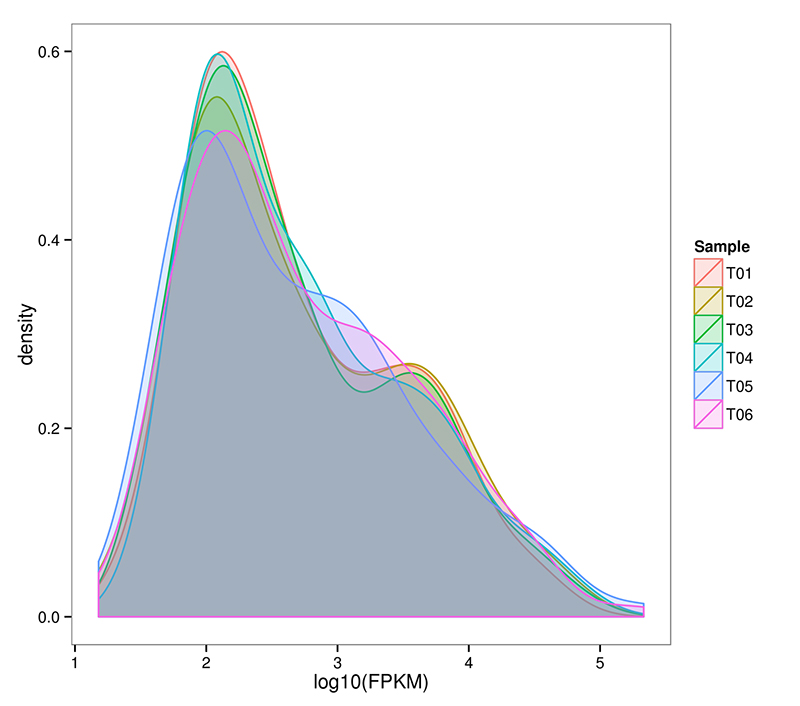
mRNA (De novo) Distribuzione di densità FPKM in ogni campione
3.mRNA (De novo) GO Analisi di arricchimentu di DEG
A basa di dati GO (Gene Ontology) hè un sistema di annotazione biologica strutturata chì cuntene un vocabulariu standard di funzioni di geni è prudutti di geni.Contene parechji livelli, induve u più bassu hè u livellu, più specifiche sò e funzioni.
mRNA (De novo) classificazione GO di DEG à u sicondu livellu
Casu BMK
Analisi di u Transcriptome di u Metabolismu di Saccarosi durante l'inflamazione di u bulbe è u sviluppu in a cipolla (Allium cepa L.)
Publicatu: frontiere in a scienza vegetale, 2016
Strategia di sequenza
Illumina HiSeq2500
Raccolta di campioni
U cultivar Utah Yellow Sweet Spain "Y1351" hè statu usatu in stu studiu.U numeru di campioni raccolti era
15esimu ghjornu dopu l'inflazione (DAS) di bulbe (2-cm di diametru è 3-4 g di pesu), 30th DAS (5-cm diametru è 100-110 g di pesu), è ~ 3 in u 40th DAS (7-cm di diametru è 260-300 grammi).
I risultati chjave
1. in u diagramma di Venn, un totale di 146 DEG sò stati rilevati in tutti i trè coppie di stadi di sviluppu.
2. "Trasportu di carbuidrati è metabolismu" hè statu rapprisintatu da solu 585 unigenes (ie, 7% di u COG annotatu).
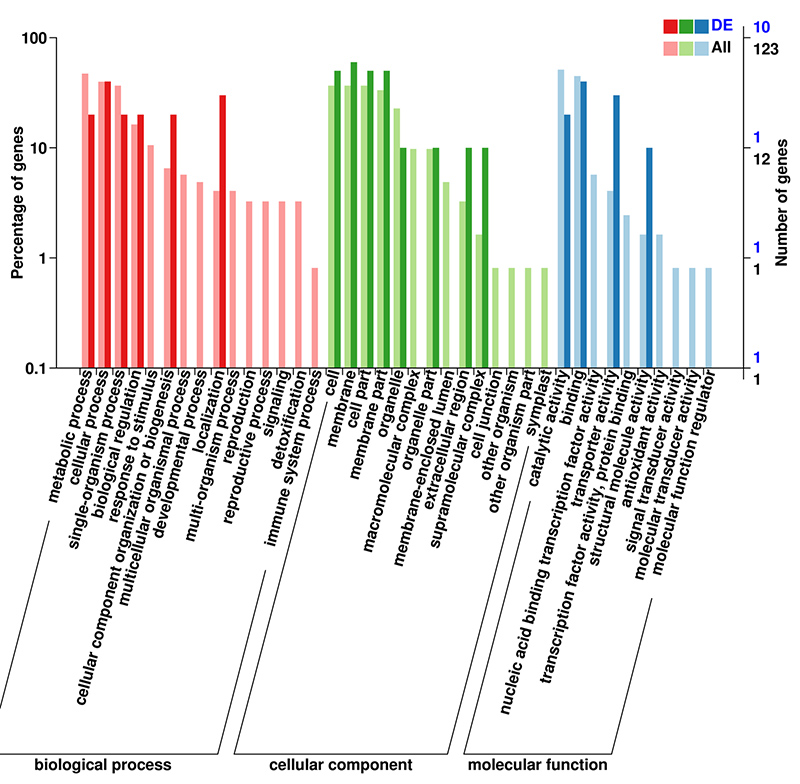
3.Unigenes annotati cù successu à a basa di dati GO sò stati classificati in trè categurie principali per i trè fasi diffirenti di u sviluppu di bulbe.A più rapprisentata in a categuria principale di "processu biologicu" era "processu metabolicu", seguita da "processu cellulare".In a categuria principale di "funzione moleculare" e duie categurie più rapprisintate eranu "ligatu" è "attività catalitica".
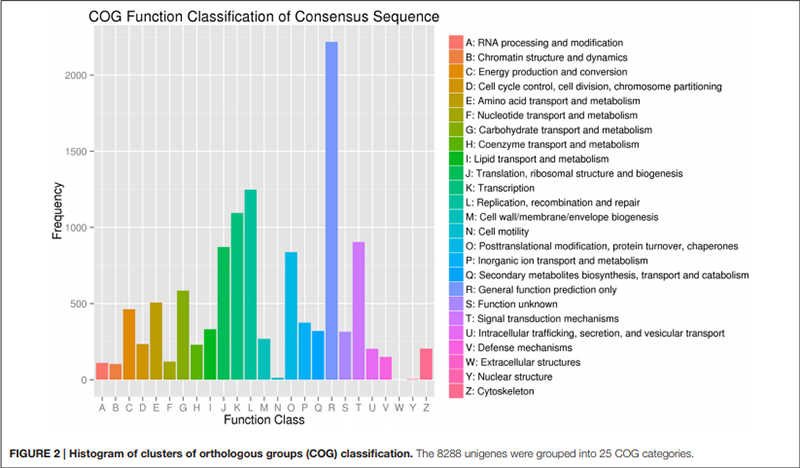 Istogramma di classificazione di gruppi di gruppi ortologhi (COG). | 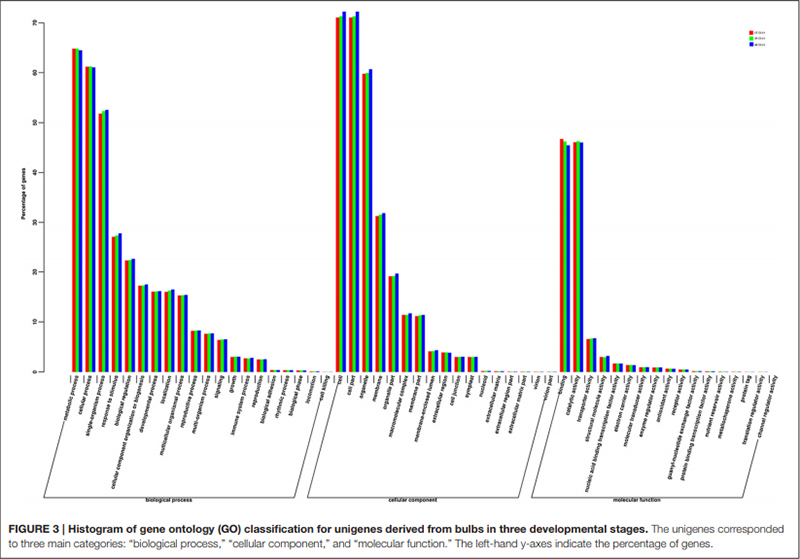 Istogramma di classificazione di l'ontologia genica (GO) per unigeni derivati da bulbi in trè fasi di sviluppu |
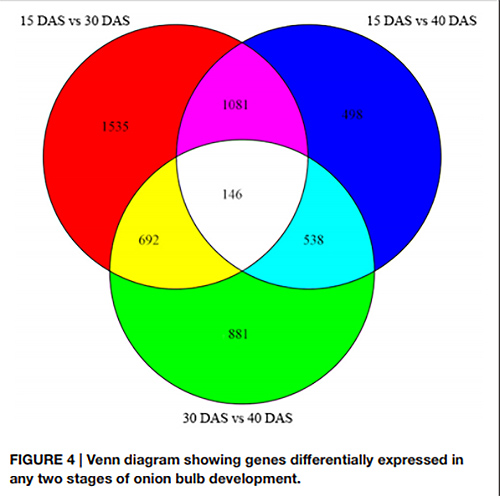 Diagramma di Venn chì mostra i geni espressi di manera sfarente in ogni dui tappe di u sviluppu di u bulbe di cipolla |
Riferimentu
Zhang C, Zhang H, Zhan Z, et al.Analisi di Transcriptome di u Metabolismu di Saccarosi durante l'Inflazione è u Sviluppu di Bulb in Cipolla (Allium cepa L.) [J].Frontiers in Plant Science, 2016, 7: 1425-.DOI: 10.3389/fpls.2016.01425