Sequenza di bisulfite à rappresentazione ridotta (RRBS)
Specificazioni di serviziu
Piattaforma: piattaforma NovaSeq, PE150
Tipu di libreria: 200-400bp inserisci libreria di DNA trattata con bisulfite
Strategia di sequenza: Paired-End 150 bp
Consiglia l'output di dati: 10 Gb di dati grezzi/campione
Requisiti di mostra
Quantità di DNA: ≥ 2 ug
Cuncentrazione di DNA: ≥ 20 ng/μl.
Purezza: OD260/280 = 1,8 à 2,0 senza degradazione o contaminazione da RNA
Analisi bioinformatica
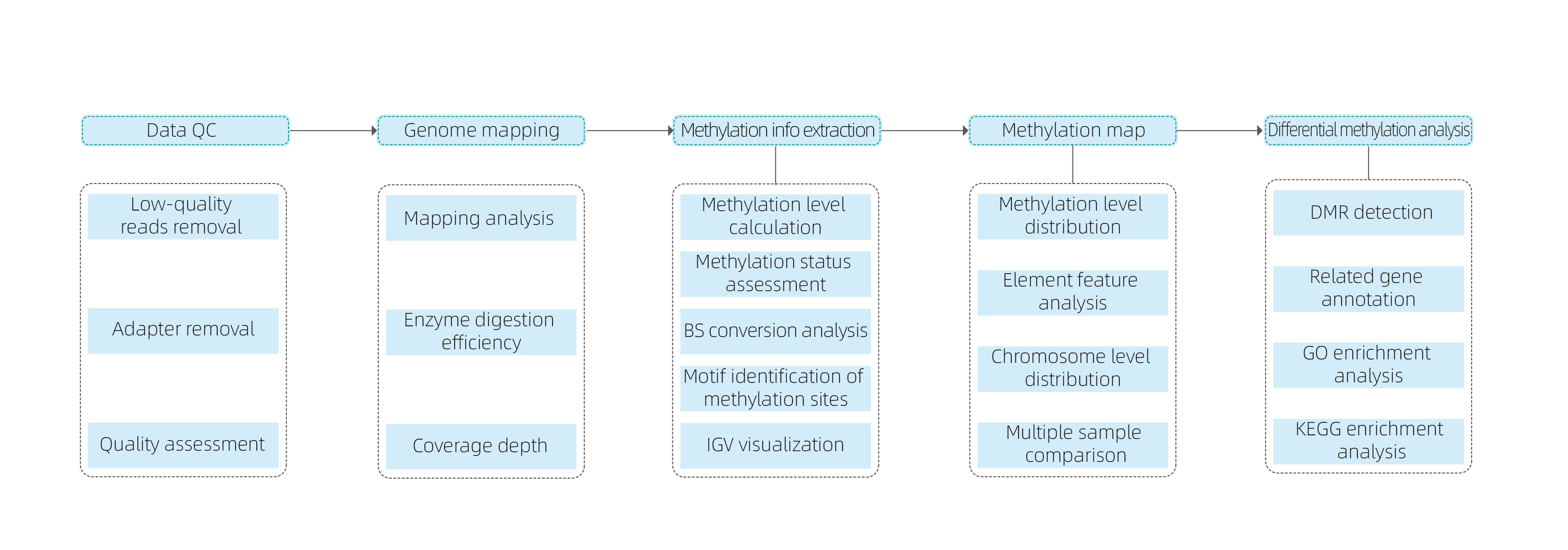
Flussu di travagliu di serviziu

Consegna di mostra

Custruzzione di biblioteca

Sequencing

Analisi di dati
Servizi post-vendita
a.Statistiche di allineamentu di u genoma di riferimentu
Statistiche di lettura di carte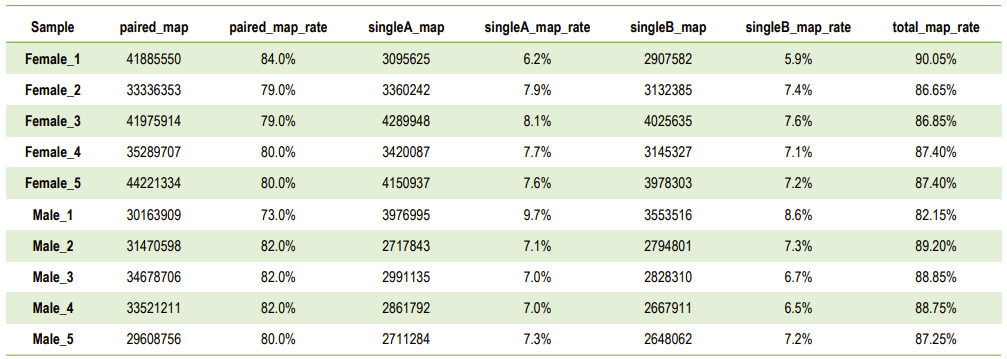
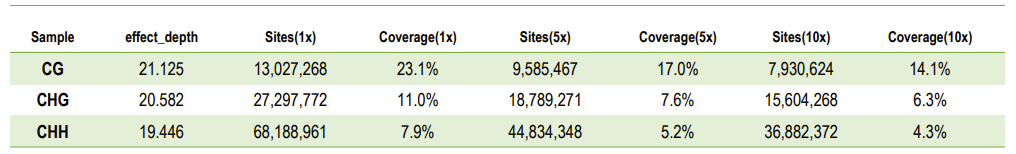
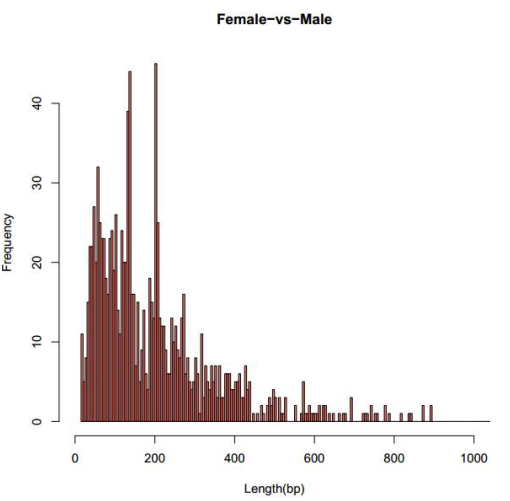
Statistics di a prufundità di sequenza è a cobertura di u situ C
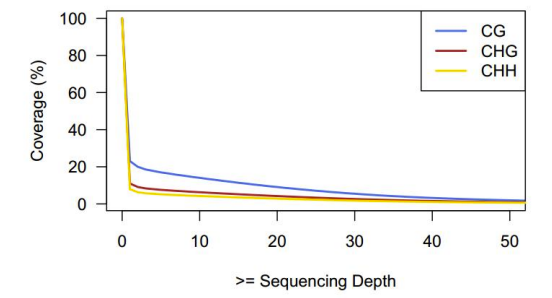
Acopertura accumulata
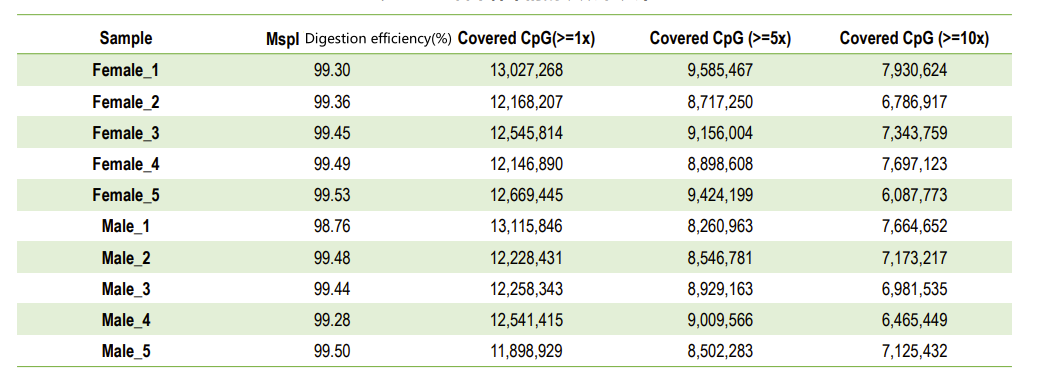
Defficienza di igestioni di ogni mostra
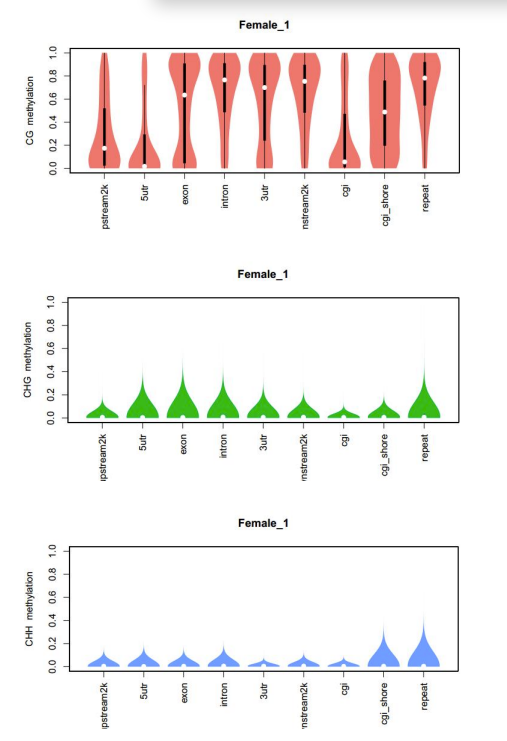
b.Rilevazione di u situ di metilazione
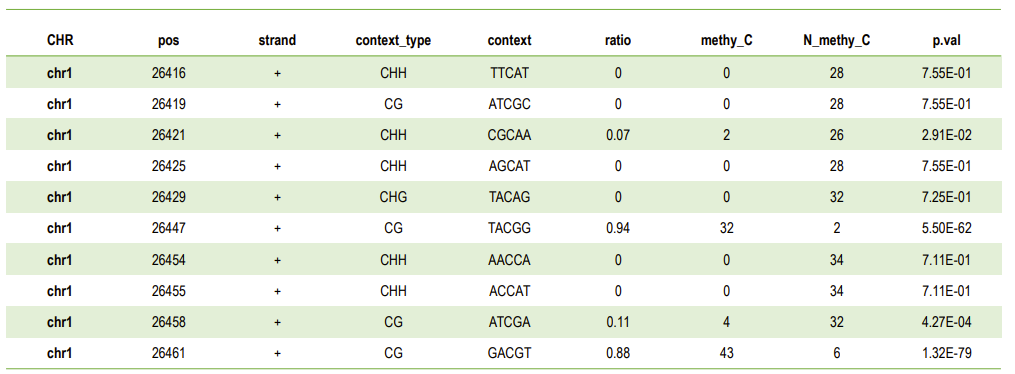
Lista di i livelli di metilazione in u situ C
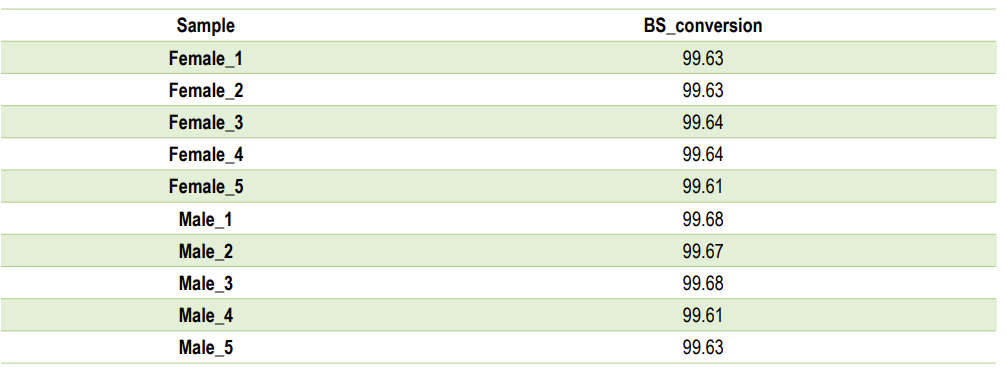
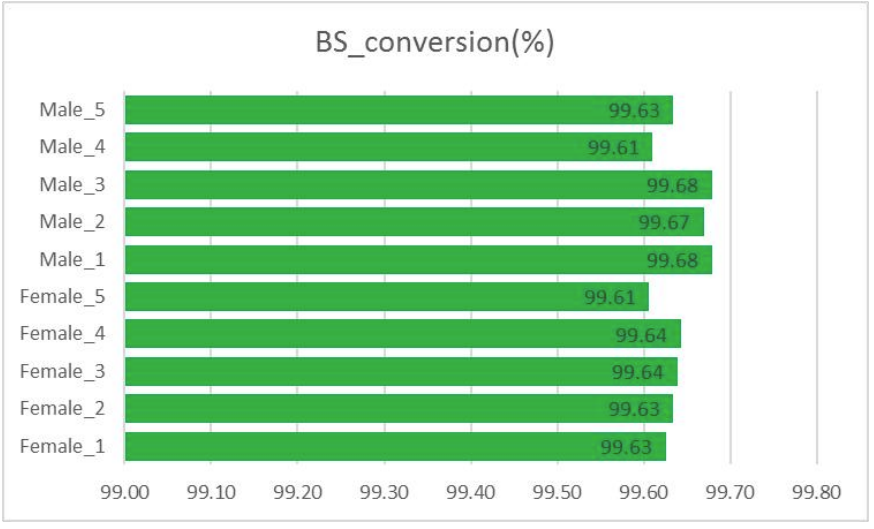
BS cunversione
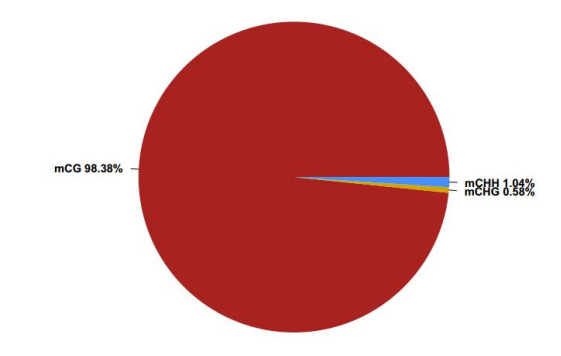
Distribuzione di u nivellu di metilazione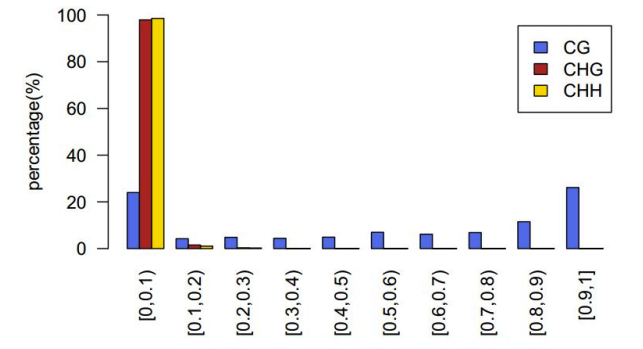
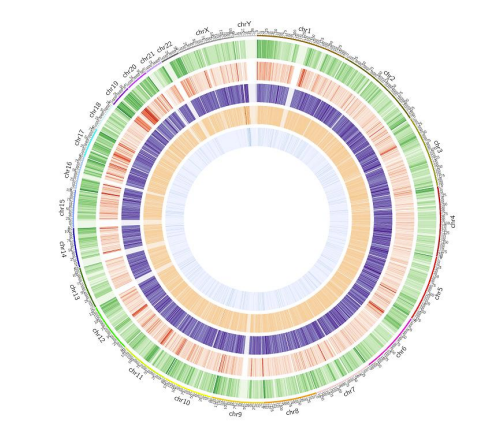
c.Mappa di metilazione
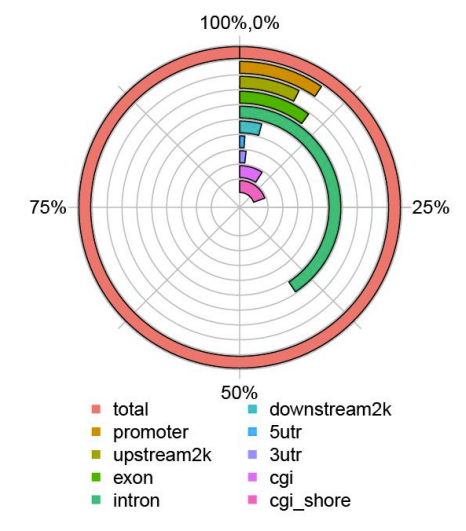
Gl'elementu enome
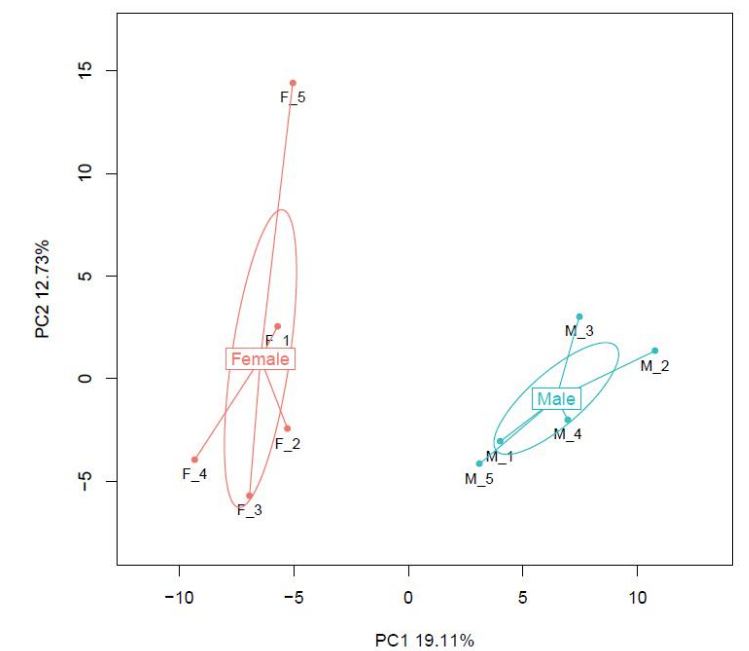
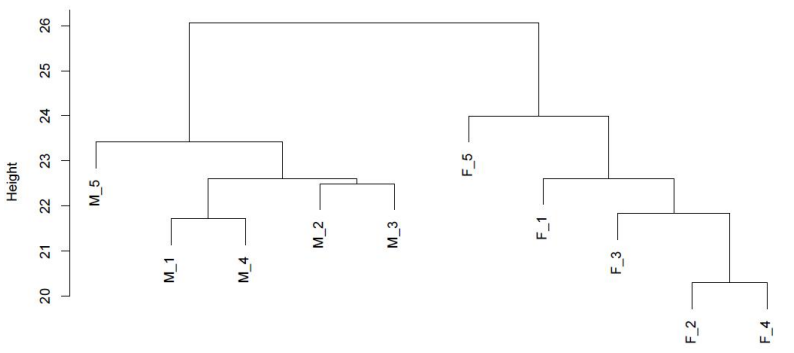
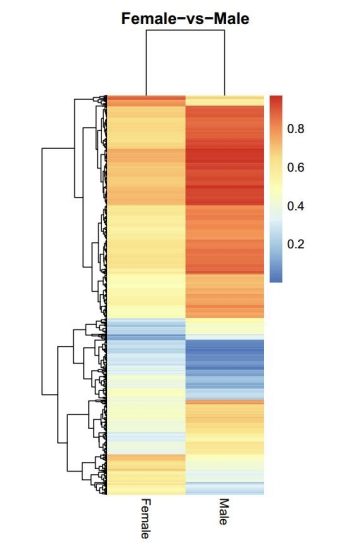
d.Comparazione di i livelli di metilazione trà i campioni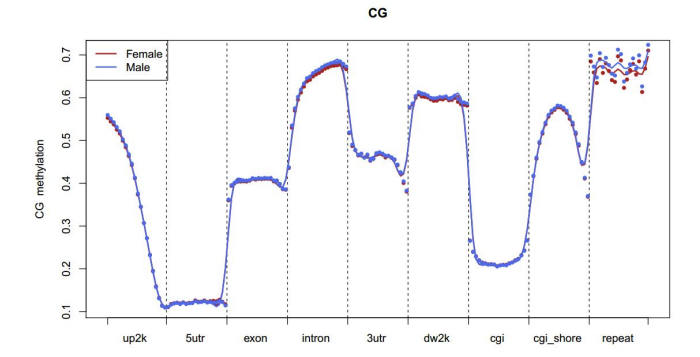
PAirwise Correlation di metilazione CG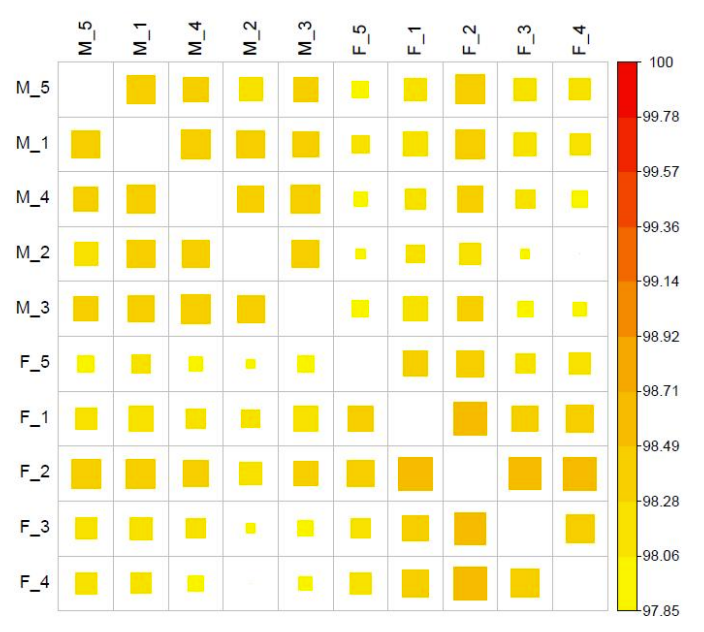
d.Analisi di metilazione differenziale
Sstatistiche di DMR