
Evoluční genetika
Výhody služby
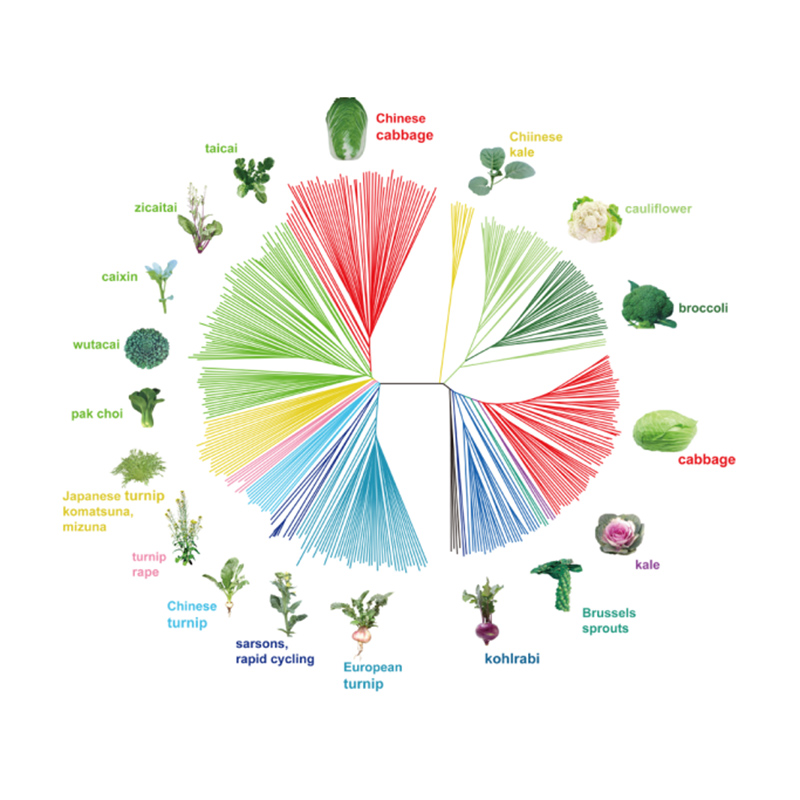
Takagi a spol.,Rostlinný deník, 2013
● Odhad času a rychlosti druhové divergence na základě variací na úrovni nukleotidů a aminokyselin
● Odhalení spolehlivějších fylogenetických vztahů mezi druhy s minimalizovaným vlivem konvergentní evoluce a paralelní evoluce
● Vytváření vazeb mezi genetickými změnami a fenotypy za účelem odhalení genů souvisejících s vlastnostmi
● Odhad genetické diverzity, která odráží evoluční potenciál druhů
● Rychlejší doba obratu
● Rozsáhlé zkušenosti: BMK za více než 12 let nashromáždila rozsáhlé zkušenosti s populačními a evolučními projekty, které pokrývají stovky druhů atd., a podílely se na více než 80 projektech na vysoké úrovni publikovaných v Nature Communications, Molecular Plants, Plant Biotechnology Journal atd.
Specifikace služby
Materiály:
Normálně se doporučují alespoň tři subpopulace (např. poddruhy nebo kmeny).Každá subpopulace by neměla obsahovat méně než 10 jedinců (Rostliny >15, u vzácných druhů lze snížit).
Strategie sekvenování:
* WGS lze použít pro druhy s vysoce kvalitním referenčním genomem, zatímco SLAF-Seq je použitelný pro druhy s referenčním genomem nebo bez něj nebo pro referenční genom nízké kvality.
| Platí pro velikost genomu | WGS | Štítky SLAF (×10 000) |
| ≤ 500 Mb | 10×/jednotlivec | Doporučuje se spíše WGS |
| 500 Mb – 1 Gb | 10 | |
| 1 Gb – 2 Gb | 20 | |
| ≥2 Gb | 30 |
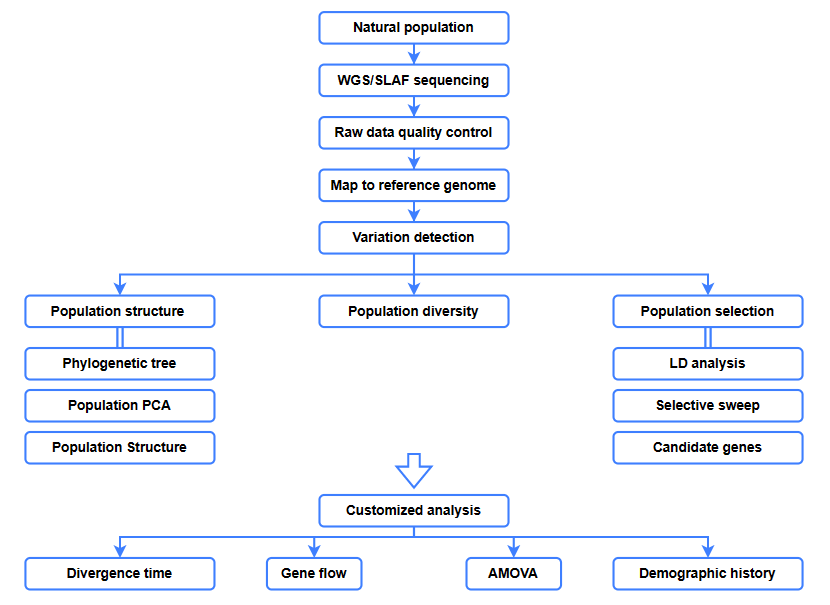
Bioinformatické analýzy
● Evoluční analýza
● Selektivní rozmítání
● Tok genů
● Demografická historie
● Čas divergence
Vzorové požadavky a dodání
Vzorové požadavky:
| Druh | Tkáň | WGS-NGS | SLAF |
| Zvíře
| Viscerální tkáň |
0,5~1g
|
0,5 g
|
| Svalová tkáň | |||
| Savčí krev | 1,5 ml
| 1,5 ml
| |
| Krev drůbeže/rybí | |||
| Rostlina
| Čerstvý list | 1~2g | 0,5~1g |
| Okvětní lístek/stonek | |||
| Kořen/semeno | |||
| Buňky | Kultivovaná buňka |
| gDNA | Koncentrace | Množství (ug) | OD260/OD280 |
| SLAF | ≥35 | ≥1,6 | 1,6-2,5 |
| WGS-NGS | ≥1 | ≥0,1 | - |
Tok servisní práce

Návrh experimentu

Vzorová dodávka

Stavba knihovny

Sekvenování

Analýza dat

Poprodejní služby
*Zde uvedené ukázkové výsledky jsou všechny z genomů publikovaných s BMKGENE
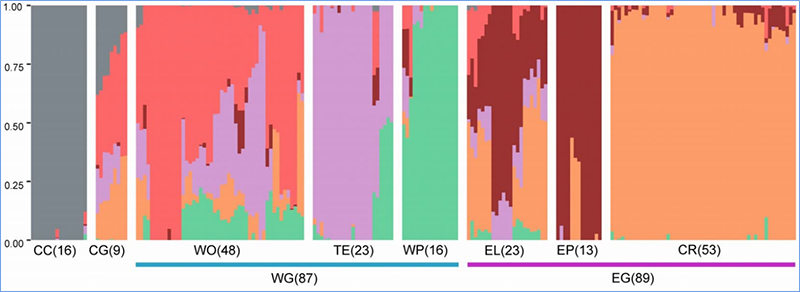
1.Evoluční analýza obsahuje konstrukci fylogenetického stromu, populační struktury a PCA na základě genetických variací.
Fylogenetický strom představuje taxonomické a evoluční vztahy mezi druhy se společným předkem.
PCA si klade za cíl vizualizovat blízkost mezi subpopulacemi.
Struktura populace ukazuje přítomnost geneticky odlišné subpopulace, pokud jde o frekvence alel.
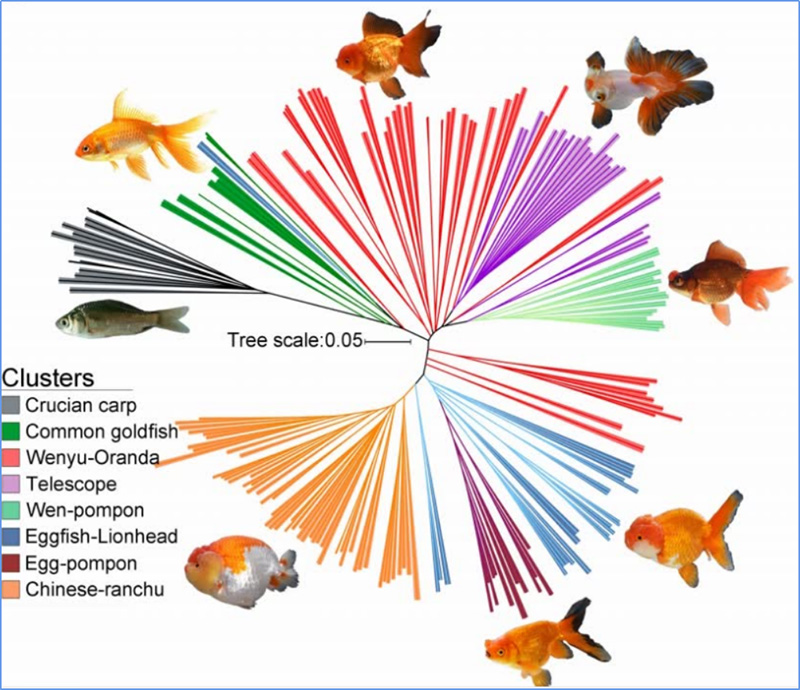
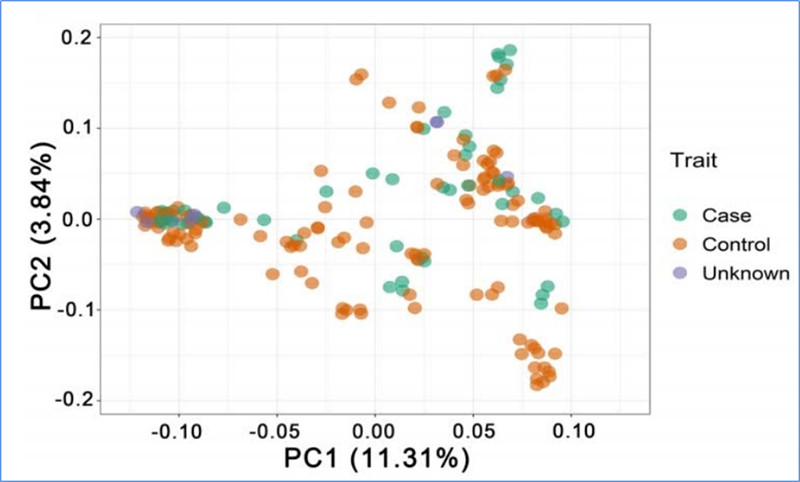
Chen, et.spol.,PNAS, 2020
2.Selektivní zametání
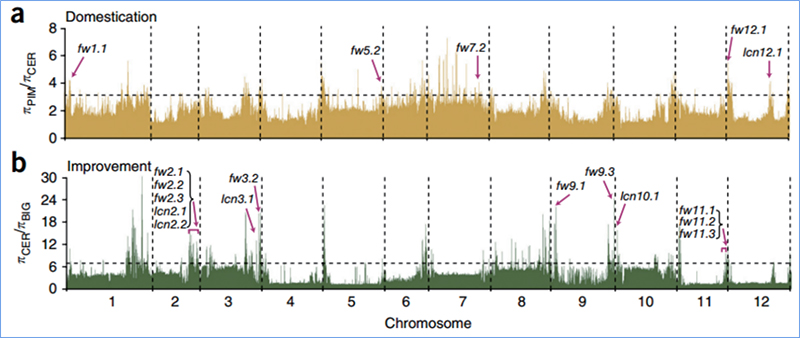
Selektivní rozmítání se týká procesu, kterým je vybráno výhodné místo a frekvence spojených neutrálních míst jsou zvýšeny a frekvence nepropojených míst jsou sníženy, což vede ke snížení regionálních.
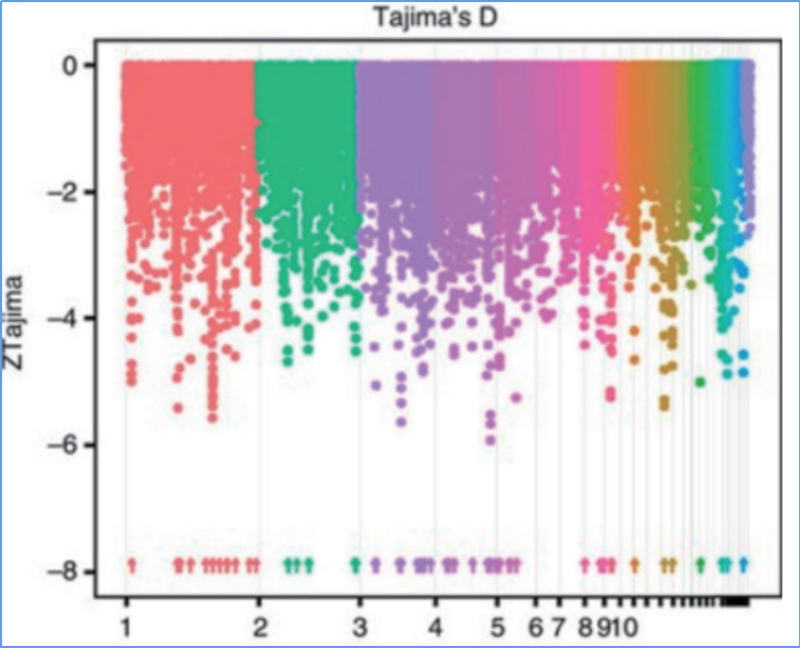
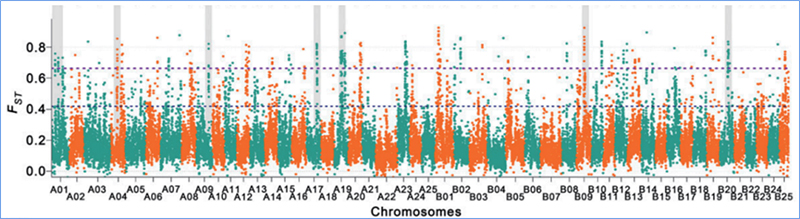
Detekce v celém genomu na selektivních zametacích oblastech je zpracována výpočtem populačního genetického indexu (π,Fst, Tajima's D) všech SNP v posuvném okně (100 Kb) v určitém kroku (10 Kb).
Nukleotidová diverzita (π)
Tajima D
Fixační index (Fst)
Wu, et.spol.,Molekulární rostlina, 2018
3. Tok genů
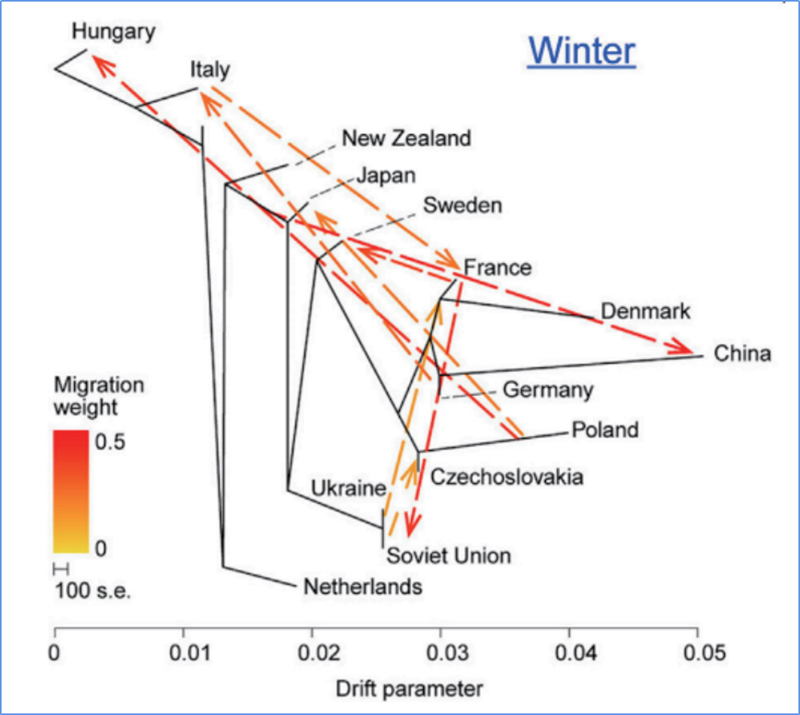
Wu, et.spol.,Molekulární rostlina, 2018
4.Demografická historie
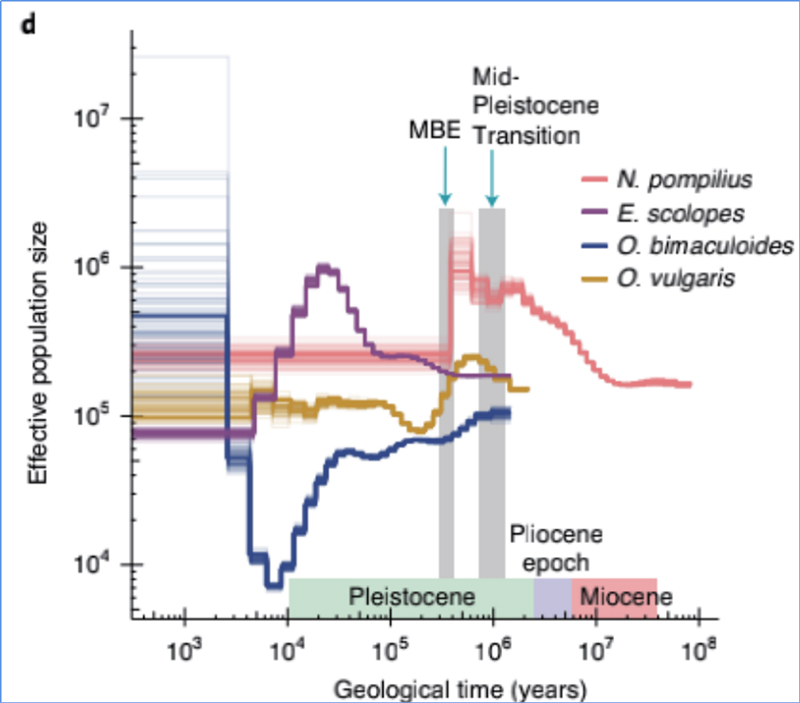
Zhang, et.spol.,Ekologie a evoluce přírody, 2021
5. Čas divergence
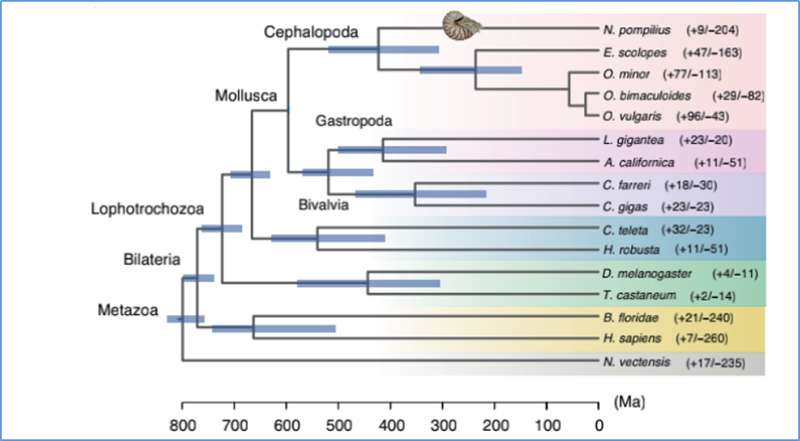
Zhang, et.spol.,Ekologie a evoluce přírody, 2021
Pouzdro BMK
Mapa genomových variací poskytuje pohled na genetický základ výběru jarního čínského zelí (Brassica rapa ssp. Pekinensis)
Publikováno: Molekulární rostlina, 2018
Strategie sekvenování:
Resekvenování: hloubka sekvenování: 10×
Klíčové výsledky
V této studii bylo zpracováno 194 čínského zelí pro opětovné sekvenování s průměrnou hloubkou 10×, což poskytlo 1 208 499 SNP a 416 070 InDels.Fylogenetická analýza těchto 194 linií ukázala, že tyto linie lze rozdělit do tří ekotypů, jarní, letní a podzimní.Navíc populační struktura a analýza PCA ukázaly, že jarní čínské zelí pochází z podzimního zelí v Shandongu v Číně.Ty byly následně zavlečeny do Koreje a Japonska, zkříženy s místními liniemi a některé z nich pozdní odrůdy byly zavlečeny zpět do Číny a nakonec se z nich stalo jarní čínské zelí.
Skenování celého genomu jarního čínského zelí a podzimního zelí při selekci odhalilo 23 genomových lokusů, které prošly silnou selekcí, z nichž dva se překrývaly s oblastí kontroly času šroubování na základě mapování QTL.Bylo zjištěno, že tyto dvě oblasti obsahují klíčové geny, které regulují kvetení, BrVIN3.1 a BrFLC1.Studií transkriptomu a transgenními experimenty bylo dále potvrzeno, že se tyto dva geny podílejí na čase roubování.
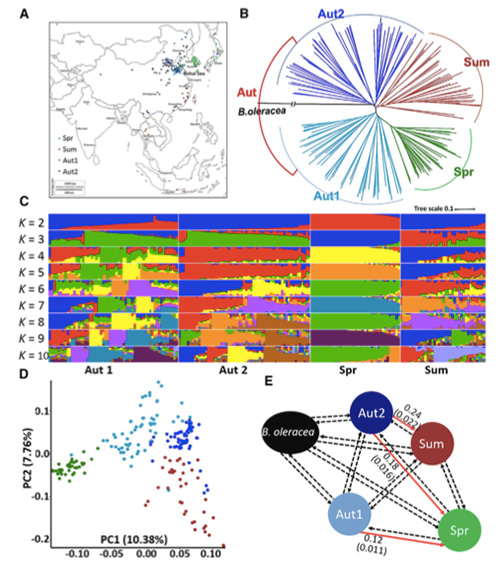 Analýza struktury populace na čínském zelí | 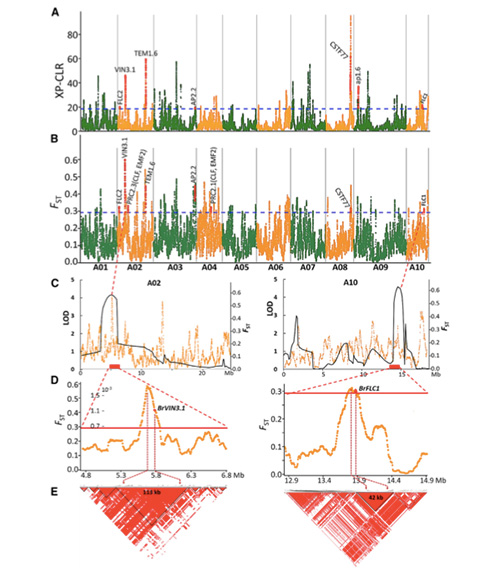 Genetické informace o výběru čínského zelí |
Tongbing a kol."Mapa genomických variací poskytuje pohledy na genetický základ jarního výběru čínského zelí (Brassica rapa ssp.pekinensis)."molekulární rostliny,11(2018):1360-1376.















