
Conjunto de genoma baseado em Hi-C
Vantagens do serviço
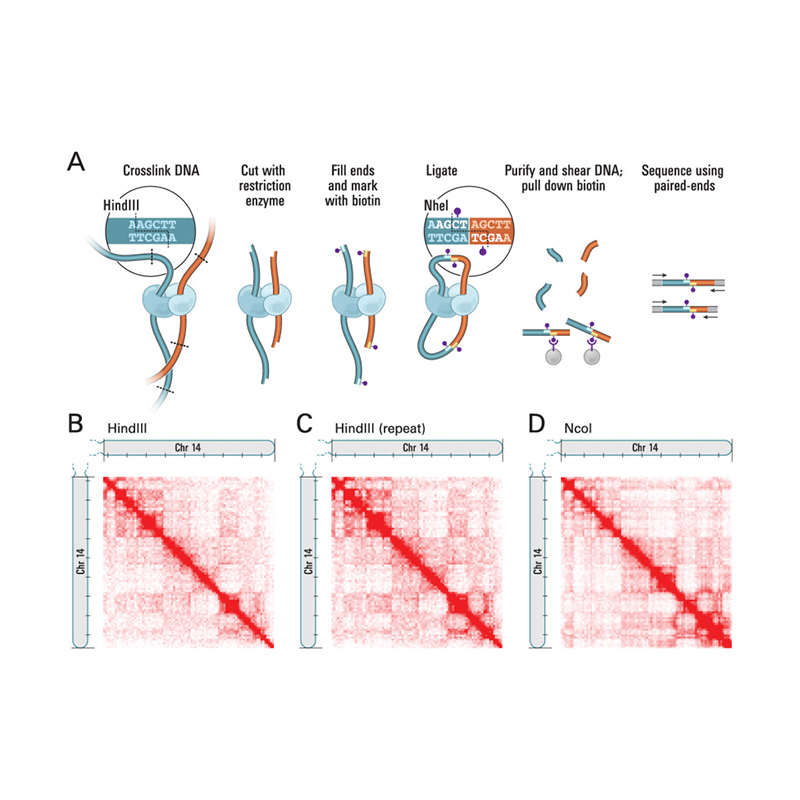
Visão geral do Hi-C
(Lieberman-Aiden E et al.,Ciência, 2009)
● Não há necessidade de construção de população genética para ancoragem de contig;
● Maior densidade de marcadores levando a maior taxa de ancoragem de contigs acima de 90%;
● Permite avaliação e correções em conjuntos de genomas existentes;
● Menor tempo de resposta com maior precisão na montagem do genoma;
● Experiência abundante com mais de 1000 bibliotecas Hi-C construídas para mais de 500 espécies;
● Mais de 100 casos de sucesso com fator de impacto acumulado publicado superior a 760;
● Montagem de genoma baseado em Hi-C para genoma poliplóide, taxa de ancoragem de 100% foi alcançada em projeto anterior;
● Patentes internas e direitos autorais de software para experimentos Hi-C e análise de dados;
● Software de ajuste de dados visualizados desenvolvido pela própria empresa, permite mover, reverter, revogar e refazer manualmente os blocos.
Especificações de serviço
|
Tipo de biblioteca
|
Plataforma | Comprimento da leitura | Recomendar estratégia |
| Olá-C | Illumina NovaSeq | PE150 | ≥ 100X |
Análises de bioinformática
● Controle de qualidade de dados brutos
● Controle de qualidade da biblioteca Hi-C
● Montagem de genoma baseada em Hi-C
● Avaliação pós-montagem
Requisitos de amostra e entrega
Requisitos de amostra:
| Animal | Fungo | Plantas
|
| Tecido congelado: 1-2g por biblioteca Células: 1x 10^7 células por biblioteca | Tecido congelado: 1g por biblioteca | Tecido congelado: 1-2g por biblioteca
|
| *Recomendamos fortemente o envio de pelo menos 2 alíquotas (1 g cada) para o experimento Hi-C. | ||
Entrega de amostra recomendada
Recipiente: tubo de centrífuga de 2 ml (folha de estanho não é recomendada)
Para a maioria das amostras, recomendamos não conservar em etanol.
Rotulagem das amostras: As amostras precisam ser claramente rotuladas e idênticas ao formulário de informações da amostra enviado.
Remessa: Gelo seco: As amostras precisam primeiro ser embaladas em sacos e enterradas em gelo seco.
Fluxo de trabalho de serviço

Projeto de experimento

Entrega de amostra

Extração de DNA

Construção de biblioteca

Sequenciamento

Análise de dados

Serviços pós-venda
*Os resultados de demonstração mostrados aqui são todos de genomas publicados com Biomarker Technologies
1. Mapa de calor de interação Hi-C deCamptotheca acuminatagenoma.Conforme mostrado no mapa, a intensidade das interações está negativamente correlacionada com a distância linear, o que indica uma montagem altamente precisa no nível cromossômico.(Proporção de ancoragem: 96,03%)
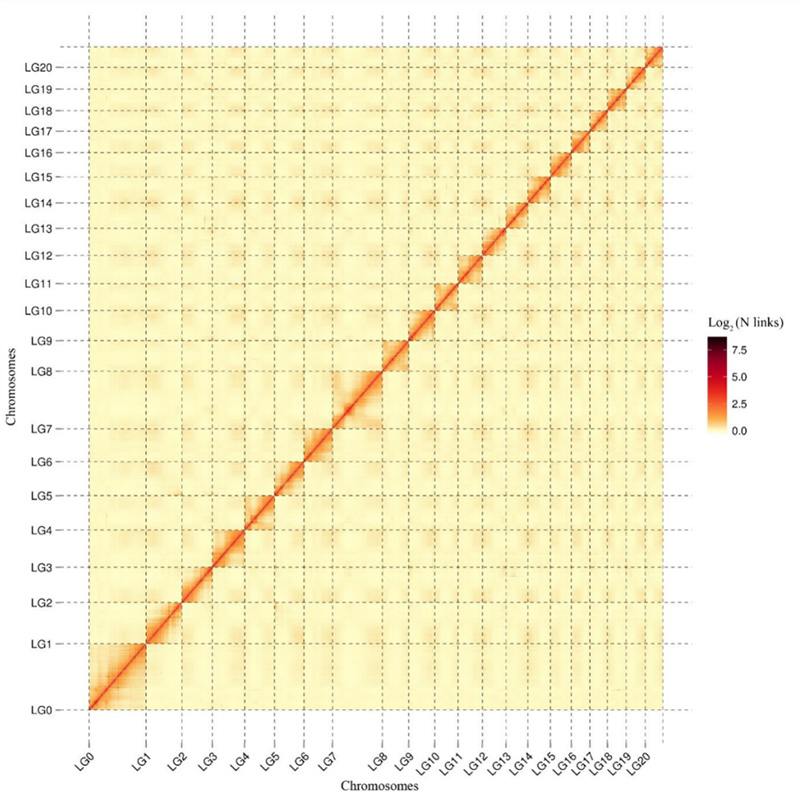
KangM et al.,Comunicações da Natureza, 2021
2.Hi-C facilitou a validação de inversões entreGossypium hirsutumL.TM-1 A06 eG. arbóreoChr06
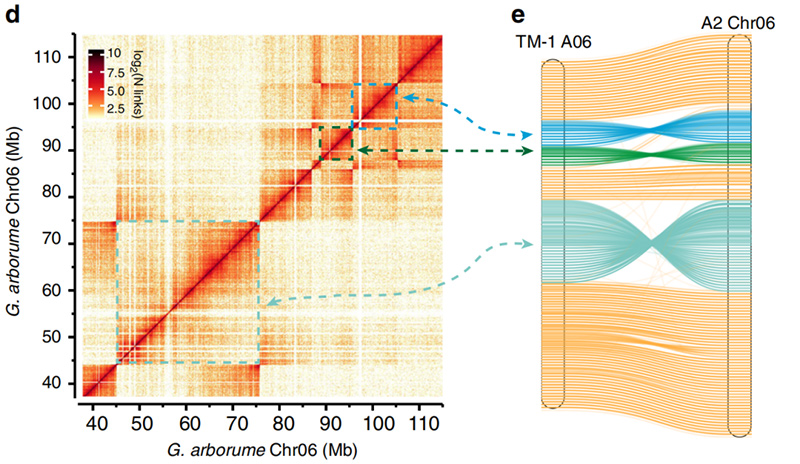
YangZ et al.,Comunicações da Natureza, 2019
3.Montagem e diferenciação bialélica do genoma da mandioca SC205.Mapa de calor Hi-C mostrado divisão clara em cromossomos homólogos.
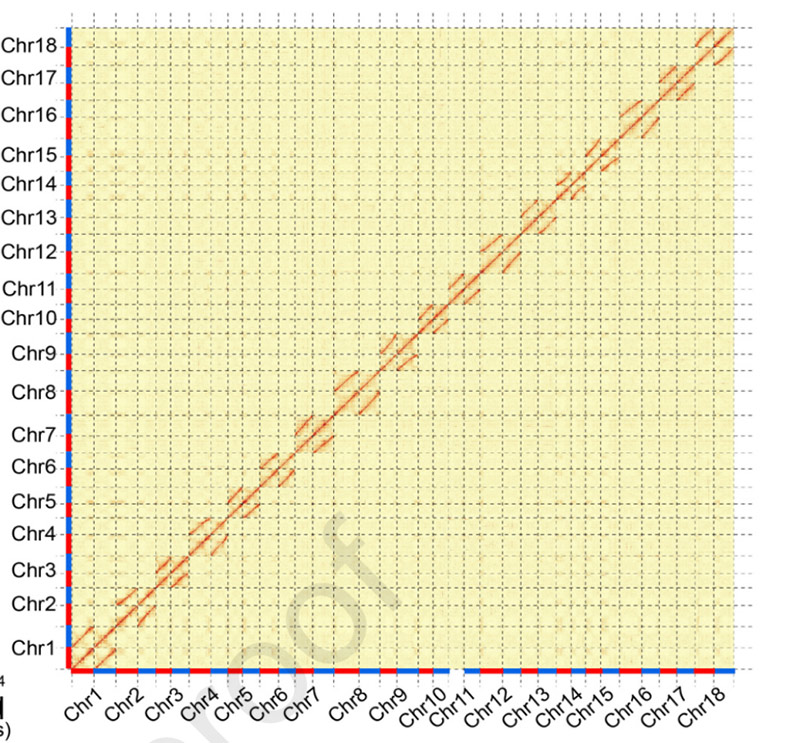
HuW et al.,Planta Molecular, 2021
4.Mapa de calor Hi-C na montagem do genoma de duas espécies de Ficus:F.microcarpa(taxa de ancoragem: 99,3%) eF.hispida (taxa de ancoragem: 99,7%)
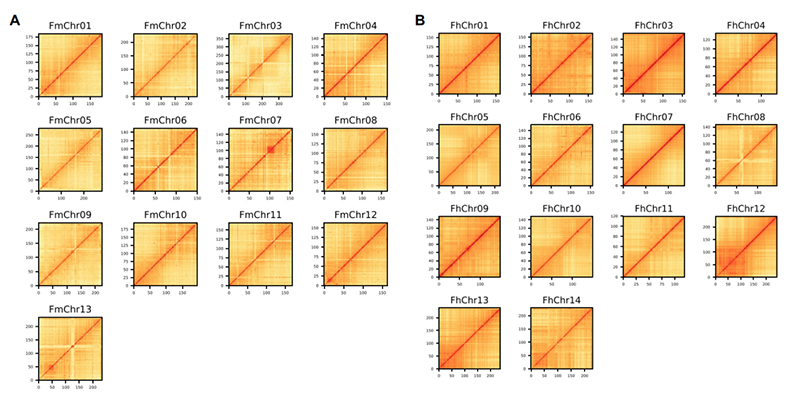
Zhang X et al.,Célula, 2020
Caso BMK
Genomas da figueira-da-índia e da vespa polinizadora fornecem informações sobre a coevolução da vespa-figueira
Publicados: Célula, 2020
Estratégia de sequenciamento:
F.microcarpa genoma: Aprox.84 X PacBio RSII (36,87 Gb) + Hi-C (44 Gb)
F. hispidagenoma: Aprox.97 X PacBio RSII (36,12 Gb) + Hi-C (60 Gb)
Eupristina verticillatagenoma: Aprox.170 X PacBio RSII (65 Gb)
Principais resultados
1. Dois genomas de figueira-da-índia e um genoma de vespa polinizadora foram construídos usando sequenciamento PacBio, Hi-C e mapa de ligação.
(1)F.microcarpagenoma: Um conjunto de 426 Mb (97,7% do tamanho estimado do genoma) foi estabelecido com contig N50 de 908 Kb, pontuação BUSCO de 95,6%.No total, 423 sequências Mb foram ancoradas em 13 cromossomos por Hi-C.A anotação do genoma rendeu 29.416 genes codificadores de proteínas.
(2)F. Hispidagenoma: Uma montagem de 360 Mb (97,3% do tamanho estimado do genoma) foi produzida com contig N50 de 492 Kb e pontuação BUSCO de 97,4%.Um total de sequências de 359 Mb foram ancoradas em 14 cromossomos por Hi-C e altamente idênticas ao mapa de ligação de alta densidade.
(3)Eupristina verticillatagenoma: Um conjunto de 387 Mb (tamanho estimado do genoma: 382 Mb) foi estabelecido com contig N50 de 3,1 Mb e pontuação BUSCO de 97,7%.
2. A análise genômica comparativa revelou um grande número de variações estruturais entre doisFigueiragenomas, que forneceram recursos genéticos inestimáveis para estudos de evolução adaptativa.Este estudo, pela primeira vez, forneceu insights sobre a coevolução da vespa-figo em nível genômico.
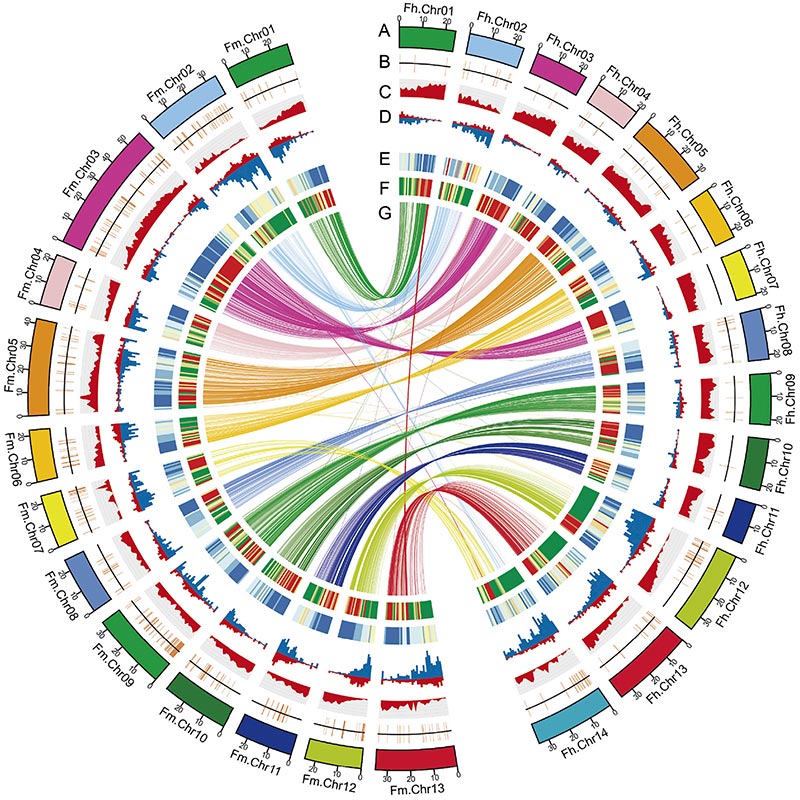 Diagrama Circos sobre características genômicas de doisFigueiragenomas, incluindo cromossomos, duplicações segmentares (SDs), transposons (LTR, TEs, DNA TEs), expressão gênica e sintenia | 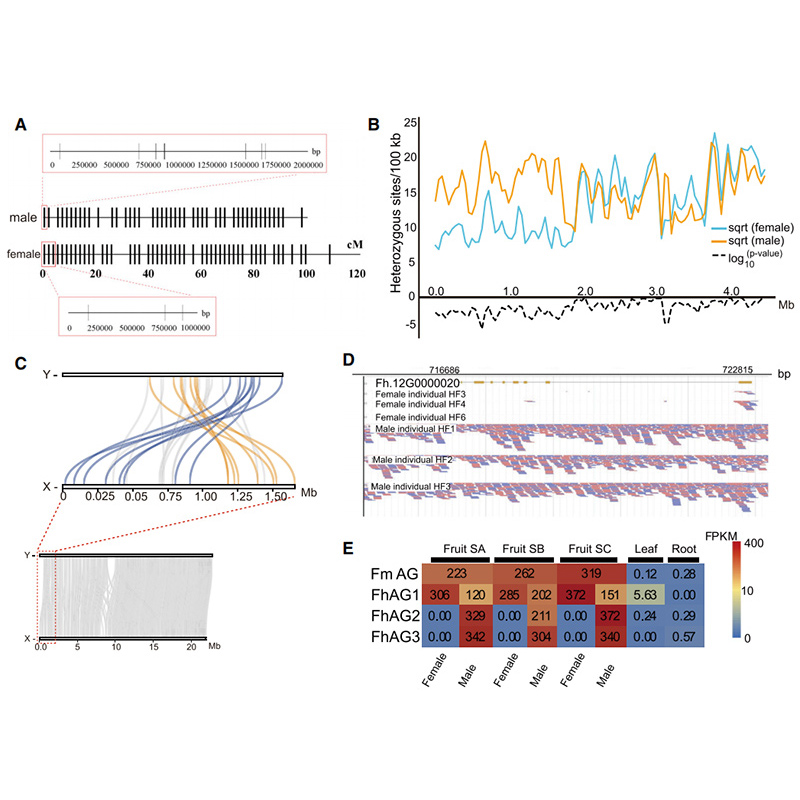 Identificação do cromossomo Y e gene candidato à determinação do sexo |
Zhang, X., et al.“Os genomas da figueira-da-índia e da vespa polinizadora fornecem informações sobre a coevolução da figueira-vespa.”Célula 183.4(2020).














