Samazinātas reprezentācijas bisulfīta sekvencēšana (RRBS)
Pakalpojuma specifikācijas
Platforma: NovaSeq platforma, PE150
Bibliotēkas veids: 200–400 bp ievieto ar bisulfītu apstrādātu DNS bibliotēku
Secības noteikšanas stratēģija: pārī beigas 150 bp
Ieteicamā datu izvade: 10 Gb neapstrādāti dati par paraugu
Prasību paraugs
DNS daudzums: ≥ 2ug
DNS koncentrācija: ≥ 20ng/μl.
Tīrība: OD260/280 = 1,8 līdz 2,0 bez degradācijas vai RNS piesārņojuma
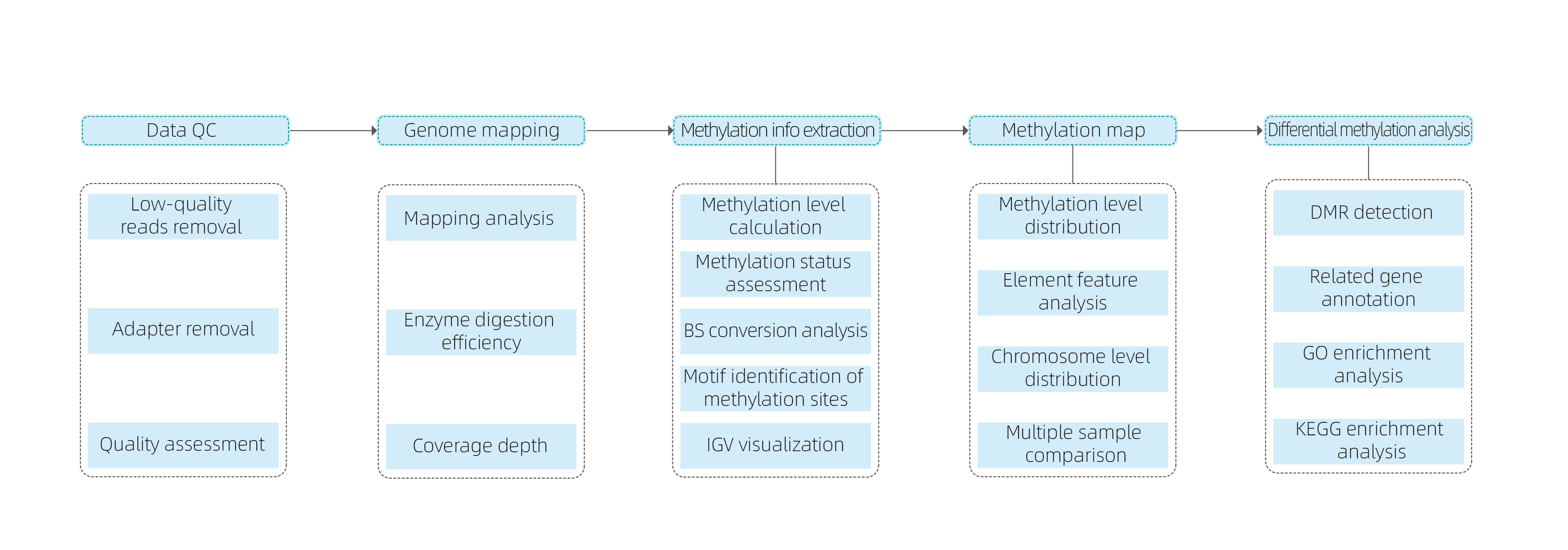
Bioinformātikas analīze
Pakalpojuma darba plūsma

Paraugu piegāde

Bibliotēkas celtniecība

Secība

Datu analīze
Pēcpārdošanas pakalpojumi
a.Atsauces genoma izlīdzināšanas statistika
Kartēšanas nolasījumu statistika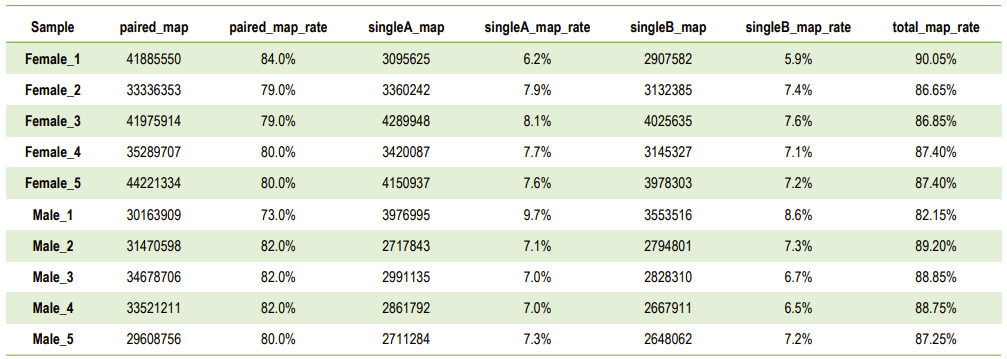
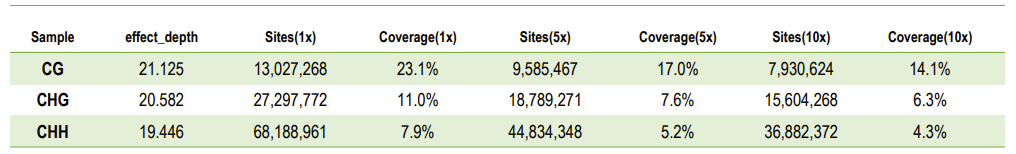
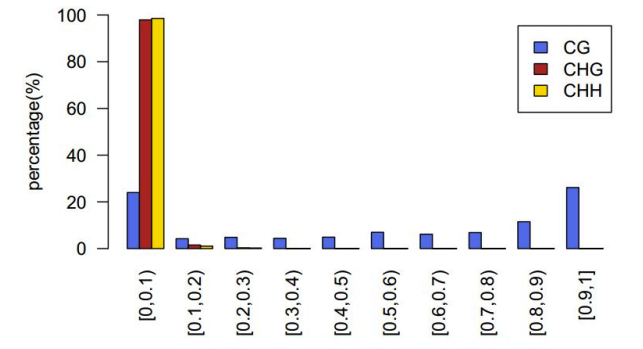
SC vietnes sekvencēšanas dziļuma un pārklājuma statistika
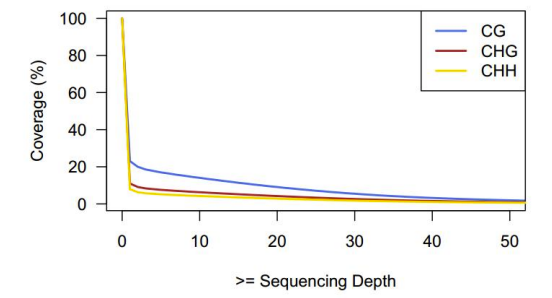
Auzkrātais pārklājums
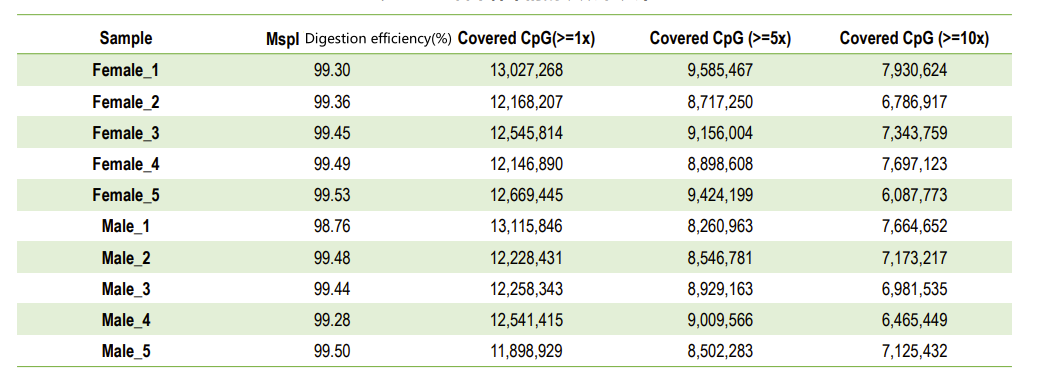
Dkatra parauga sagremošanas efektivitāte
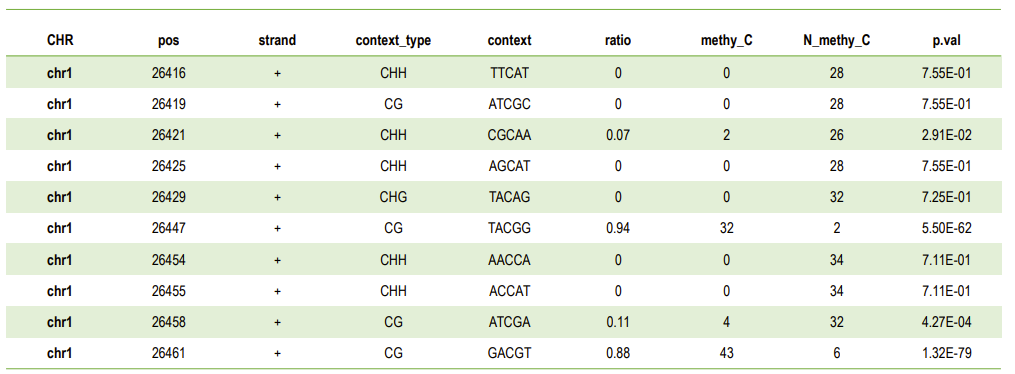
b.Metilēšanas vietas noteikšana
Metilēšanas līmeņu saraksts C vietā
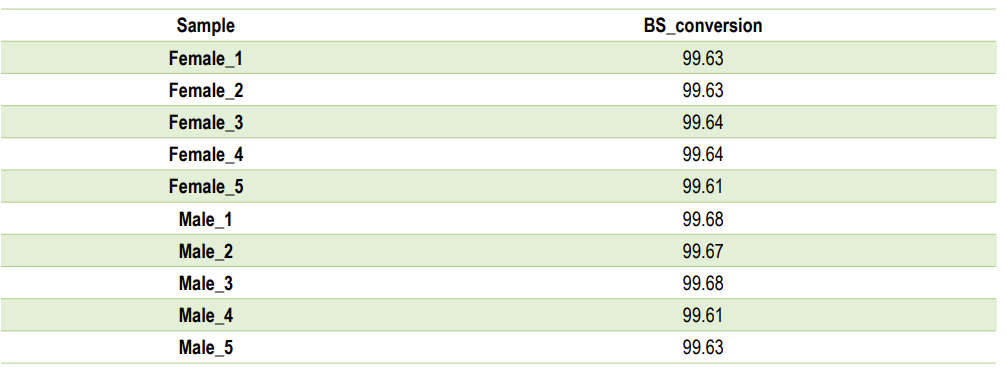
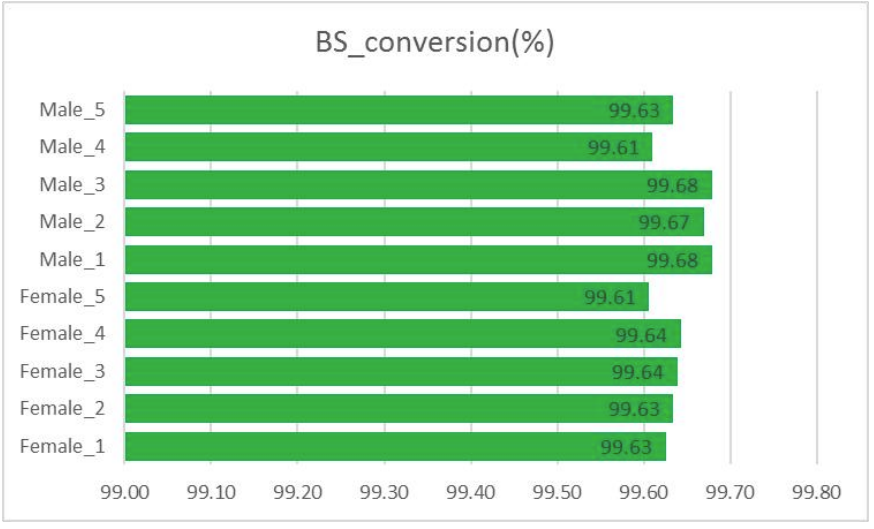
BS konversija
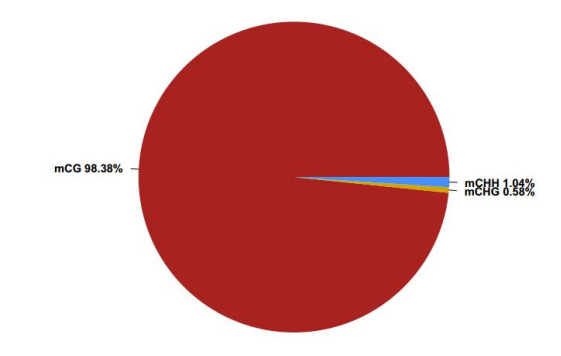
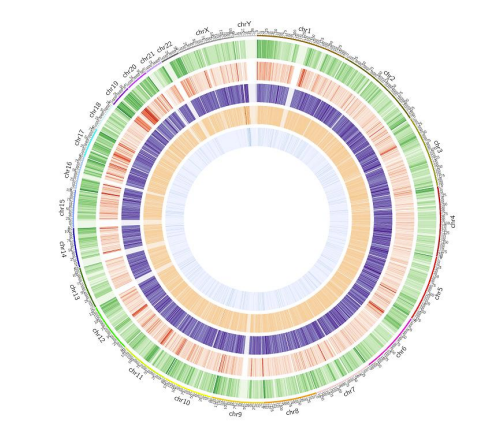
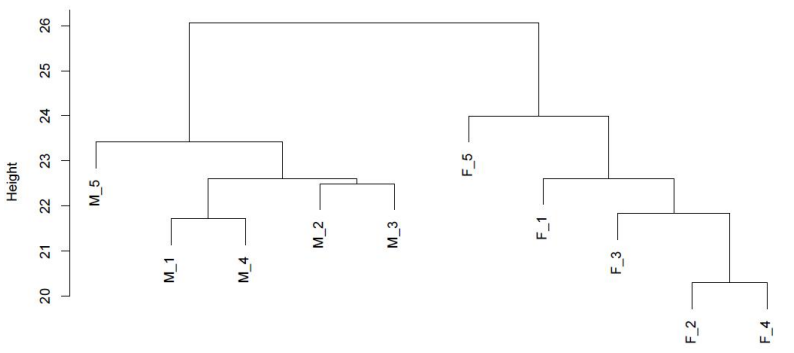
c.Metilēšanas karte
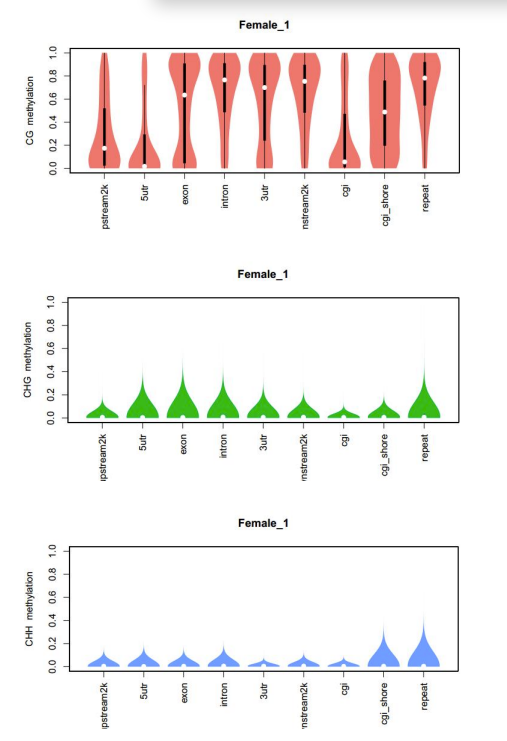
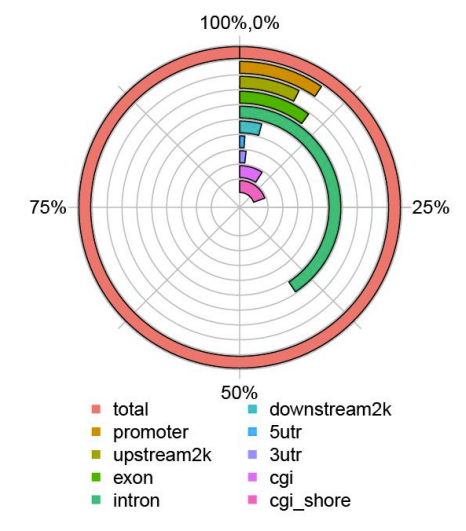
Genome elements
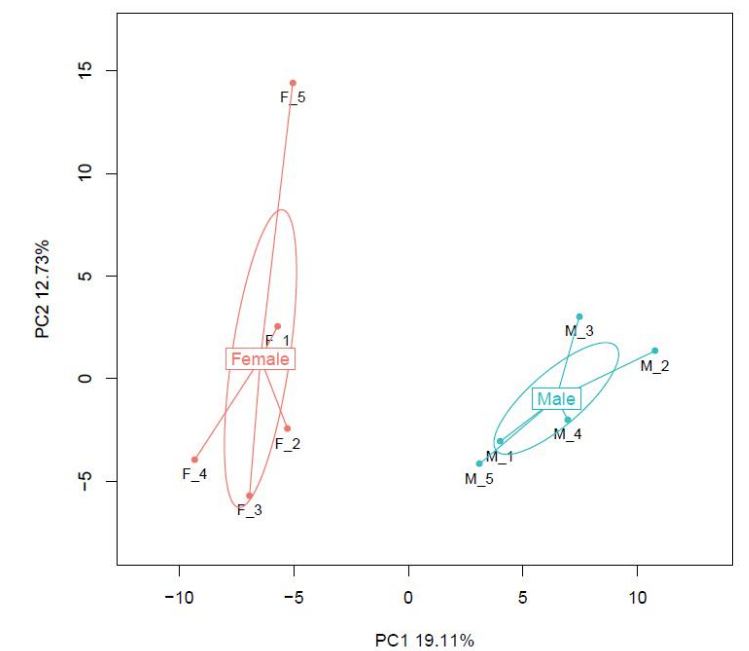
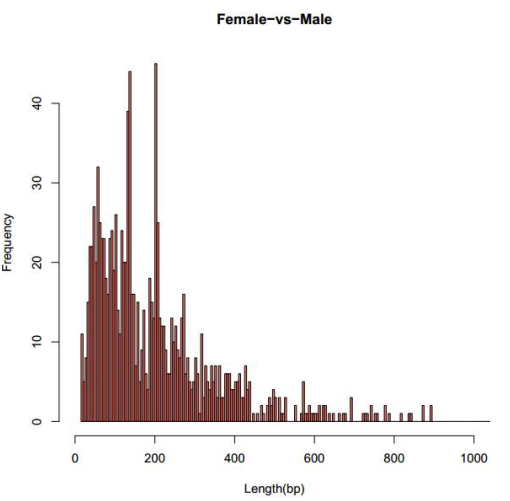
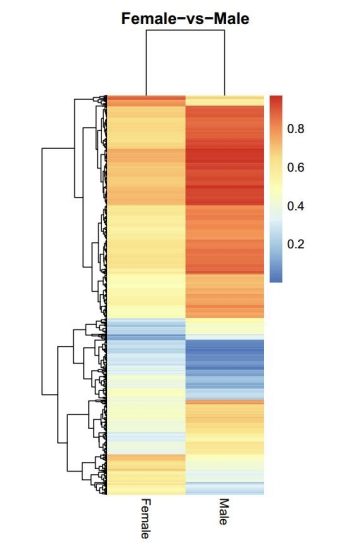
d.Metilēšanas līmeņu salīdzinājums starp paraugiem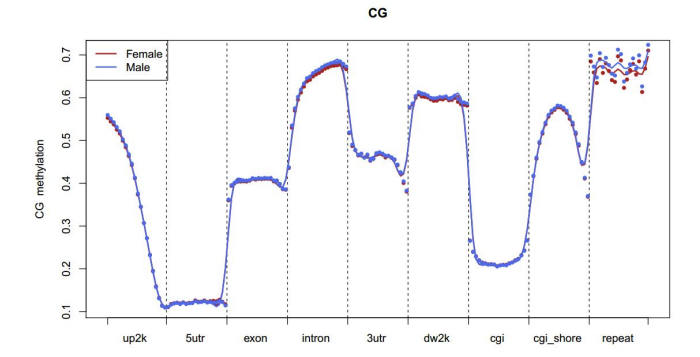
Pairwise CG metilēšanas korelācija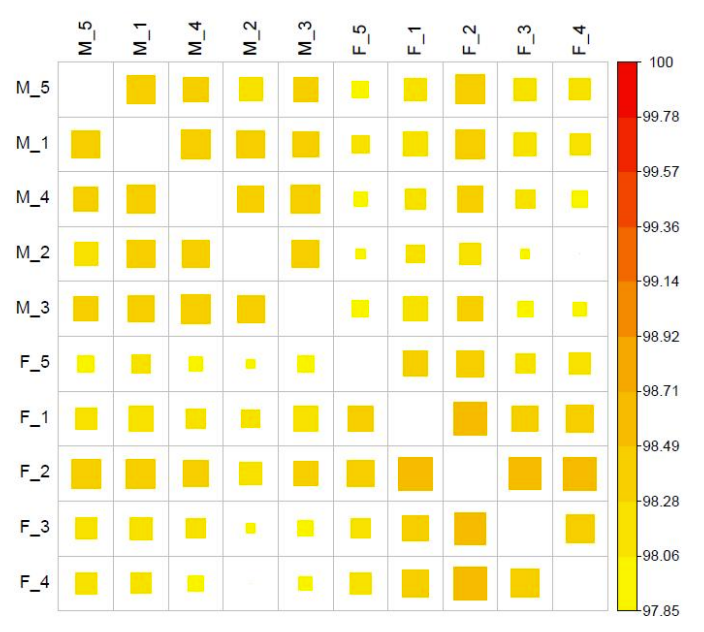
d.Diferenciālā metilēšanas analīze
SDMR statistika