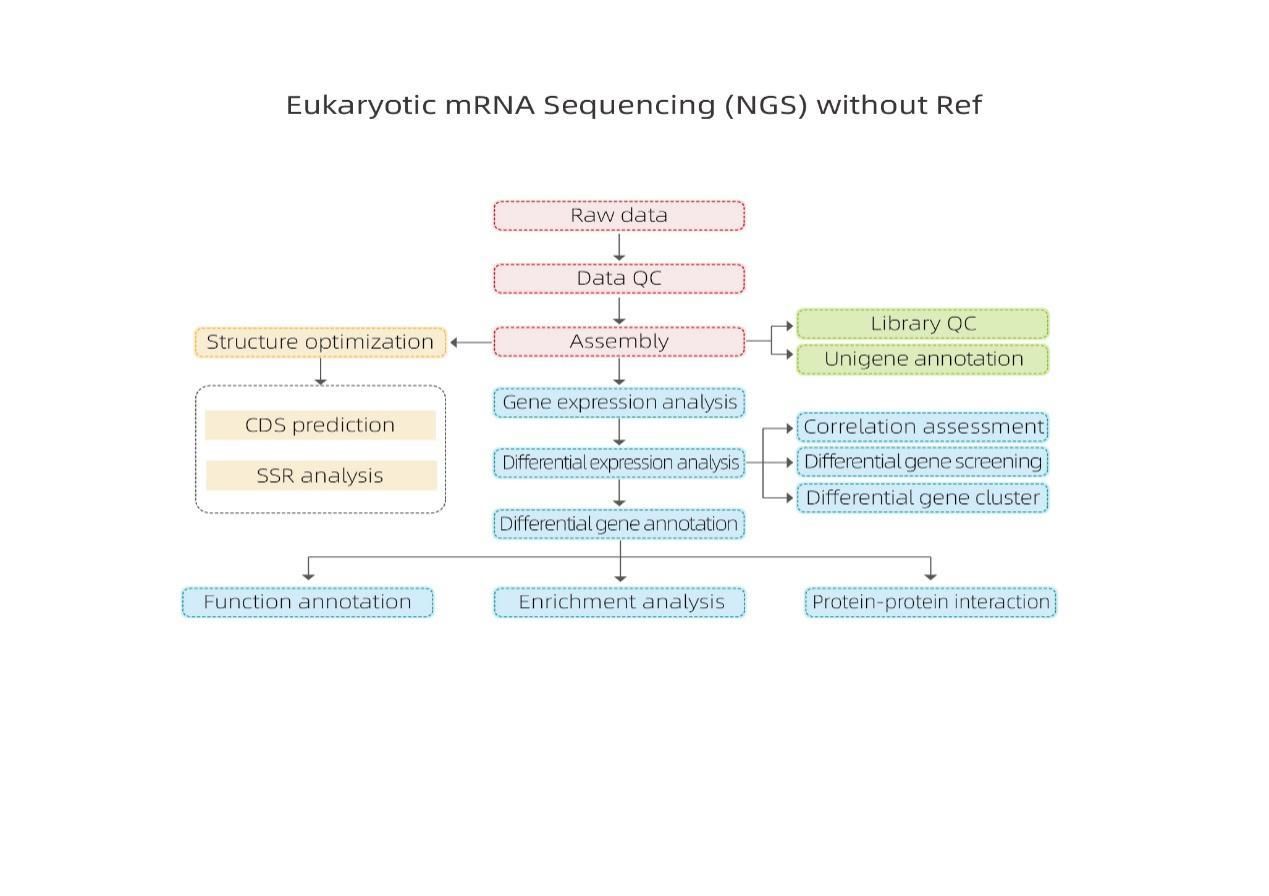
Secuenciación de ARNm non baseada en referencia-Illumina
características
● Independente de calquera xenoma de referencia,
● Os datos poderían utilizarse para analizar a estrutura e a expresión das transcricións
● Identificar sitios de recorte variables
Vantaxes do servizo
● Entrega de resultados baseada en BMKCloud: os resultados entréganse como ficheiro de datos e informe interactivo a través da plataforma BMKCloud, que permite a lectura sinxela de saídas de análise complexas e a minería de datos personalizada en base á análise bioinformática estándar.
● Servizos posvenda: servizos posvenda válidos durante 3 meses despois da finalización do proxecto, incluíndo o seguimento dos proxectos, a resolución de problemas, as preguntas e respostas dos resultados, etc.
Requisitos de mostra e entrega
Requisitos de mostra:
Nucleótidos:
| Conc. (ng/μl) | Cantidade (μg) | Pureza | Integridade |
| ≥ 20 | ≥ 0,5 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Contaminación limitada ou nula de proteínas ou ADN no xel. | Para plantas: RIN≥6,5; Para animais: RIN≥7,0; 5,0≥28S/18S≥1,0; elevación de referencia limitada ou nula |
Tecido: Peso (seco): ≥1 g
*Para tecidos inferiores a 5 mg, recomendamos enviar mostras de tecido conxelada instantáneamente (en nitróxeno líquido).
Suspensión celular: reconto celular = 3×107
*Recomendamos enviar lisado celular conxelado.No caso de que esa cela conte menos de 5×105, recoméndase conxelar flash en nitróxeno líquido.
Mostras de sangue:
PA×xeneBloodRNATube;
6 ml de TRIzol e 2 ml de sangue (TRIzol: sangue = 3:1)
Entrega de mostra recomendada
Envase:
Tubo de centrífuga de 2 ml (non se recomenda papel de aluminio)
Etiquetaxe da mostra: grupo+réplica, por exemplo, A1, A2, A3;B1, B2, B3....
Envío:
1. Xeo seco: as mostras deben ser embaladas en bolsas e enterradas en xeo seco.
2.Tubos RNAstable: as mostras de ARN pódense secar nun tubo de estabilización de ARN (por exemplo, RNAstable®) e enviarse a temperatura ambiente.
Fluxo de traballo do servizo

Deseño de experimentos

Entrega da mostra

extracción de ARN

Construción da biblioteca

Secuenciación

Análise de datos

Servizos posvenda
Bioinformática
1.ARNm(denovo) Principio de ensamblaxe
Por Trinity, as lecturas están fragmentadas en anacos máis pequenos, coñecidos como K-mer.Estes K-mers úsanse entón como sementes para estenderse en contigs e despois compoñente baseándose en superposicións contig.Finalmente, De Bruijn aplicouse aquí para recoñecer as transcricións nos compoñentes.
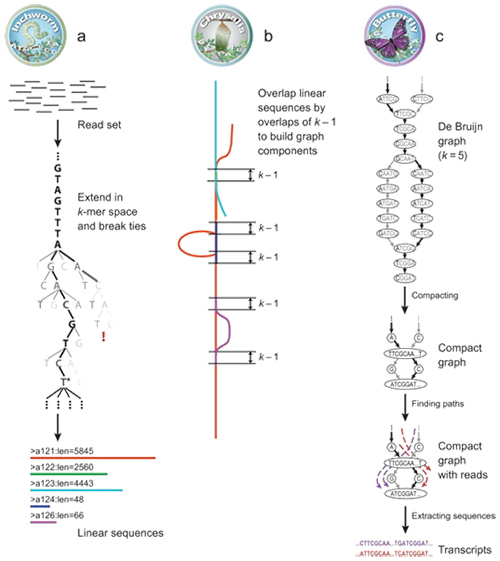
ARNm (De novo) Visión xeral de Trinity
2.ARNm (De novo) Distribución do nivel de expresión xénica
ARN-Seq é capaz de lograr unha estimación moi sensible da expresión xénica.Normalmente, o rango detectable de expresións de transcricións FPKM varía de 10^-2 a 10^6
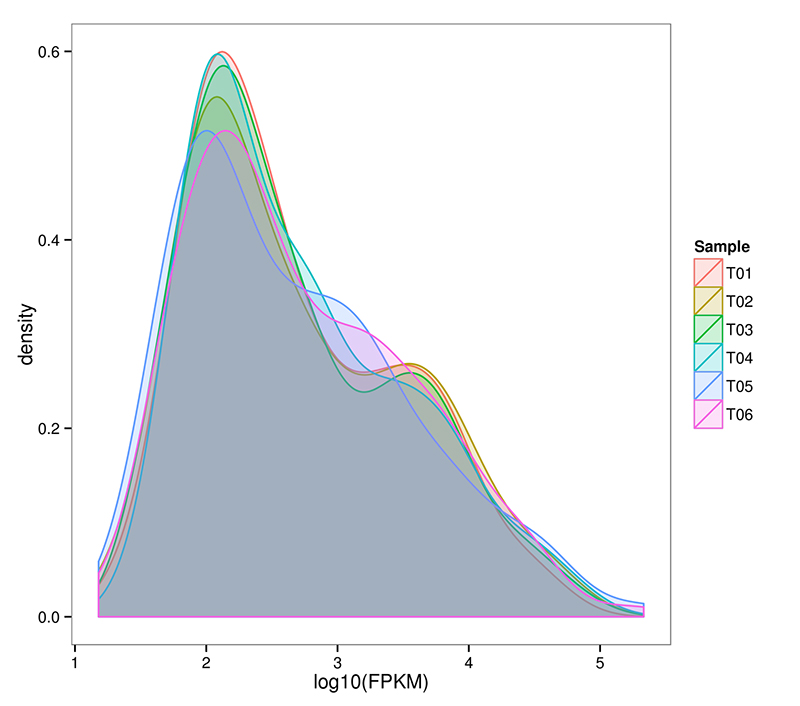
ARNm (De novo) Distribución da densidade de FPKM en cada mostra
3.ARNm (De novo) Análise de enriquecemento GO de DEG
A base de datos GO (Gene Ontology) é un sistema de anotación biolóxica estruturada que contén un vocabulario estándar de funcións de xenes e produtos xenéticos.Contén varios niveis, onde canto máis baixo sexa o nivel, máis específicas serán as funcións.
ARNm (De novo) Clasificación GO de DEGs en segundo nivel
Caso BMK
Análise do transcriptoma do metabolismo da sacarosa durante o inchazo e desenvolvemento do bulbo na cebola (Allium cepa L.)
Publicado: fronteiras na ciencia das plantas, 2016
Estratexia de secuenciación
Illumina HiSeq2500
Recollida de mostras
Neste estudo utilizouse o cultivar Utah Yellow Sweet Spain "Y1351".O número de mostras recollidas foi
15º día despois do inchazo (DAS) do bulbo (2 cm de diámetro e 3-4 g de peso), 30º DAS (5 cm de diámetro e 100-110 g de peso) e ∼3 no 40º DAS (7 cm de diámetro e 260-300 gramos).
Resultados clave
1. No diagrama de Venn detectáronse un total de 146 DEG nos tres pares de etapas de desenvolvemento.
2. "Transporte e metabolismo de carbohidratos" estaba representado por só 585 uníxenos (é dicir, o 7% do COG anotado).
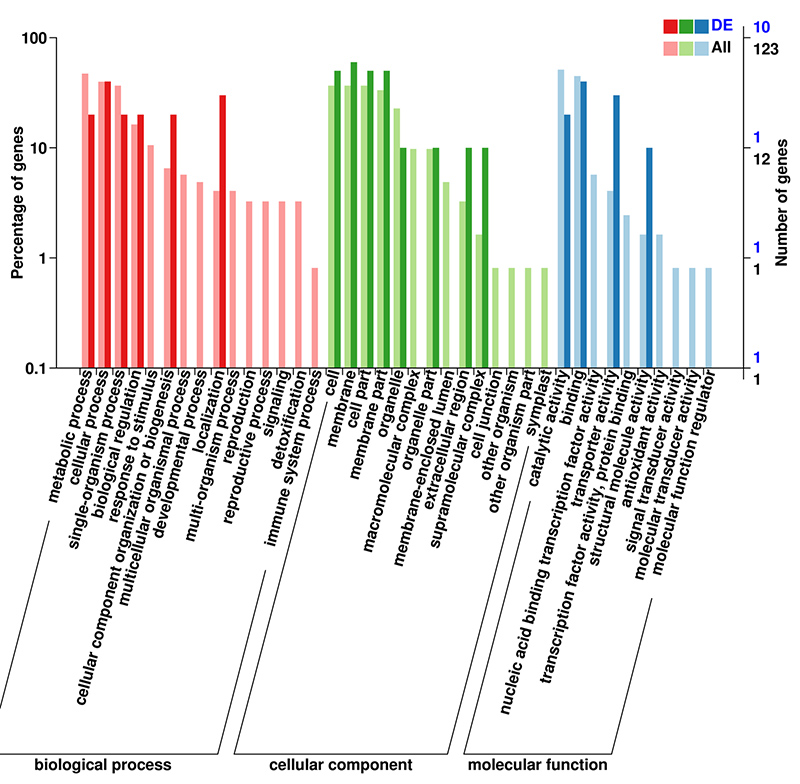
3. Os Unigenes anotados con éxito na base de datos GO clasificáronse en tres categorías principais para as tres diferentes etapas do desenvolvemento da lámpada.Os máis representados na categoría principal de "proceso biolóxico" foron "proceso metabólico", seguido de "proceso celular".Na categoría principal de "función molecular" as dúas categorías máis representadas foron "unión" e "actividade catalítica".
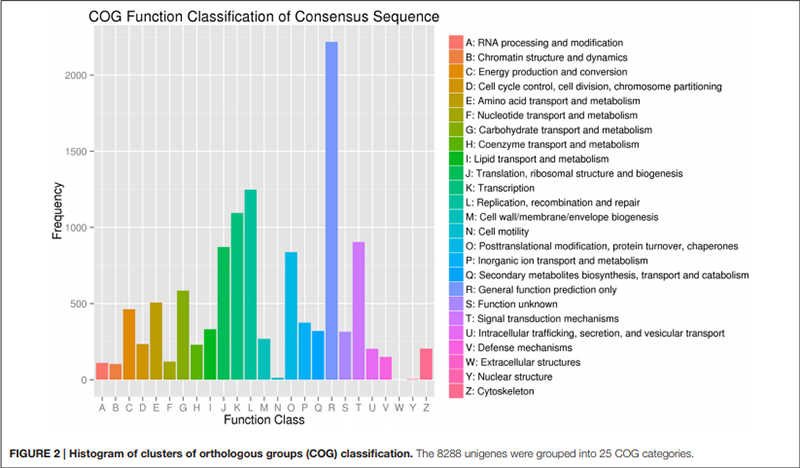 Clasificación do histograma de grupos de grupos ortólogos (COG). | 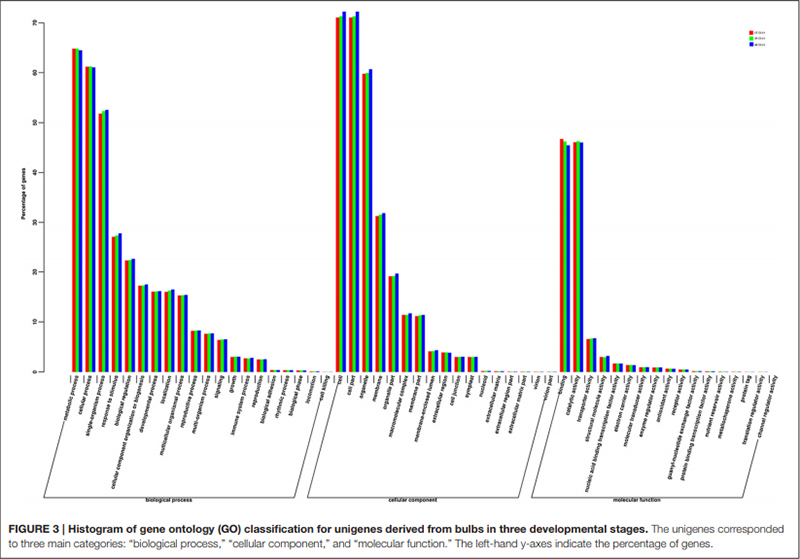 Histograma de clasificación de ontoloxía xenética (GO) para uníxenos derivados de bulbos en tres etapas de desenvolvemento |
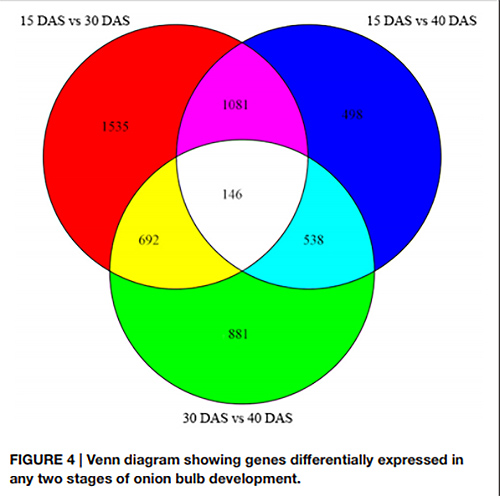 Diagrama de Venn que mostra xenes expresados de forma diferencial en dúas etapas calquera do desenvolvemento do bulbo de cebola |
Referencia
Zhang C, Zhang H, Zhan Z, et al.Análise do transcriptoma do metabolismo da sacarosa durante o inchazo e desenvolvemento do bulbo na cebola (Allium cepa L.)[J].Frontiers in Plant Science, 2016, 7:1425-.DOI: 10.3389/fpls.2016.01425