Augu/dzīvnieku visa genoma sekvencēšana
1. Pakalpojuma priekšrocības
Plaša pieredze genomu sekvencēšanā vairāk nekā 1000 sugām.
Vairāk nekā 800 publicētu gadījumu, kuru kumulatīvā ietekmes koeficients pārsniedz 4000.
Visaptveroša bioinformātikas analīze par variāciju izsaukšanu un funkciju analīzi.
2. Pakalpojuma specifikācijas
| Platforma | Bibliotēka | Ieteicamais secības dziļums | |
| Illumina | PE 150 | SNP gadījumā InDel zvana ≥ 10x SV, CNY zvani ≥ 30x
| |
| Nanopore
| 8 kb | SV, CNY zvani ≥ 20x | |
| Pacbio | CCS | 15 kb | SNP, InDel, SV, CNY zvaniem ≥ 10x |
3. Prasību paraugs
| Platforma | Konc.(ng/μL)
| Summa (ng)
| Tīrība
| Agarozes želeja
| ||
| OD260/280 | OD260/230 | 1. Notīriet galveno joslu bez vai ierobežotasuz gēla novērota degradācija. 2. RNS vai olbaltumvielu piesārņojums nav vai ir ierobežots
| ||||
| Illumina | ≥1 | ≥30
| - | - | ||
| Nanopore
| ≥30 | Atkarīgs no datu apjoma 10 μg/šūnā | 1,7-2,2 | ≥1,5 | ||
| Pacbio | CCS | ≥50 | 1,7-2,2 | 1,8-2,5 | ||
4. Bioinformācijas analīze
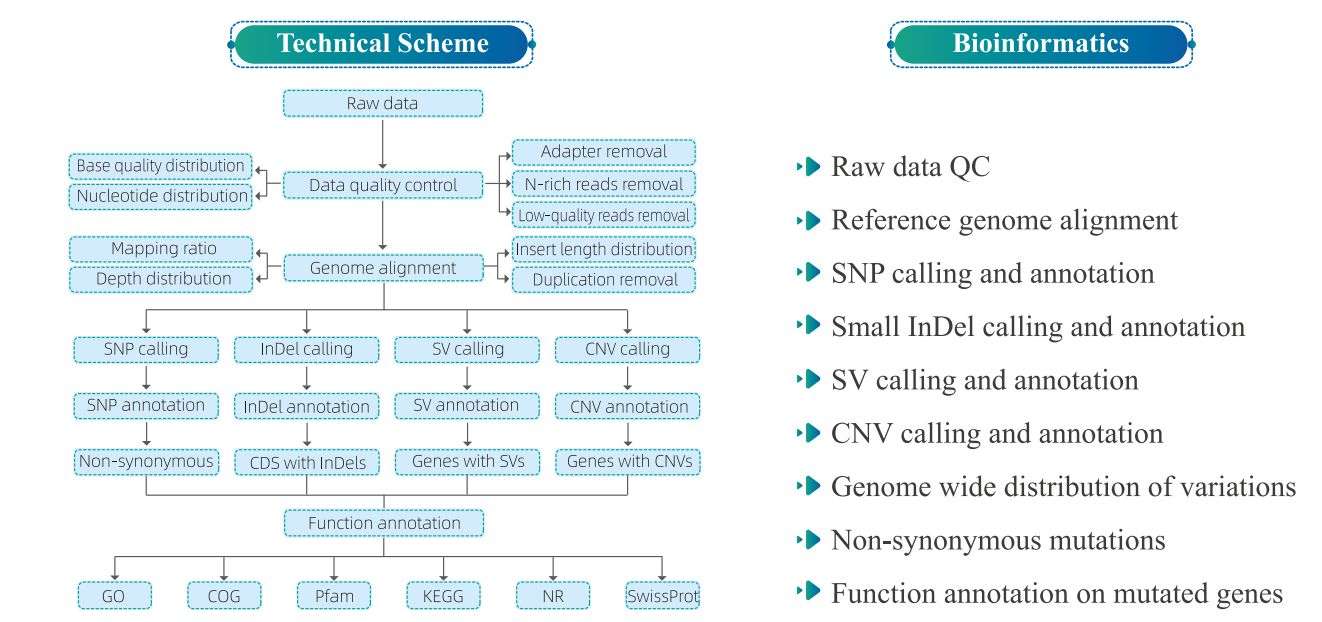
5. Servisa darba plūsma

Paraugu piegāde

DNS ekstrakcija

Bibliotēkas celtniecība

Secība

Datu analīze
Datu piegāde
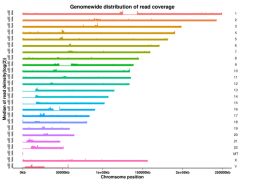
1) Genoma kartēšanas statistika
1. tabula Kartēšanas rezultātu statistika
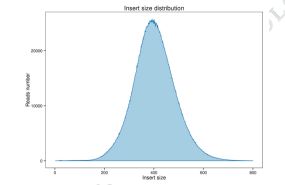
1. attēls. Ieliktņa izmēra un nolasījumu pārklājuma sadalījums.
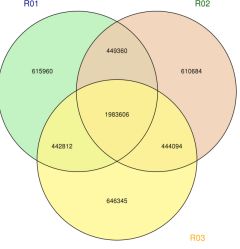
2) Variate Detection
2. attēls SNP/INDEL/SV statistika un anotācija starp paraugiem
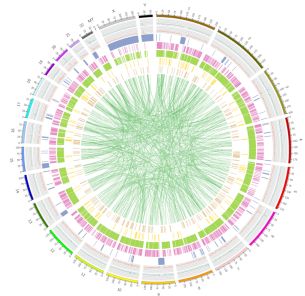
3. attēls Genoma mēroga vatāciju sadalījums
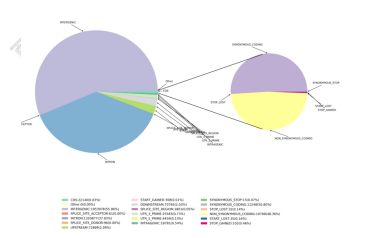
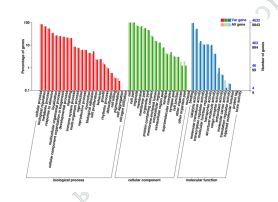
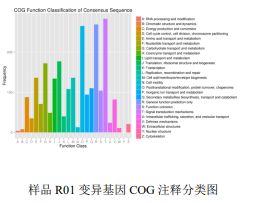
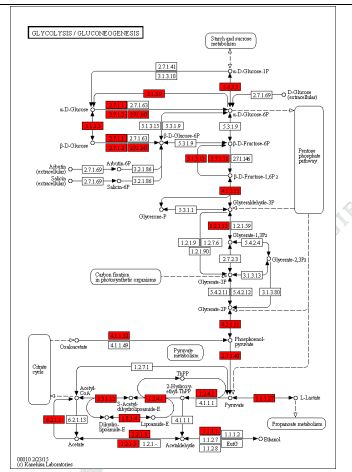
3) Variāciju funkcionālā anotācija
| 2019. gads | Dabas komunikācijas | Visa genoma atkārtota sekvencēšana atklāj Brassica napus izcelsmi un ģenētiskos lokus, kas iesaistīti tā uzlabošanā |
| 2020. gads | PNAS | Zelta zivtiņas (Carassius auratus) evolūcijas izcelsme un pieradināšanas vēsture |
| 2021. gads | Augu biotehnoloģijas žurnāls | Abu kultivēto džutas sugu atsauces genomi |
| 2021. gads | Augu biotehnoloģijas žurnāls | Dārzeņu un eļļas sēklu allopoliploīda Brassicajuncea genoma paraksti un ģenētiskie loki, kas kontrolē glikozinolātu uzkrāšanos |
| 2019. gads | Molekulārais augs | Visa genoma atkārtota sekvencēšana pasaules mēroga rapša pievienošanās kolekcijai atklāj to ekotipa atšķirības ģenētisko pamatu |
| 2022. gads | Dārzkopības pētījumi | Genoma mēroga asociācijas analīze sniedz molekulāru ieskatu arbūzu sēklu lieluma dabiskajās variācijās |
| 2021. gads | Eksperimentālās botānikas žurnāls | Genoma mēroga asociācijas pētījums identificē GhSAD1 variantus, kas nodrošina aukstuma toleranci kokvilnai |
| 2021. gads | Eksperimentālās botānikas žurnāls | Genoma mēroga asociācijas pētījums un transkriptu salīdzinājums atklāj jaunus QTL un kandidātgēnus, kas kontrolē ziedlapu izmēru rapšu sēklās |