Gara nekodēta secība-Illumina
Pakalpojuma priekšrocības
● Pakalpojuma priekšrocības
● Šūnu un audu specifisks
● Konkrēts posms izsaka un parāda dinamiskas izteiksmes izmaiņas
● Precīzi laika un telpas izteiksmes modeļi
● Kopīga analīze ar mRNS datiem.
● Uz BMKCloud balstīta rezultātu piegāde: platformā pieejama pielāgota datu ieguve.
● Pēcpārdošanas pakalpojumi spēkā 3 mēnešus pēc projekta pabeigšanas
Prasību paraugs un piegāde
| Bibliotēka | Platforma | Ieteicamie dati | Datu kvalitātes kontrole |
| rRNS izsīkums | Illumina PE150 | 10 Gb | Q30≥85% |
| Konc. (ng/μl) | Daudzums (μg) | Tīrība | Integritāte |
| ≥ 100 | ≥ 0,5 | OD260/280=1,7-2,5 OD260/230=0,5-2,5 Uz gēla parādīts ierobežots proteīnu vai DNS piesārņojums vai tā nav. | Augiem: RIN≥6,5; Dzīvniekiem: RIN≥7,0; 5,0≥28S/18S≥1,0; ierobežots vai vispār nav bāzes līmeņa pacēluma |
Nukleotīdi:
Audi: svars (sauss): ≥1 g
*Audiem, kas ir mazāki par 5 mg, iesakām nosūtīt ātri sasaldētu (šķidrā slāpeklī) audu paraugu.
Šūnu suspensija: Šūnu skaits = 3 × 107
* Mēs iesakām nosūtīt saldētu šūnu lizātu.Gadījumā, ja šūnu skaits ir mazāks par 5 × 105, ieteicams ātri sasaldēt šķidrā slāpeklī.
Asins paraugi:
PA×geneBloodRNATube;
6 ml TRIzola un 2 ml asiņu (TRIzol: Blood = 3: 1)
Ieteicamā paraugu piegāde
Tvertne: 2 ml centrifūgas caurule (skārda folija nav ieteicama)
Marķējuma paraugs: grupa + atkārtojums, piemēram, A1, A2, A3;B1, B2, B3......
Sūtījums:
1. Sausais ledus: paraugi jāiepako maisos un jāierok sausajā ledū.
2.RNAstable caurules: RNS paraugus var žāvēt RNS stabilizācijas mēģenē (piemēram, RNAstable®) un nosūtīt istabas temperatūrā.
Pakalpojuma darba plūsma

Eksperimenta dizains

Paraugu piegāde

RNS ekstrakcija

Bibliotēkas celtniecība

Secība

Datu analīze

Pēcpārdošanas pakalpojumi
Bioinformātika
1.LncRNS klasifikācija
LncRNS, ko paredzēja četras iepriekš minētās programmatūras, tika klasificētas 4 kategorijās: lincRNS, anti-sense-LncRNS, intronic-LncRNA;sajūta-LncRNS.LncRNS klasifikācija tika parādīta zemāk esošajā histogrammā.
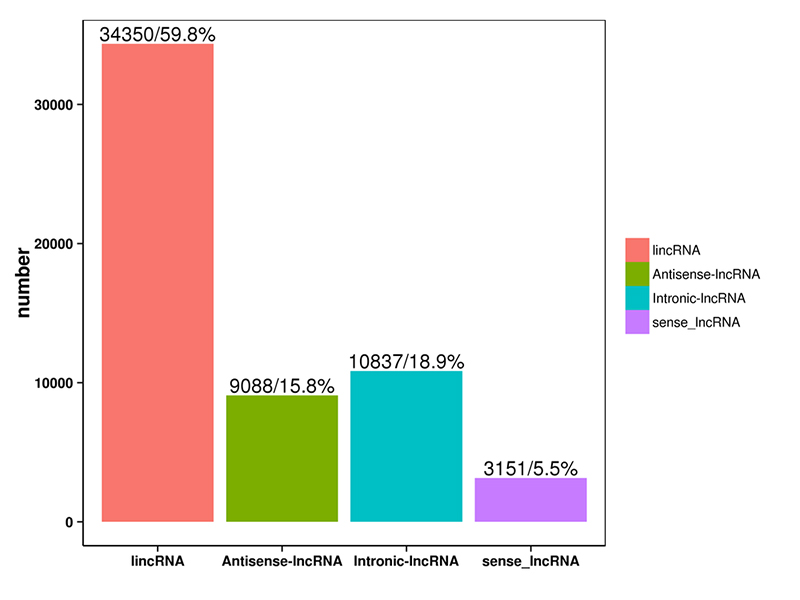
LncRNS klasifikācija
2. DE-lncRNS bagātināšanas analīzes cis-mērķētie gēni
ClusterProfiler tika izmantots GO bagātināšanas analīzē ar cis-mērķētu diferenciāli ekspresētas lncRNS (DE-lncRNS) gēniem bioloģisko procesu, molekulāro funkciju un šūnu komponentu ziņā.GO bagātināšanas analīze ir process, lai identificētu uz DEG vērstus ievērojami bagātinātus GO terminus, salīdzinot ar visu genomu.Bagātinātie termini tika parādīti histogrammā, burbuļu diagrammā utt., kā parādīts tālāk.
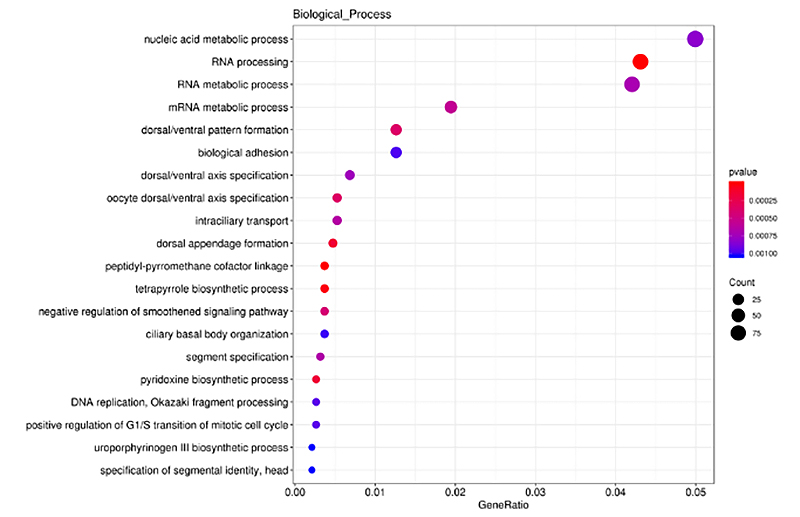 DE-lncRNS bagātināšanas analīzes cis-mērķēti gēni - burbuļu diagramma
DE-lncRNS bagātināšanas analīzes cis-mērķēti gēni - burbuļu diagramma
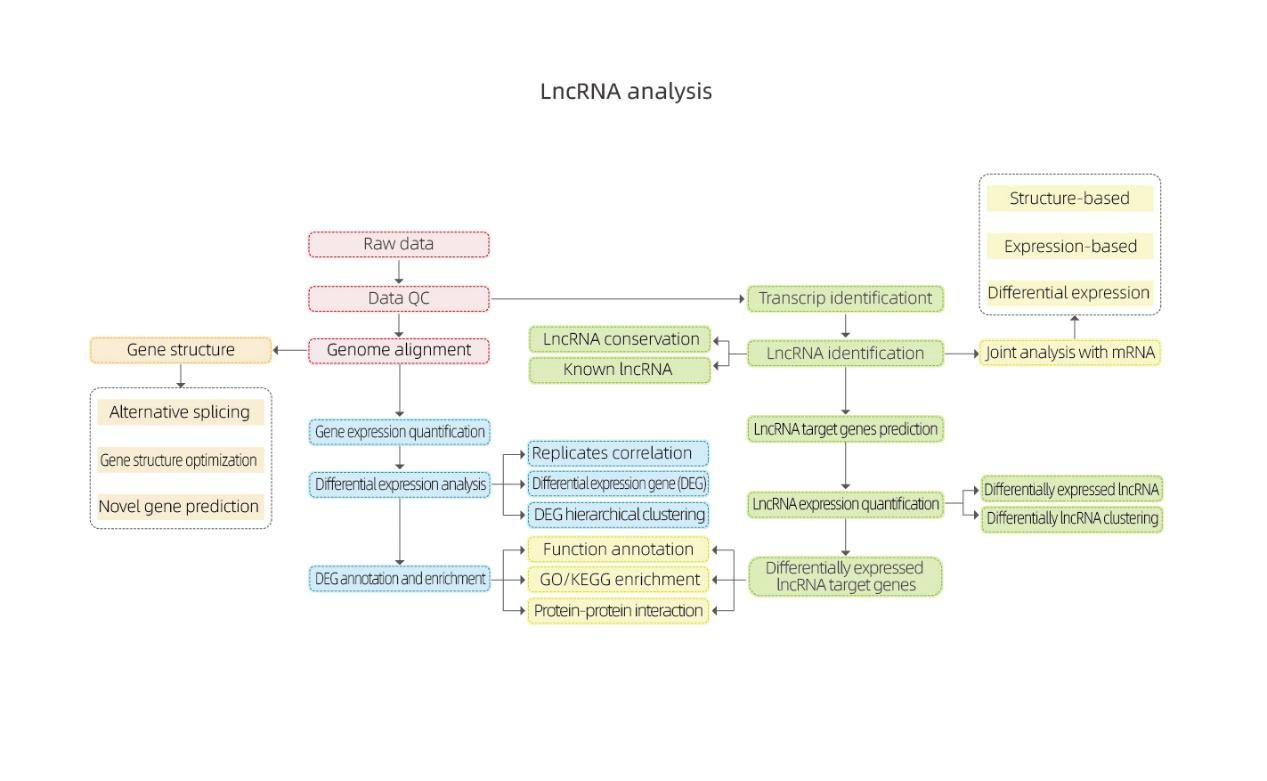
3. Salīdzinot mRNS un lncRNS garumu, eksonu skaitu, ORF un ekspresijas daudzumu, mēs varam saprast atšķirības to struktūrā, secībā un tā tālāk, kā arī pārbaudīt, vai mūsu prognozētā jaunā lncRNS atbilst vispārīgajām īpašībām.
BMK lieta
Deregulēts lncRNS ekspresijas profils peles plaušu adenokarcinomās ar KRAS-G12D mutāciju un P53 nokautu
Publicēts:Šūnu un molekulārās medicīnas žurnāls,2019. gads
Sekvences stratēģija
Illumina
Paraugu kolekcija
NONMMUT015812-knockdown KP (shRNA-2) šūnas un negatīvās kontroles (sh-Scr) šūnas tika iegūtas konkrētas vīrusu infekcijas 6. dienā.
Galvenie rezultāti
Šis pētījums pēta aberranti ekspresētās lncRNS peles plaušu adenokarcinomā ar P53 nokautu un KrasG12D mutāciju.
1,6424 lncRNS tika izteikti atšķirīgi (≥ 2 reizes lielākas izmaiņas, P < 0,05).
2. No visām 210 lncRNS (FC≥8) 11 lncRNS ekspresiju regulēja attiecīgi P53, 33 lncRNS ar KRAS un 13 lncRNS ar hipoksiju primārajās KP šūnās.
Lai analizētu tā šūnu funkciju, tika atklāts 3.NONMMUT015812, kas tika ievērojami paaugstināts peles plaušu adenokarcinomas gadījumā un negatīvi regulēts ar P53 atkārtotu ekspresiju.
4. NONMMUT015812 notriekšana ar shRNS samazināja KP šūnu proliferācijas un migrācijas spējas.NONMMUT015812 bija potenciāls onkogēns.
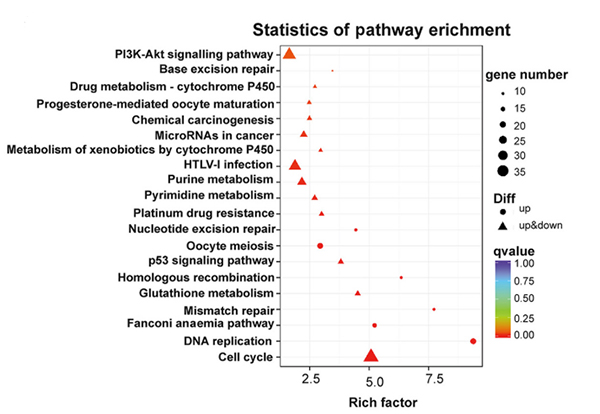 KEGG ceļa analīze diferencēti izteiktiem gēniem NONMMUT015812-knockdown KP šūnās | 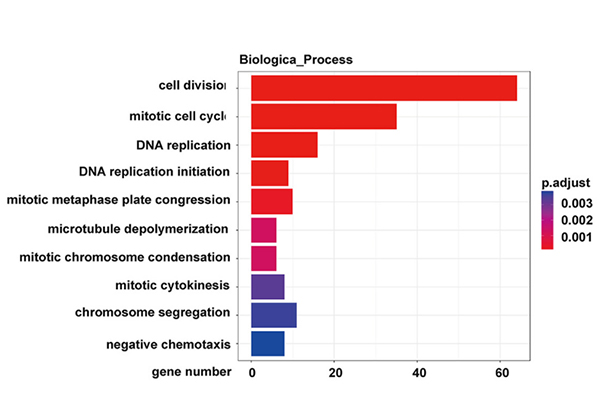 Gēnu ontoloģijas analīze diferencēti izteiktiem gēniem NONMMUT015812-knockdown KP šūnās |
Atsauce
Deregulēts lncRNS ekspresijas profils peles plaušu adenokarcinomās ar KRAS-G12D mutāciju un P53 nokautu [J].Žurnāls Cellular and Molecular Medicine, 2019, 23(10).DOI: 10.1111/jcmm.14584