Séquençage long non codant-Illumina
Avantages des services
● Avantages des services
● Spécifique aux cellules et aux tissus
● Une étape spécifique exprime et présente un changement d'expression dynamique
● Modèles précis d'expression temporelle et spatiale
● Analyse conjointe avec les données d'ARNm.
● Livraison de résultats basée sur BMKCloud : exploration de données personnalisée disponible sur la plateforme.
● Services après-vente valables 3 mois après la fin du projet
Exigences et livraison des échantillons
| Bibliothèque | Plate-forme | Données recommandées | CQ des données |
| épuisement de l'ARNr | Illumina PE150 | 10 Go | Q30≥85 % |
| Conc. (ng/μl) | Quantité (μg) | Pureté | Intégrité |
| ≥ 100 | ≥ 0,5 | DO260/280=1,7-2,5 DO260/230=0,5-2,5 Contamination limitée ou inexistante en protéines ou en ADN indiquée sur le gel. | Pour les plantes : RIN≥6,5 ; Pour les animaux : RIN≥7,0 ; 5,0≥28S/18S≥1,0 ; élévation de la ligne de base limitée ou inexistante |
Nucléotides :
Tissu : Poids (sec) : ≥1 g
*Pour les tissus inférieurs à 5 mg, nous recommandons d’envoyer un échantillon de tissu surgelé (dans l’azote liquide).
Suspension cellulaire : nombre de cellules = 3×107
*Nous recommandons d’expédier du lysat cellulaire congelé.Dans le cas où cette cellule compte moins de 5×105, une surgélation dans l'azote liquide est recommandée.
Échantillons de sang:
PA×gèneBloodRNATube ;
6 ml de LTRIzol et 2 ml de sang (TRIzol : sang = 3 : 1)
Livraison d’échantillon recommandée
Récipient : tube à centrifuger de 2 ml (le papier d'aluminium n'est pas recommandé)
Étiquetage des échantillons : Groupe + répétition, par exemple A1, A2, A3 ;B1, B2, B3... ...
Expédition:
1. Glace sèche : Les échantillons doivent être emballés dans des sacs et enterrés dans de la glace carbonique.
2.Tubes RNAstable : les échantillons d'ARN peuvent être séchés dans un tube de stabilisation d'ARN (par exemple RNAstable®) et expédiés à température ambiante.
Flux de travail des services

Conception d'expériences

Livraison d'échantillon

Extraction d'ARN

Construction d'une bibliothèque

Séquençage

L'analyse des données

Services après-vente
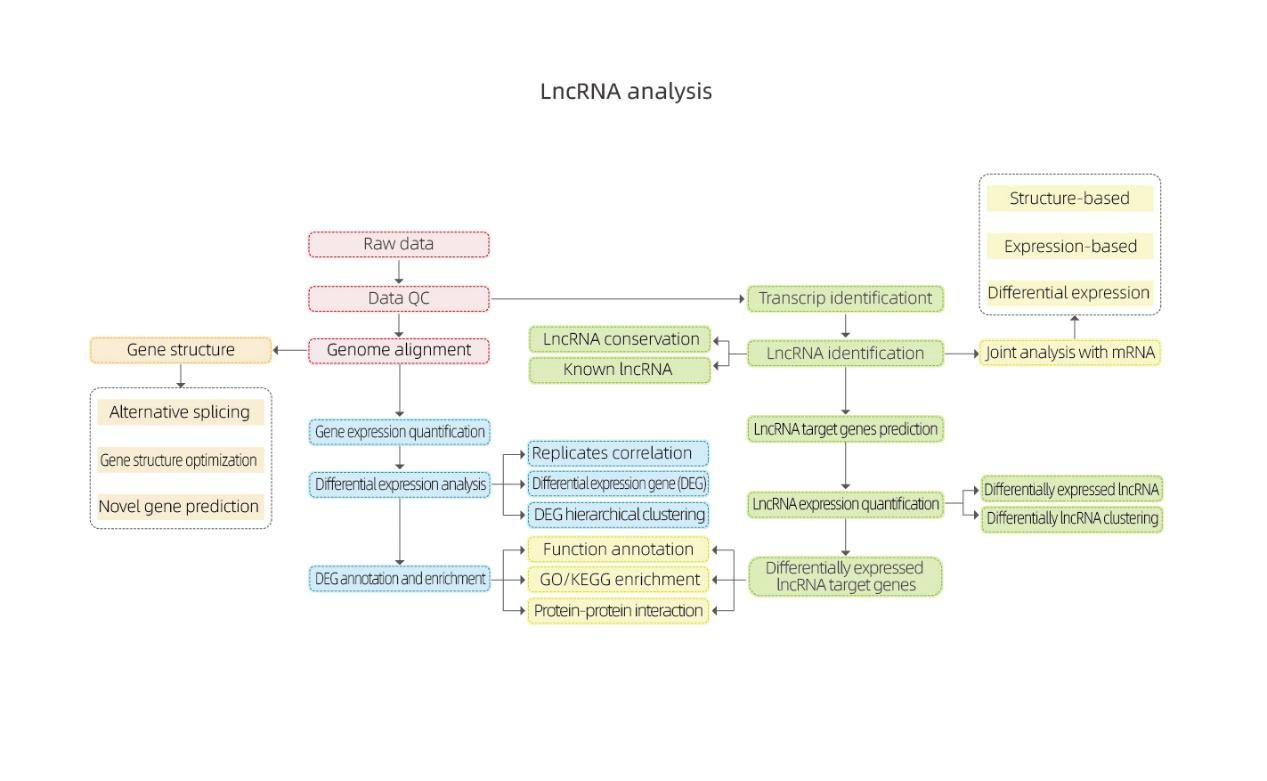
Bioinformatique
1.Classification LncARN
Les LncRNA prédits par les quatre logiciels ci-dessus ont été classés en 4 catégories : lincRNA, anti-sens-LncRNA, intronic-LncRNA ;sens-LncRNA.La classification des LncRNA a été présentée dans l'histogramme ci-dessous.
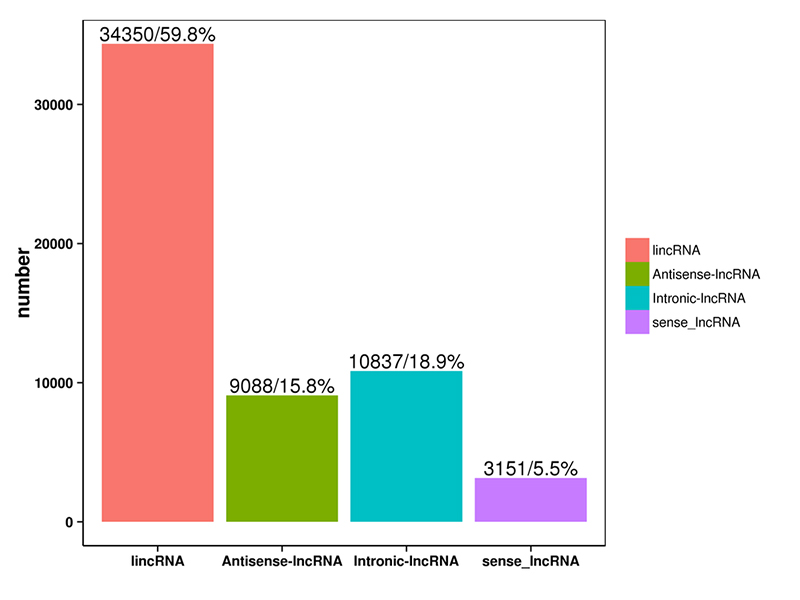
Classification des ARNlnc
2. Gènes ciblés Cis pour l’analyse d’enrichissement DE-lncRNA
ClusterProfiler a été utilisé dans l'analyse d'enrichissement GO sur des gènes cis-ciblés d'ARNnc exprimés différentiellement (DE-lncRNA), en termes de processus biologiques, de fonctions moléculaires et de composants cellulaires.L'analyse d'enrichissement GO est un processus permettant d'identifier les termes GO significativement enrichis dirigés par DEG par rapport au génome entier.Les termes enrichis ont été présentés sous forme d'histogramme, de graphique à bulles, etc., comme indiqué ci-dessous.
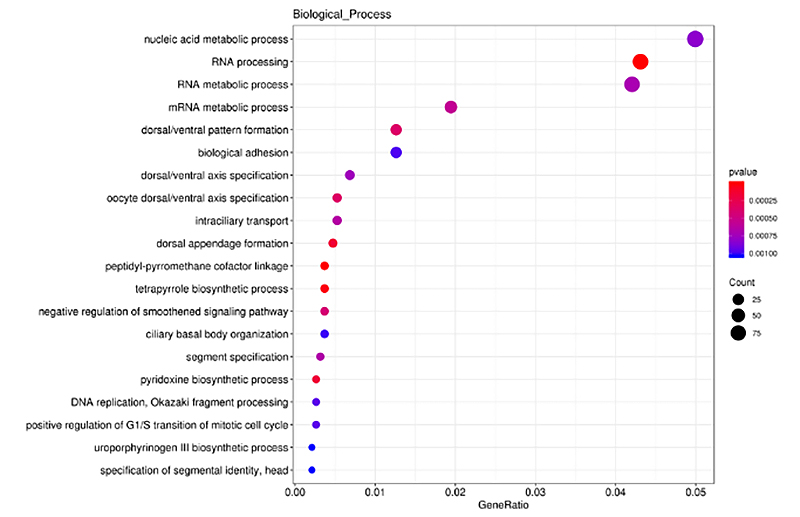 Gènes ciblés cis de l'analyse d'enrichissement DE-lncRNA - Graphique à bulles
Gènes ciblés cis de l'analyse d'enrichissement DE-lncRNA - Graphique à bulles
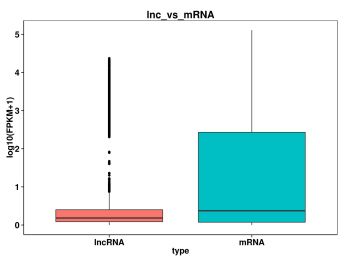
3. En comparant la longueur, le nombre d'exons, l'ORF et la quantité d'expression de l'ARNm et de l'ARNnc, nous pouvons comprendre les différences de structure, de séquence, etc. entre eux, et également vérifier si le nouvel ARNnc prédit par nous est conforme aux caractéristiques générales.
Affaire BMK
Profil d'expression dérégulé de lncRNA dans les adénocarcinomes pulmonaires de souris avec mutation KRAS‐G12D et knock-out de P53
Publié :Journal de médecine cellulaire et moléculaire,2019
Stratégie de séquençage
Illumine
Collecte d'échantillons
Les cellules NONMMUT015812-knockdown KP (shRNA-2) et les cellules de contrôle négatif (sh-Scr) ont été obtenues au jour 6 d'une infection virale spécifique.
Résultats clés
Cette étude examine les ARNnc exprimés de manière aberrante dans l'adénocarcinome du poumon de souris avec knock-out P53 et mutation KrasG12D.
1,6424 ARNnc ont été exprimés de manière différentielle (changement ≥ 2 fois, P < 0,05).
2. Parmi les 210 ARNnc (FC≥8), l'expression de 11 ARNnc était régulée par P53, 33 ARNnc par KRAS et 13 ARNnc par hypoxie dans les cellules KP primaires, respectivement.
3.NONMMUT015812, qui était remarquablement régulé positivement dans l'adénocarcinome du poumon de souris et régulé négativement par la réexpression de P53, a été détecté pour analyser sa fonction cellulaire.
4. L'inactivation de NONMMUT015812 par les shRNA a diminué les capacités de prolifération et de migration des cellules KP.NONMMUT015812 était un oncogène potentiel.
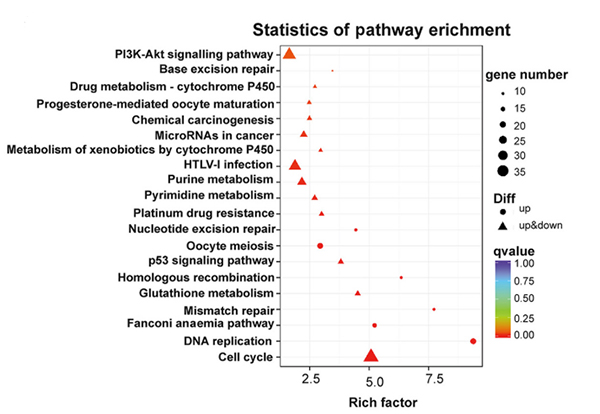 Analyse de la voie KEGG des gènes exprimés différentiellement dans les cellules KP NONMMUT015812-knockdown | 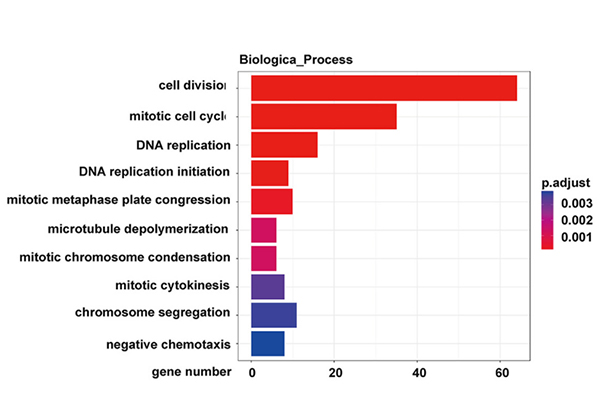 Analyse de l'ontologie des gènes des gènes exprimés différentiellement dans les cellules KP NONMMUT015812-knockdown |
Référence
Profil d'expression dérégulé de lncRNA dans les adénocarcinomes pulmonaires de souris avec mutation KRAS‐G12D et knock-out P53 [J].Journal de médecine cellulaire et moléculaire, 2019, 23(10).DOI:10.1111/jcmm.14584