Sequenziamento lungo non codificante-Illumina
Vantaggi del servizio
● Vantaggi del servizio
● Specifico per cellule e tessuti
● Lo stadio specifico esprime e presenta un cambiamento dinamico dell'espressione
● Modelli precisi di espressione temporale e spaziale
● Analisi congiunta con dati di mRNA.
● Consegna dei risultati basata su BMKCloud: data mining personalizzato disponibile sulla piattaforma.
● Servizi post-vendita validi per 3 mesi dal completamento del progetto
Requisiti e consegna del campione
| Biblioteca | piattaforma | Dati consigliati | Controllo qualità dei dati |
| Deplezione dell’rRNA | Illumina PE150 | 10 GB | Q30≥85% |
| Concentrazione (ng/μl) | Quantità (μg) | Purezza | Integrità |
| ≥ 100 | ≥ 0,5 | DE260/280=1,7-2,5 DE260/230=0,5-2,5 Contaminazione limitata o assente di proteine o DNA mostrata sul gel. | Per gli impianti: RIN≥6,5; Per gli animali: RIN≥7,0; 5,0≥28S/18S≥1,0; elevazione della linea di base limitata o assente |
Nucleotidi:
Tessuto: Peso (secco): ≥1 g
*Per tessuti di peso inferiore a 5 mg, si consiglia di inviare campioni di tessuto congelati istantaneamente (in azoto liquido).
Sospensione cellulare: conta cellulare = 3×107
*Si consiglia di spedire il lisato cellulare congelato.Nel caso in cui la cella conteggi inferiore a 5×105, si consiglia il congelamento rapido in azoto liquido.
Campioni di sangue:
PA×geneBloodRNATube;
6 ml di TRIzol e 2 ml di sangue (TRIzol:sangue=3:1)
Consegna del campione consigliata
Contenitore: provetta da centrifuga da 2 ml (la carta stagnola non è consigliata)
Etichettatura del campione: Gruppo+replica, ad esempio A1, A2, A3;B1, B2, B3... ...
Spedizione:
1. Ghiaccio secco: i campioni devono essere confezionati in sacchetti e sepolti nel ghiaccio secco.
2.Provette RNAstable: i campioni di RNA possono essere essiccati in provette di stabilizzazione dell'RNA (ad esempio RNAstable®) e spediti a temperatura ambiente.
Flusso di lavoro del servizio

Progettazione dell'esperimento

Consegna del campione

Estrazione dell'RNA

Costruzione della biblioteca

Sequenziamento

Analisi dei dati

Servizi post-vendita
Bioinformatica
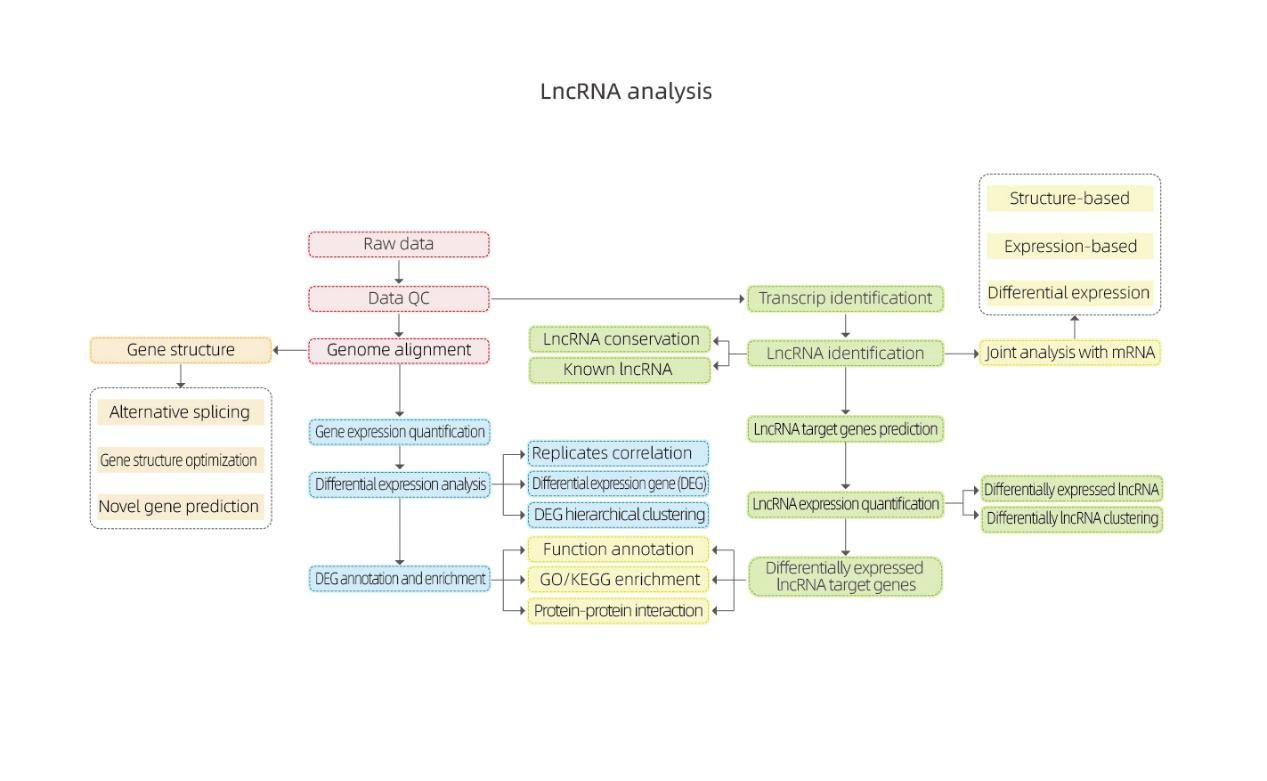
1.Classificazione dell'LncRNA
Gli LncRNA predetti dai quattro software di cui sopra sono stati classificati in 4 categorie: lincRNA, LncRNA anti-senso, LncRNA intronico;senso-LncRNA.La classificazione dell'LncRNA è stata mostrata nell'istogramma seguente.
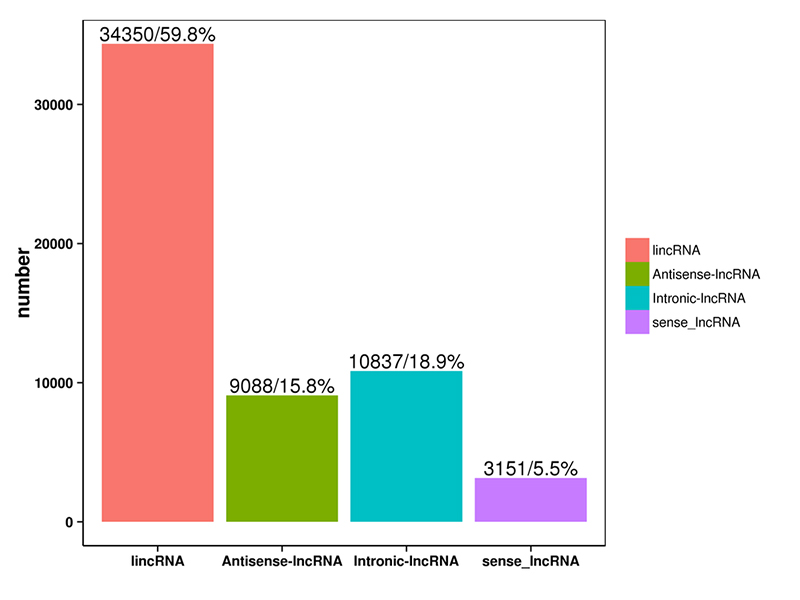
Classificazione dell'LncRNA
2. Geni mirati al cis dell'analisi di arricchimento di DE-lncRNA
ClusterProfiler è stato impiegato nell'analisi di arricchimento GO su geni bersaglio cis di lncRNA differenzialmente espressi (DE-lncRNA), in termini di processi biologici, funzioni molecolari e componenti cellulari.L'analisi dell'arricchimento GO è un processo per identificare termini GO significativamente arricchiti diretti da DEG rispetto all'intero genoma.I termini arricchiti sono stati presentati in un istogramma, un grafico a bolle, ecc. come mostrato di seguito.
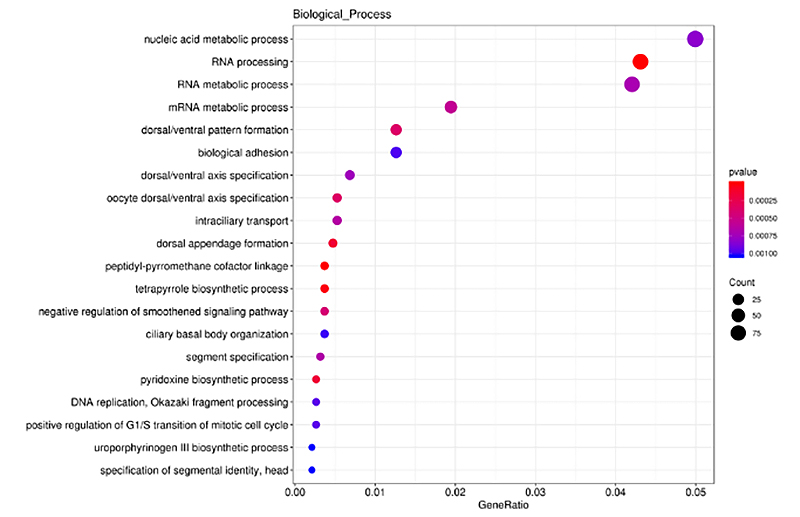 Geni mirati a Cis dell'analisi di arricchimento di DE-lncRNA - Grafico a bolle
Geni mirati a Cis dell'analisi di arricchimento di DE-lncRNA - Grafico a bolle
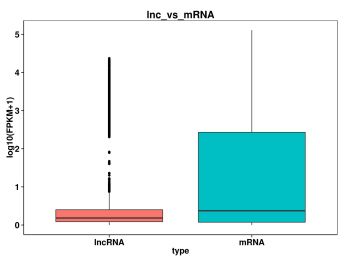
3. Confrontando la lunghezza, il numero dell'esone, l'ORF e la quantità di espressione di mRNA e lncRNA, possiamo comprendere le differenze nella struttura, nella sequenza e così via tra loro, e anche verificare se il nuovo lncRNA da noi previsto è conforme alle caratteristiche generali.
Caso BMK
Profilo di espressione deregolamentato dell'lncRNA negli adenocarcinomi polmonari di topo con mutazione KRAS-G12D e knockout P53
Pubblicato:Giornale di medicina cellulare e molecolare,2019
Strategia di sequenziamento
Illumina
Raccolta campioni
Le cellule KP NONMMUT015812-knockdown (shRNA-2) e le cellule di controllo negativo (sh-Scr) sono state ottenute il giorno 6 di una specifica infezione virale.
Risultati chiave
Questo studio indaga gli lncRNA espressi in modo anomalo nell'adenocarcinoma polmonare del topo con knockout P53 e la mutazione KrasG12D.
1,6424 lncRNA erano espressi in modo differenziale (cambiamento ≥ 2 volte, P <0,05).
2. Tra tutti i 210 lncRNA (FC≥8), l'espressione di 11 lncRNA era regolata da P53, 33 lncRNA da KRAS e 13 lncRNA dall'ipossia nelle cellule KP primarie, rispettivamente.
3.NONMMUT015812, che era notevolmente sovraregolato nell'adenocarcinoma polmonare del topo e regolato negativamente dalla riespressione di P53, è stato rilevato per analizzare la sua funzione cellulare.
4.L'abbattimento di NONMMUT015812 da parte degli shRNA ha ridotto le capacità di proliferazione e migrazione delle cellule KP.NONMMUT015812 era un potenziale oncogene.
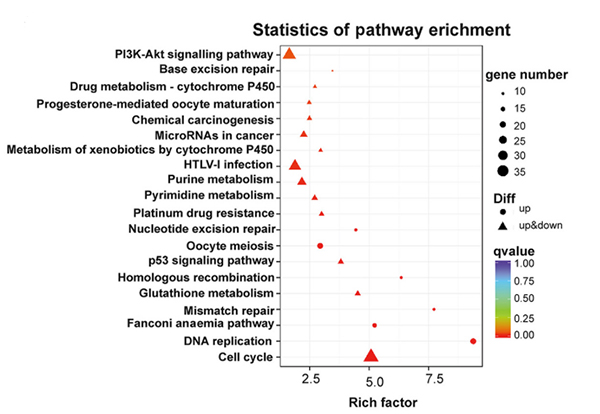 Analisi del percorso KEGG dei geni espressi in modo differenziale nelle cellule KP knockdown NONMMUT015812 | 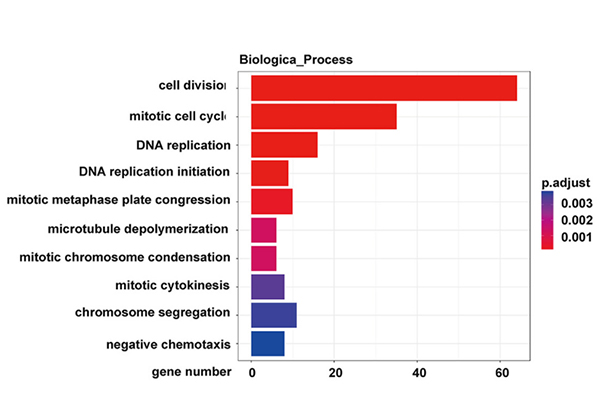 Analisi di ontologia genetica dei geni espressi in modo differenziale nelle cellule KP knockdown NONMMUT015812 |
Riferimento
Profilo di espressione deregolamentato dell'lncRNA negli adenocarcinomi polmonari di topo con mutazione KRAS-G12D e knockout P53 [J].Giornale di medicina cellulare e molecolare, 2019, 23(10).DOI: 10.1111/jcmm.14584