DNA/RNA 시퀀싱 – 나노포어 시퀀서
서비스 내용 특징
| 플랫폼 | 라이브러리 크기 | 이론적인 데이터 수율(세포당) | 단일 염기 정확도 | 응용 |
| 나노기공 | 8Kb, 10kb, 20kb, 울트라롱, cDNA-PCR | 70-90Gb/셀 | 85-92% | SV 호출, De novo, 전체 길이 시퀀싱, Iso-Seq, 유전자 주석, DNA 메틸화 검출 |
서비스 장점
● 다양한 종을 대상으로 한 수천 건의 비공개 프로젝트를 통해 PacBio 시퀀싱 플랫폼에서 5년 이상의 경험을 보유하고 있습니다.
● BMKGENE은 이중 플랫폼 RNA/DNA 인증을 받은 Oxford Nanopore의 공식 파트너입니다.
● 완전한 장비와 충분한 시퀀싱 처리량을 갖춘 시퀀서의 주류 모델이 있습니다.
● Nanopore 플랫폼을 기반으로 10개 이상의 동식물 Denovo 연구가 국제적으로 유명한 저널에 게재되었습니다.
샘플 요구 사항
| 샘플 유형 | 양 | 농도(Qubit ®) | 용량 | 청정 | 기타 |
| 게놈 DNA | 데이터 요구 사항에 따라 다름 | ≥20ng/μl | ≥15μl | OD260/280=1.7-2.2; OD260/230≥1.5; 260 nm에서 명확한 피크, 오염 없음 | 농도는 Qubit 및 Qubit/Nanopore ≤ 2로 측정해야 합니다. |
| 총 RNA | ≥1.2μg | ≥100μg/μl | ≥15μl | OD260/280=1.7-2.5; OD260/230=0.5-2.5;오염 없음 | RIN 값 ≥7.5 |
서비스 워크플로
샘플 준비

도서관 건립

시퀀싱

데이터 분석

프로젝트 납품
DNA 샘플의 데이터 품질 평가
표 1. 정리된 데이터에 대한 통계
| BM키드 | rawSeqNum | rawSumBase | cleanSeqNum | cleanSumBase | 클린N50렌 | 클린N90렌 | 깨끗한평균렌 | 클린맥스렌 | cleanMeanQual |
| DNA_BMK01 | 1,218,239 | 26.37 | 1,121,736 | 25.90 | 28,014 | 15,764 | 23,090 | 143,181 | 9 |
RNA 샘플의 데이터 품질 평가
표 1. 정리된 데이터에 대한 통계
| 파일 이름 | 클라이언트 ID | 읽은 횟수 | 기본 번호 | N50 | 평균 길이 | 최대 길이 | 평균Q점수 |
| RNA_BMK001 | C2 | 8,947,708 | 4,047,230,083 | 398 | 452 | 129,227 | Q12 |
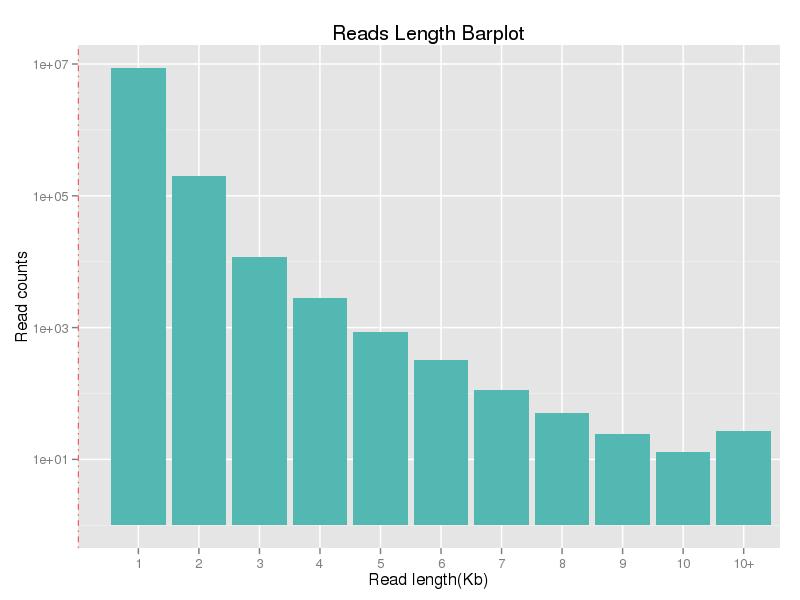
그림 1. 읽기 길이 분포
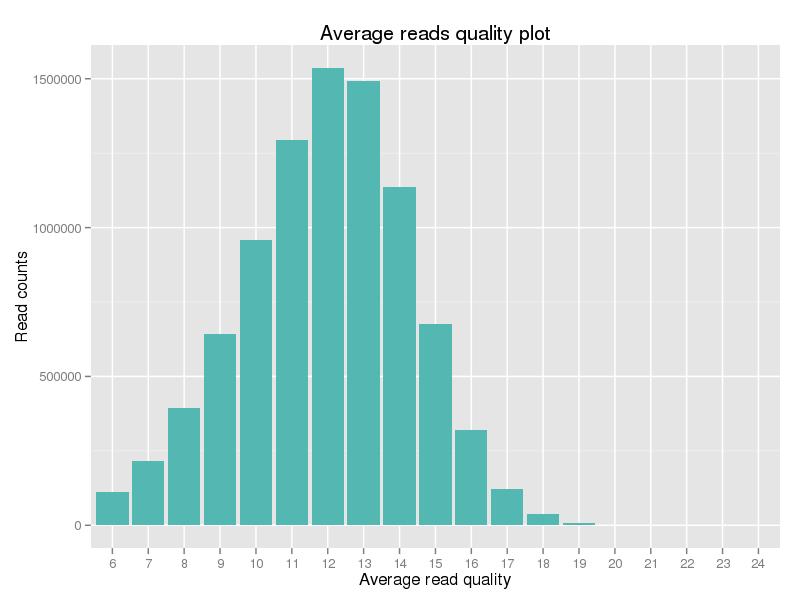
그림 2. 클린 데이터의 품질 점수 분포
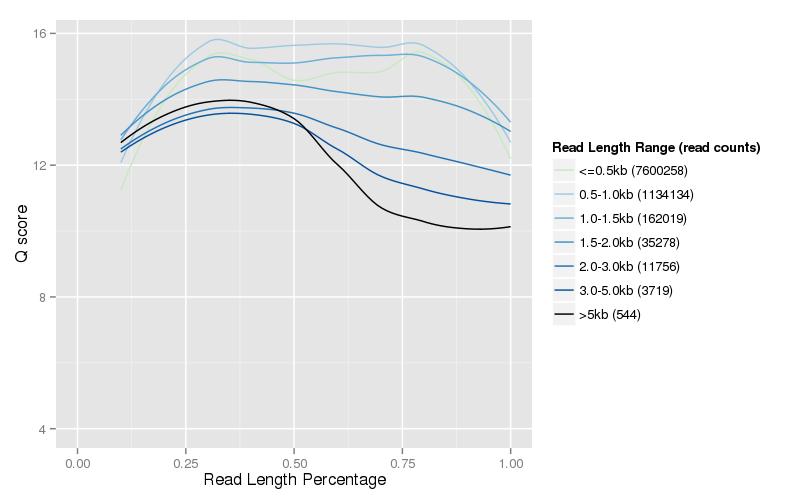
그림 3. 순수 데이터의 길이 및 품질 점수 분포